d4b8152d300848f4ebcdbf483e302573.ppt
- Количество слайдов: 20

Создание рекомбинантного штаммапродуцента новой MD-эндонуклеазы из энтеробактерий для использования в эпигенетике и онкодиагностике «Исследования и разработки по приоритетным направлениям развития научно-технологического комплекса России на 2014 – 2020 годы» Руководитель проекта: с. н. с. , к. с-х. н. Чернухин В. А.

Приоритетное направление: Науки о жизни. Критическая технология: Биокаталитические, биосинтетические и биосенсорные технологии. Плановое финансирование проекта: 8, 75 млн. руб. Бюджетные средства: 3, 5 млн. руб. , Внебюджетные средства: 5, 25 млн. руб, , в том числе: - в 2014 году в размере 1 250 000 (Один миллион двести пятьдесят тысяч) рублей, - в 2015 году в размере 4 050 000 (Четыре миллиона пятьдесят тысяч) Исполнитель: Общество с ограниченной ответственностью «Сиб. Энзайм»

Проект направлен на Расширение методологической базы для поиска и клонирования генов новых ферментов. Связанной с этим поиском расширением ферментной базы для эпигенетики, в частности, онкодиагностики.

Цели проекта 1. 2. 3. Поиск в коллекции природных штаммов энтеробактерий продуцента новой МD-эндонуклеазы, кодируемой геном, последовательность которого гомологична гену МDэндонуклеазы Mte. I. Создание методами биоинженерии рекомбинантного штамма-продуцента новой метилзависимой сайтспецифической ДНК-эндонуклеазы (МD-эндонуклеазы), востребованной для использования в эпигенетике и онкодиагностике. Исследование полученной генетической конструкции, технологических характеристик штамма-продуцента и специфичности продуцируемой рекомбинантной МDэндонуклеазыi

Конечные продукты Рекомбинантный штамм-продуцент новой метилзависимой сайт-специфической эндонуклеазы (MD-эндонуклеазы) Препарат фермента, выделенного из него. Новый фермент должен позволять детектировать эпигенетические изменения генома, проявляющиеся как определённый узор метилирования ДНК, что делает его важным инструментом в эпигенетике и онкодиагностике.
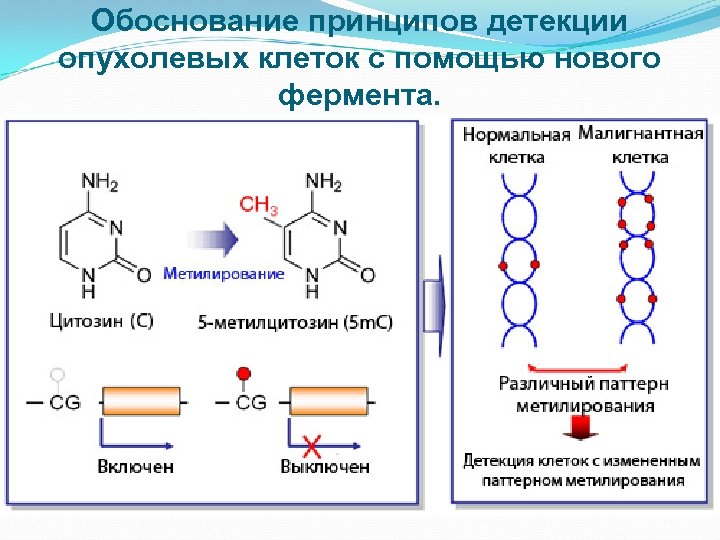
Обоснование принципов детекции опухолевых клеток с помощью нового фермента.

Предлагаемый принцип получения рекомбинантных штаммов-продуцентов новых MD-эндонуклеаз За основу поиска взята первичная структура белковой последовательности MDэндонуклеазы Mte. I (узнаёт метилированную последовательность 5’-GCGCNGCGC-3’). В базе данных ищутся гомологи в геномах энтеробактерий: Находятся консервативные последовательности Разрабатываются праймеры для ПЦР Проводится ПЦР-скрининг Амплифицированные фрагменты встраиваются в плазмиду p. UC 19.

___________ Почему энтеробактерии? В разных группах энтеробактерий есть высококонсервативные последовательности, гомологичные Mte. I? Mte. I – сайт-специфическая ДНК- эндонуклеаза, расщепляющая только С 5 метилированную ДНК и не расщепляющая метилированную.

Была собрана коллекция энтеробактерий – 97 штаммов из природных источников Высев на чашку со средой Эндо Поиск эрвиний в опухолях растений

Создан нетрудоёмкий метод быстрого минипрепаративного выделения геномной ДНК из энтеробактерий. Для выделения достаточно 1/10 -1/2 спичечной головки биомассы, которую можно взять с отдельного клона на чашке Петри. На выделение тратится менее 2 часов.

Проведение биоиформационных исследований и разработка праймеров для проведения ПЦР-скрининга Enterobact 1 (1) -------MSAREAYRQYREAVTACKDIFARGGNVTGDYGEHLVKQLYG Enterobact 2 (1) -------MSAREAYRQYREAVTACKGIFARGGNVTGDYGEHLVKQLYG Enterobact 3 (1) -------MSAREAYRQYREAVTACKGIFARGGNVTGDYGEHLVKQLYG Enterobact 4 (1) --------MHVKHIGSIEKRWLLAKAFFARGGNVTGDYGEHLVKQLYG Mte. I (1) MTEPSLPFDPTALTVRQLLAAHVAILDELTRRGLIRTRNSPLGDLAETLAVRAYG Enterobact 1 (42) GELLPNSHKSADVRLDDGTLLQVKTRVNKTQLG------GIRSWDFDYLIGIQLN Enterobact 2 (42) GELLPNSHKSADVRLGDGTLLQVKTRVNKTQLG------GIRSWDFDYLIGIQLN Enterobact 3 (42) GELLPNSHKSADVRLGDGTLLQVKTRVNKTQLG------GIRSWDFDYLIGIQLN Enterobact 4 (41) GELLPNSHKSADVRLSDGTLLQVKTRVNKTQLG------GIRSWDFDYLIGIQLN Mte. I (56) GTLAPNSEKSFDLTAADGRRIQVKARLVDPGDKRSQTFSAFRSFDFDAAVFVLFD Enterobact 1 (91) DDAEVMLAVRVPVDVCRQIAG-YASHDNKFVIHLNGVLLKTPGVENVTEEFQSV Enterobact 2 (91) DDAEVMLAVRVPVDVCRQIAG-YASHDNKFVIHLNGVLLKTPGVENVTEEFQSV Enterobact 3 (91) DDAEVMLAVRVPVDVCRQIAG-YASHDNKFVIHLNSVLLKTPGVENVTEEFQSV Enterobact 4 (90) EDAEVVMAVRVPVGICRQIAG-YASHDNKFVIHLNGVLLKTPGVENVTEEFRQCN Mte. I (111) TRSYDLLWARELTSDDVAVLGRRTEHVRATAITVRAVRAAGADVTEQLRRAYDQV Enterobact 1 (144) ---Enterobact 2 (144) ---Выравнивание аминокислотных последовательностей Enterobact 3 (144) ---Enterobact 4 (144) P--Mte. I (166) DEPR

Enterobact 1 (1) ATGAGTGCACGTGAAGCATATCGGCAGTATCGAGAAGCGGTGACTGCTTGCAAAG Enterobact 2 (1) ATGAGTGCACGTGAAGCATATCGGCAGTATCGAGAAGCGGTGACTGCTTGCAAGG Enterobact 3 (1) ATGAGTGCACGTGAAGCATATCGGCAGTATCGAGAAGCGGTGACTGCTTGCAAGG Enterobact 4 (1) ----GTGCACGTGAAGCATATCGGCAGTATCGAGAAGCGGTGGCTGCTTGCAAAG Consensus (1) ATGAGTGCACGTGAAGCATATCGGCAGTATCGAGAAGCGGTGACTGCTTGCAAGG Enterobact 1 (56) ACATTTTT-GCCCGAGGTGGTAATGTCACTGGTGATTACGGTGAACATCTCGTAA Enterobact 2 (56) GCATTTTT-GCCCGAGGTGGTAATGTCACTGGTGATTATGGTGAACATCTCGTAA Enterobact 3 (56) GCATTTTT-GCCCGAGGTGGTAATGTCACTGGTGATTATGGTGAACATCTCGTAA Enterobact 4 (52) GCATTTTTTGCCCGAGGTGGTAATGTCACTGGTGATTATGGTGAACATCTCGTAA Consensus (56) GCATTTTT GCCCGAGGTGGTAATGTCACTGGTGATTATGGTGAACATCTCGTAA Enterobact 1 (110) AGCAACTTTATGGTGGTGAATTATTGCCAAACTCCCATAAAAGCGCCGATGTCAG Enterobact 2 (110) AGCAACTTTATGGCGGTGAATTATTGCCAAACTCCCATAAAAGCGCCGATGTAAG Enterobact 3 (110) AGCAACTTTATGGCGGTGAATTATTGCCAAACTCCCATAAAAGCGCCGATGTAAG Enterobact 4 (107) AGCAACTTTATGGGGGTGAATTATTGCCAAACTCCCATAAAAGCGCCGATGTAAG Consensus (111) AGCAACTTTATGGCGGTGAATTATTGCCAAACTCCCATAAAAGCGCCGATGTAAG Enterobact 1 (165) ATTAGACGATGGCACGCTGTTGCAGGTCAAAACCAGAGTCAATAAAACCCAGTTA Enterobact 2 (165) ATTAGGCGATGGCACGCTATTGCAGGTCAAAACCAGAGTCAATAAAACCCAGTTA Enterobact 3 (165) ATTAGGCGATGGCACGCTATTGCAGGTCAAAACCAGAGTCAATAAAACCCAGTTG Enterobact 4 (162) ATTAAGCGATGGGACGCTGTTGCAGGTCAAAACCAGAGTCAATAAAACCCAGTTA Consensus (166) ATTAGGCGATGGCACGCTGTTGCAGGTCAAAACCAGAGTCAATAAAACCCAGTTA Enterobact 1 (220) GGCGGAATTCGCTCCTGGGATTTCGATTACCTGATCGGTATTCAGCTTAATGACG Enterobact 2 (220) GGCGGAATTCGCTCCTGGGATTTCGATTACCTGATCGGTATTCAGCTTAATGACG Enterobact 3 (220) GGCGGAATTCGCTCCTGGGATTTCGATTACCTGATCGGTATTCAGCTTAATGACG Enterobact 4 (217) GGCGGAATTCGCTCCTGGGATTTCGATTACCTGATCGGCATTCAGCTTAATGAAG Consensus (221) GGCGGAATTCGCTCCTGGGATTTCGATTACCTGATCGGTATTCAGCTTAATGACG Enterobact 1 (275) ATGCCGAAGTCATGTTGGCAGTTCGTGTCCCTGTAGATGTTTGTCGCCAAATTGC Enterobact 2 (275) ATGCCGAAGTCATGTTGGCAGTTCGTGTCCCTGTAGATGTTTGTCGCCAAATTGC Enterobact 3 (275) ATGCCGAAGTCATGTTGGCAGTTCGTGTCCCTGTAGATGTTTGTCGCCAAATTGC Enterobact 4 (272) ATGCCGAAGTAGTGATGGCAGTTCGTGTCCCTGTGGGTATTTGTCGCCAAATTGC Consensus (276) ATGCCGAAGTCATGTTGGCAGTTCGTGTCCCTGTAGATGTTTGTCGCCAAATTGC Enterobact 1 (330) CGGATATGCCATGATAACAAATTTGTGATCCATCTTAATGGCGTGCTTCTT Enterobact 2 (330) CGGATATGCCATGATAACAAATTTGTGATCCATCTTAATGGCGTGCTTCTT Enterobact 3 (330) CGGATATGCCATGATAACAAATTTGTGATCCATCTTAATAGCGTGCTTCTT Enterobact 4 (327) CGGATATGCCACGATAACAAATTTGTGATTCATCTCAATGGCGTGCTTCTT Consensus (331) CGGATATGCCATGATAACAAATTTGTGATCCATCTTAATGGCGTGCTTCTT Enterobact 1 (385) AAAACGCCTGGCGTAGAAAACGTCACTGAAGAGTTTCAGTGTAATCCCTAA Enterobact 2 (385) AAAACGCCTGGCGTAGAAAACGTCACCGAAGAGTTTCAGTGTAA------Enterobact 3 (385) AAAACGCCTGGCGTAGAAAACGTCACTGAAGAGTTTCAGTGTAA------Enterobact 4 (382) AAAACGCCTGGCGTAGAAAACGTCACTGAAGAGTTTC-GTCAATGTAATCCTTAA Consensus (386) AAAACGCCTGGCGTAGAAAACGTCACTGAAGAGTTTCAGTGTAATCC TAA Выравнивание высококонсервативных нуклеотидных последовательностей последовательнсотей Высококонсервативные гомологи обнаружены в родах Escherichia, Klebsiella, Cronobacter , Erwinia.

По итогам описанных биоинформационных исследований был проведён дизайн трёх праймеров (один прямой и два обратных): Entero direct Entero reverse 1 3' Entero reverse 2 5' - ATGAGTGCACGTGAAGCATATC-3' 5'-TTAGGGATTACACTGAAACTCTTC 5’- TTACACTGAAACTCTTC -3’.

ПЦР-скрининг Фрагмент № 17 был встроен в полилинкер p. UC 19 по сайту Sma. I Полученная плазмида получила временное обозначение p. Esp 17

Тестирование сайт-специфической MDнуклеазной активности в клоне № 17 М- маркёр 1 kb; 1 – 3 мкл лизата; 2 – 1 мкл лизата; 3 – 1/3 мкл лизата.
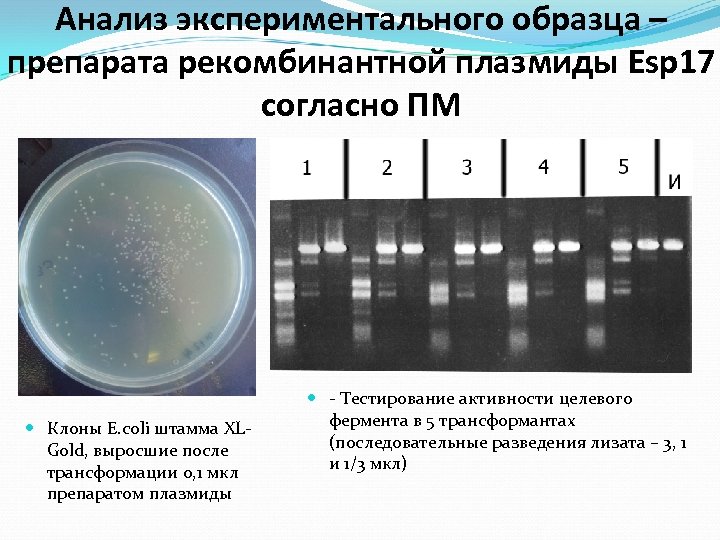
Анализ экспериментального образца – препарата рекомбинантной плазмиды Esp 17 согласно ПМ Клоны E. coli штамма XLGold, выросшие после трансформации 0, 1 мкл препаратом плазмиды - Тестирование активности целевого фермента в 5 трансформантах (последовательные разведения лизата – 3, 1 и 1/3 мкл)

Анализ экспериментального образца – биомассы штамма-продуцента согласно ПМ 1 -6 – последовательные 2 кратные разведения лизата в реакционной смести, содержащей p. Hsp. AI 10/(Dri. I+M. Fsp 4 H) в SEбуфере «W» ; 7 – исходная ДНКp. Hsp. AI 10/(Dri. I+M. Fsp 4 H); 8 – ДНК фага λ; 9 – ДНК фага λ в SE-буфере «Y» , обработанная 1 мкл лизата.

Анализ экспериментального образца – препарата MD-эндонуклеазы согласно ПМ 1 -10 – последовательные разведения препарата Esp 17 в 2 раза в SE-буфере «W» c ДНК p. Hsp. AI 10/(Dri. I+M. Fsp 4 H), начиная от аликовоты 1 мкл на 20 мкл реакционной смеси; 11 ДНК p. Hsp. AI 10/(Dri. I+M. Fsp 4 H); 12 – ДНК фага λ; 13 - ДНК фага λ, обработанная 1 мкл Esp 17; М – маркёр 1 kb.
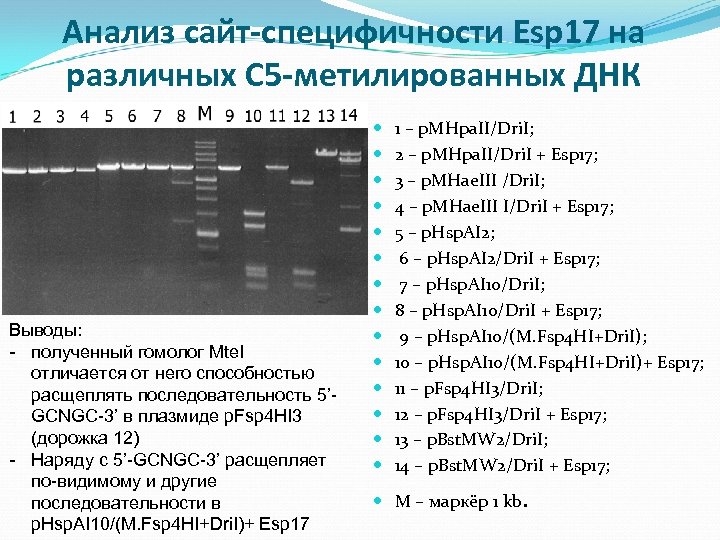
Анализ сайт-специфичности Esp 17 на различных С 5 -метилированных ДНК Выводы: - полученный гомолог Mte. I отличается от него способностью расщеплять последовательность 5’GCNGC-3’ в плазмиде p. Fsp 4 HI 3 (дорожка 12) - Наряду с 5’-GCNGC-3’ расщепляет по-видимому и другие последовательности в p. Hsp. AI 10/(M. Fsp 4 HI+Dri. I)+ Esp 17 1 – p. MHpa. II/Dri. I; 2 – p. MHpa. II/Dri. I + Esp 17; 3 – p. MHae. III /Dri. I; 4 – p. MHae. III I/Dri. I + Esp 17; 5 – p. Hsp. AI 2; 6 – p. Hsp. AI 2/Dri. I + Esp 17; 7 – p. Hsp. AI 10/Dri. I; 8 – p. Hsp. AI 10/Dri. I + Esp 17; 9 – p. Hsp. AI 10/(M. Fsp 4 HI+Dri. I); 10 – p. Hsp. AI 10/(M. Fsp 4 HI+Dri. I)+ Esp 17; 11 – p. Fsp 4 HI 3/Dri. I; 12 – p. Fsp 4 HI 3/Dri. I + Esp 17; 13 – p. Bst. MW 2/Dri. I; 14 – p. Bst. MW 2/Dri. I + Esp 17; M – маркёр 1 kb.

Предварительные выводы: Новая рекомбинантная эндонуклеаза Esp 17 отличается от его гомолога Mte. I, узнающего 8 -нуклеотидную последовательность 5’-GCGCNGCGC-3’ и узнаёт и расщепляет С 5 -метилированную последовательность 5’GCNGC-3’ и отличается от его гомолога Mte. I. Требуются дальнейшие экспериментальные исследования по уточнению сайт-специфичности данного фермента. Активность фермента в рекомбинантном штамме достаточна для его промышленного производства. Полученные новые данные о структуре MDэндонуклеазы могут быть использованы для усовершенствования методов поиска и клонирвоания новых ферментов.
d4b8152d300848f4ebcdbf483e302573.ppt