BI_Lection_2017_2.ppt
- Количество слайдов: 36
 Секвенирование нового поколения (NGS) Васильев Геннадий Владимирович Институт цитологии и генетики СО РАН
Секвенирование нового поколения (NGS) Васильев Геннадий Владимирович Институт цитологии и генетики СО РАН
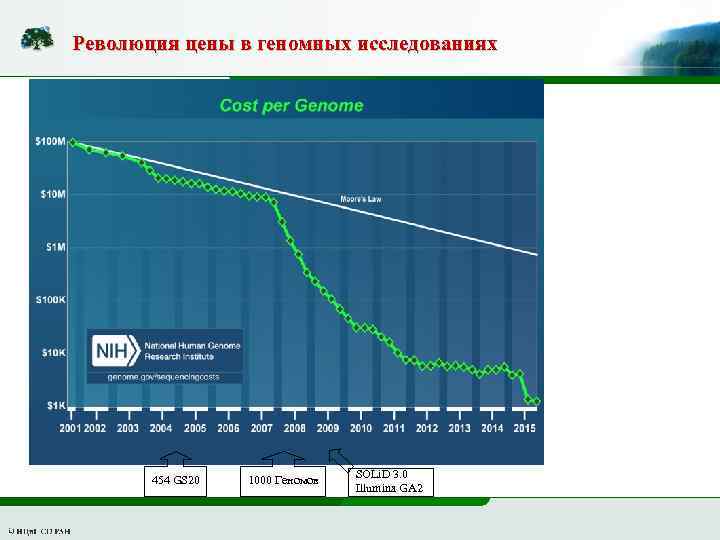 Революция цены в геномных исследованиях 454 GS 20 1000 Геномов SOLi. D 3. 0 Illumina GA 2
Революция цены в геномных исследованиях 454 GS 20 1000 Геномов SOLi. D 3. 0 Illumina GA 2
 Второе поколение секвенаторов – NGS – создатели геномики Roche FLX Titanium SOLi. D 5500 Illumina Hi. Seq Ion Proton
Второе поколение секвенаторов – NGS – создатели геномики Roche FLX Titanium SOLi. D 5500 Illumina Hi. Seq Ion Proton
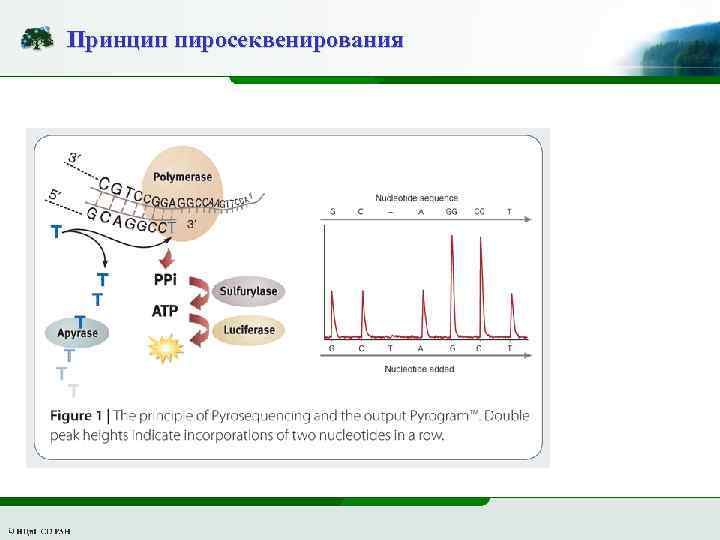 Принцип пиросеквенирования
Принцип пиросеквенирования
 Пиросеквенирование: приготовление библиотек
Пиросеквенирование: приготовление библиотек
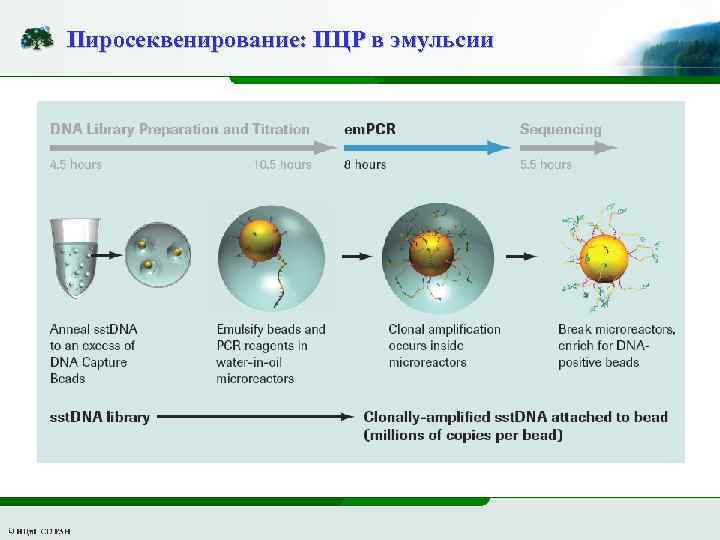 Пиросеквенирование: ПЦР в эмульсии
Пиросеквенирование: ПЦР в эмульсии
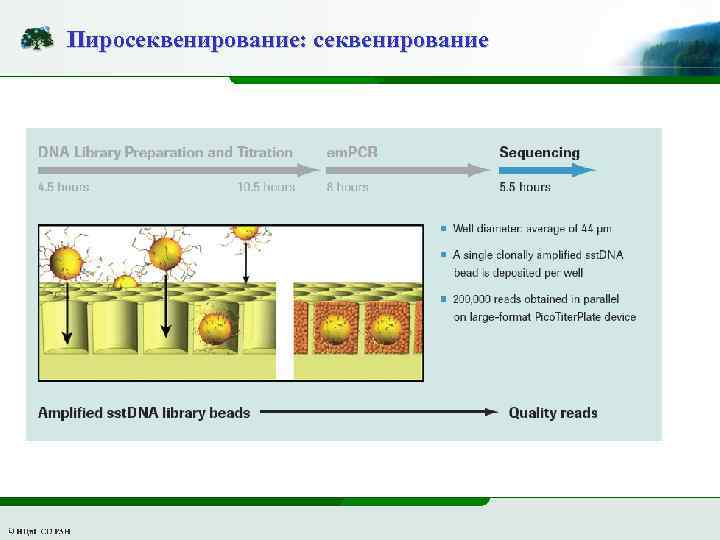 Пиросеквенирование: секвенирование
Пиросеквенирование: секвенирование
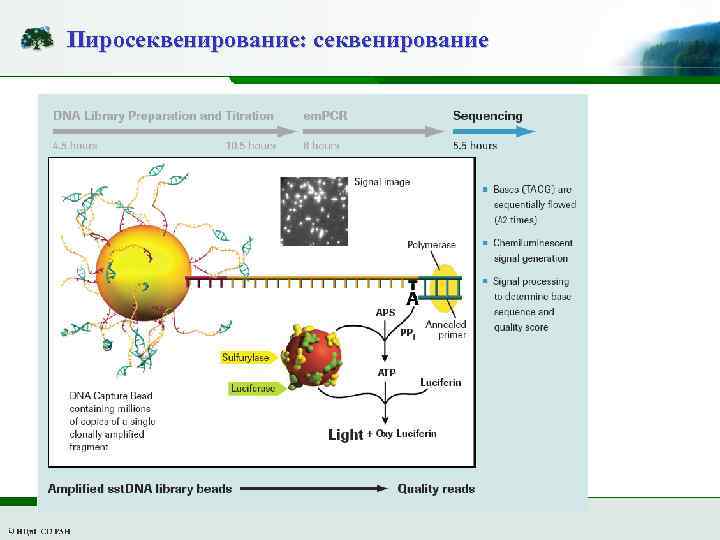 Пиросеквенирование: секвенирование
Пиросеквенирование: секвенирование
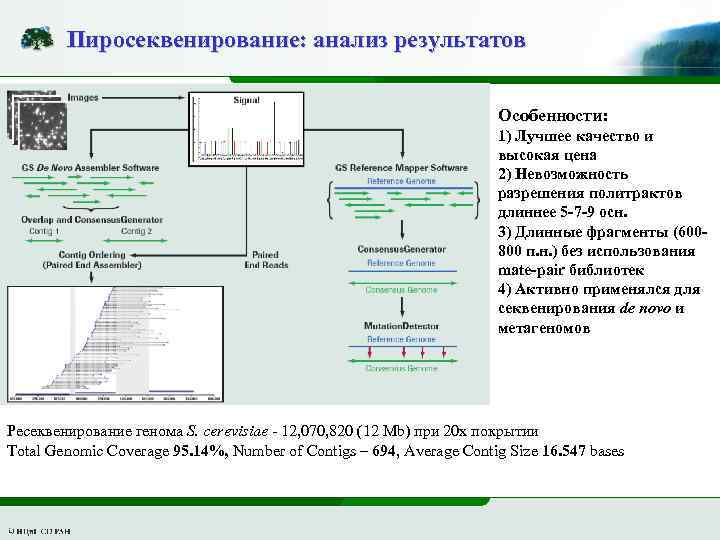 Пиросеквенирование: анализ результатов Особенности: 1) Лучшее качество и высокая цена 2) Невозможность разрешения политрактов длиннее 5 -7 -9 осн. 3) Длинные фрагменты (600800 п. н. ) без использования mate-pair библиотек 4) Активно применялся для секвенирования de novo и метагеномов Ресеквенирование генома S. cerevisiae - 12, 070, 820 (12 Mb) при 20 х покрытии Total Genomic Coverage 95. 14%, Number of Contigs – 694, Average Contig Size 16. 547 bases
Пиросеквенирование: анализ результатов Особенности: 1) Лучшее качество и высокая цена 2) Невозможность разрешения политрактов длиннее 5 -7 -9 осн. 3) Длинные фрагменты (600800 п. н. ) без использования mate-pair библиотек 4) Активно применялся для секвенирования de novo и метагеномов Ресеквенирование генома S. cerevisiae - 12, 070, 820 (12 Mb) при 20 х покрытии Total Genomic Coverage 95. 14%, Number of Contigs – 694, Average Contig Size 16. 547 bases
 SOLi. D 4 SOLi. D 5500 Особенности: 1) Самые короткие чтения 50 или 75 п. н. , используется при ресеквенировании и анализе транскриптомов 2) Есть чтение mate-pair библиотек 3) Достаточно высокая точность при использовании специализированного ПО
SOLi. D 4 SOLi. D 5500 Особенности: 1) Самые короткие чтения 50 или 75 п. н. , используется при ресеквенировании и анализе транскриптомов 2) Есть чтение mate-pair библиотек 3) Достаточно высокая точность при использовании специализированного ПО
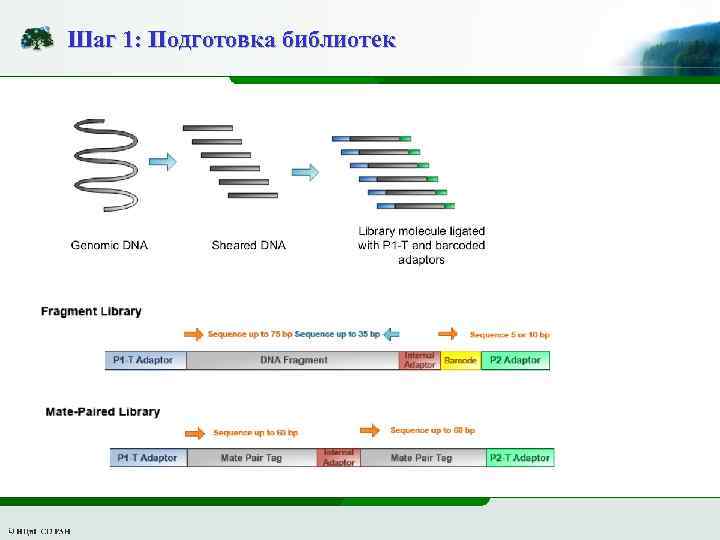 Шаг 1: Подготовка библиотек
Шаг 1: Подготовка библиотек
 SOLi. D: результат ПЦР в эмульсии 1. 6 x 109 150 – 300 x 109
SOLi. D: результат ПЦР в эмульсии 1. 6 x 109 150 – 300 x 109
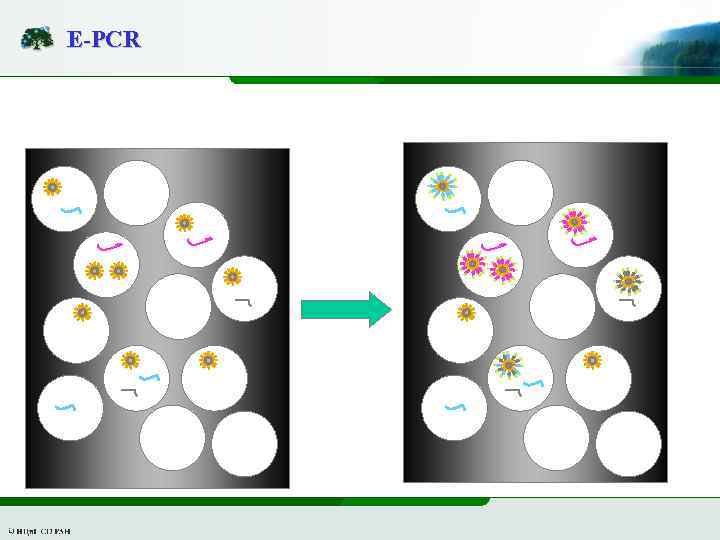 E-PCR
E-PCR
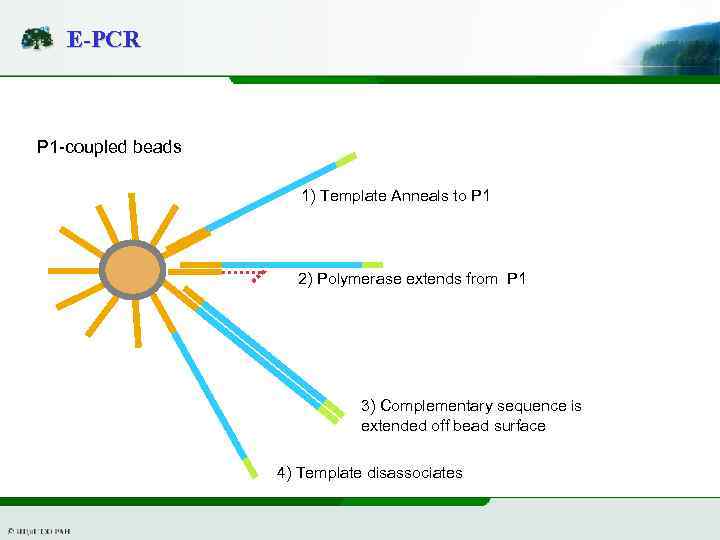 E-PCR P 1 -coupled beads 1) Template Anneals to P 1 2) Polymerase extends from P 1 3) Complementary sequence is extended off bead surface 4) Template disassociates
E-PCR P 1 -coupled beads 1) Template Anneals to P 1 2) Polymerase extends from P 1 3) Complementary sequence is extended off bead surface 4) Template disassociates
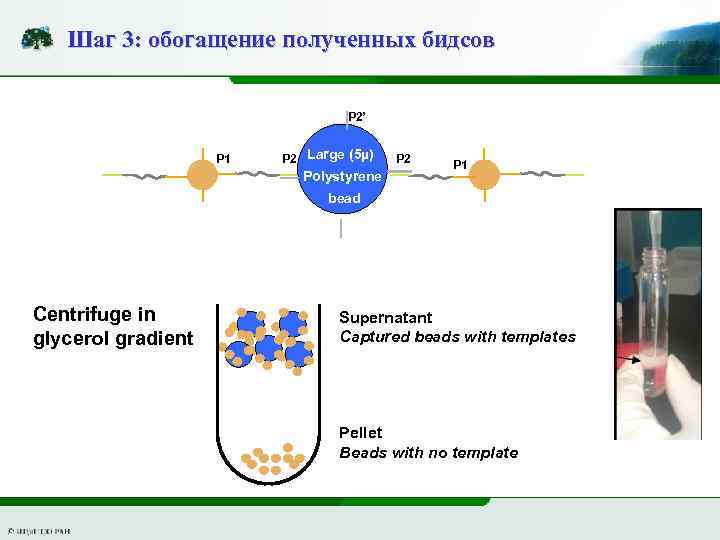 Шаг 3: обогащение полученных бидсов P 2’ P 1 P 2 Large (5µ) Polystyrene P 2 P 1 bead Centrifuge in glycerol gradient Supernatant Captured beads with templates Pellet Beads with no template
Шаг 3: обогащение полученных бидсов P 2’ P 1 P 2 Large (5µ) Polystyrene P 2 P 1 bead Centrifuge in glycerol gradient Supernatant Captured beads with templates Pellet Beads with no template
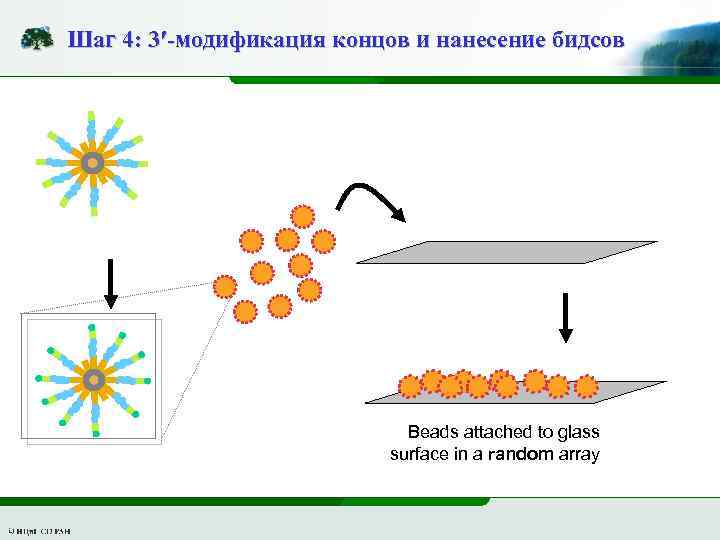 Шаг 4: 3′-модификация концов и нанесение бидсов Beads attached to glass surface in a random array
Шаг 4: 3′-модификация концов и нанесение бидсов Beads attached to glass surface in a random array
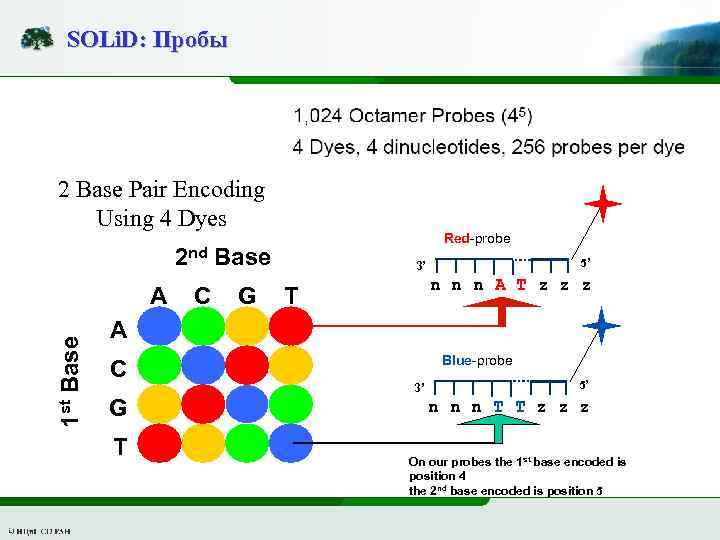 SOLi. D: Пробы 2 Base Pair Encoding Using 4 Dyes Red-probe 2 nd Base 1 st Base A C G 5’ 3’ n n n A T z z z T A C G T Blue-probe 3’ 5’ n n n T T z z z On our probes the 1 st base encoded is position 4 the 2 nd base encoded is position 5
SOLi. D: Пробы 2 Base Pair Encoding Using 4 Dyes Red-probe 2 nd Base 1 st Base A C G 5’ 3’ n n n A T z z z T A C G T Blue-probe 3’ 5’ n n n T T z z z On our probes the 1 st base encoded is position 4 the 2 nd base encoded is position 5
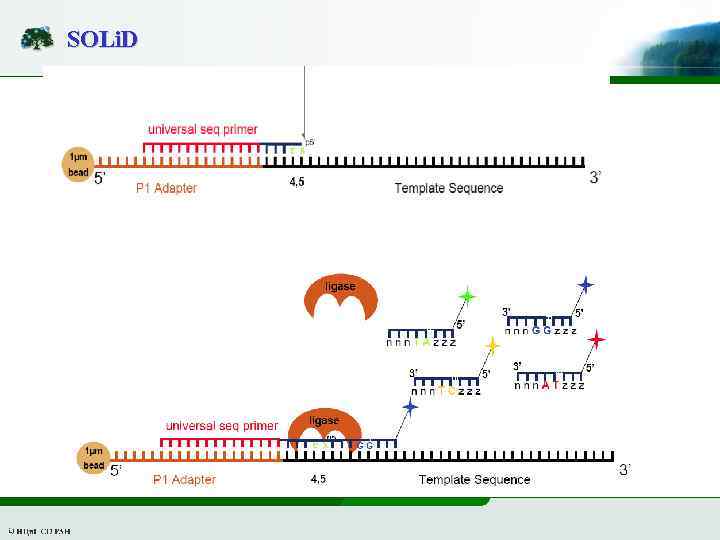 SOLi. D
SOLi. D
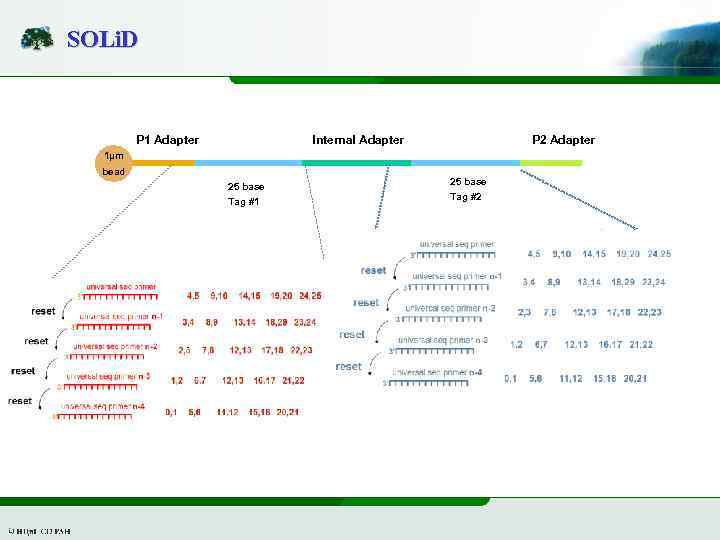 SOLi. D Internal Adapter P 1 Adapter P 2 Adapter 1µm bead 25 base Tag #1 25 base Tag #2
SOLi. D Internal Adapter P 1 Adapter P 2 Adapter 1µm bead 25 base Tag #1 25 base Tag #2
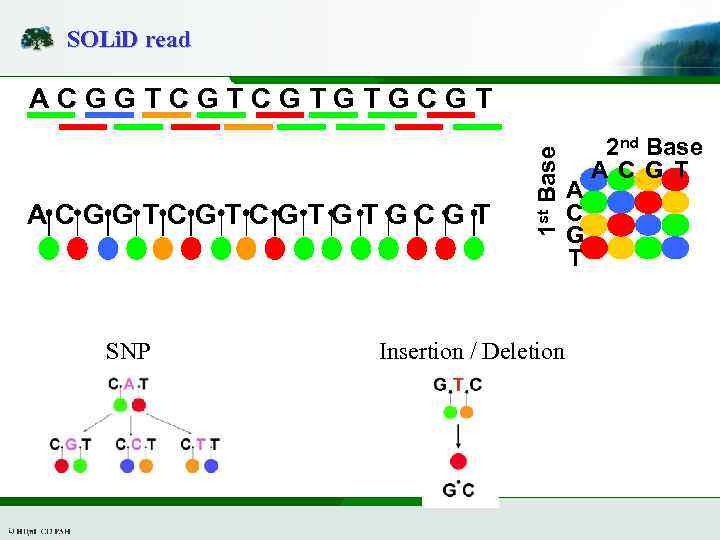 SOLi. D read ACGGTCGTCGTGTGCGT SNP 1 st Base ACGGTCGTCGTGTGCGT Insertion / Deletion A C G T 2 nd Base A C G T
SOLi. D read ACGGTCGTCGTGTGCGT SNP 1 st Base ACGGTCGTCGTGTGCGT Insertion / Deletion A C G T 2 nd Base A C G T
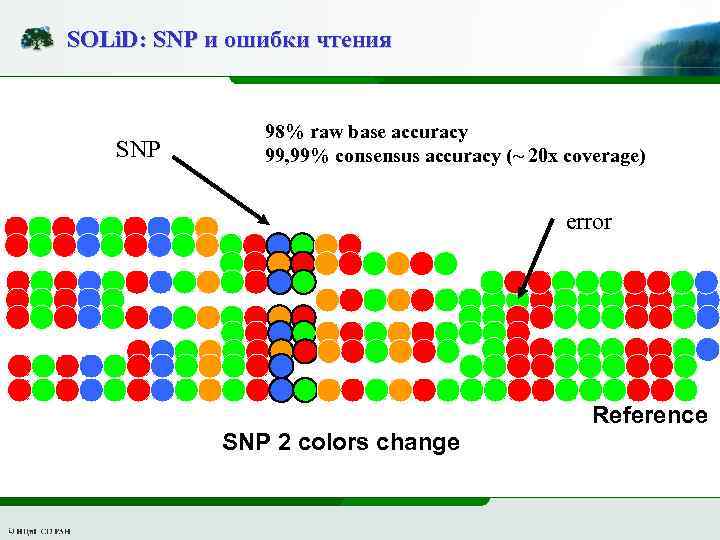 SOLi. D: SNP и ошибки чтения SNP 98% raw base accuracy 99, 99% consensus accuracy (~ 20 x coverage) error Reference SNP 2 colors change
SOLi. D: SNP и ошибки чтения SNP 98% raw base accuracy 99, 99% consensus accuracy (~ 20 x coverage) error Reference SNP 2 colors change
 Технология фирмы Illumina – Hi. Seq, My. Seq, Next. Seq, Nova. Seq Особенности: 1) Чтения 50 -300 п. н. прямые либо парные 2) Есть чтение mate-pair библиотек 3) Доминирующая на рынке (80 -90%), применяется везде.
Технология фирмы Illumina – Hi. Seq, My. Seq, Next. Seq, Nova. Seq Особенности: 1) Чтения 50 -300 п. н. прямые либо парные 2) Есть чтение mate-pair библиотек 3) Доминирующая на рынке (80 -90%), применяется везде.
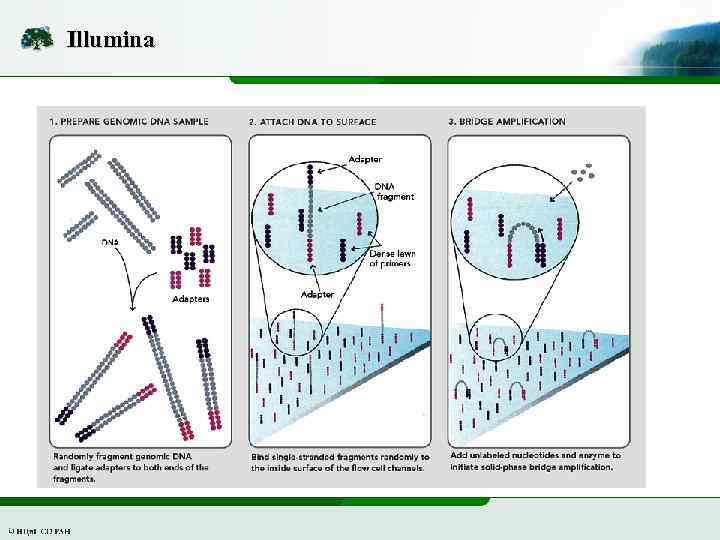 Illumina
Illumina
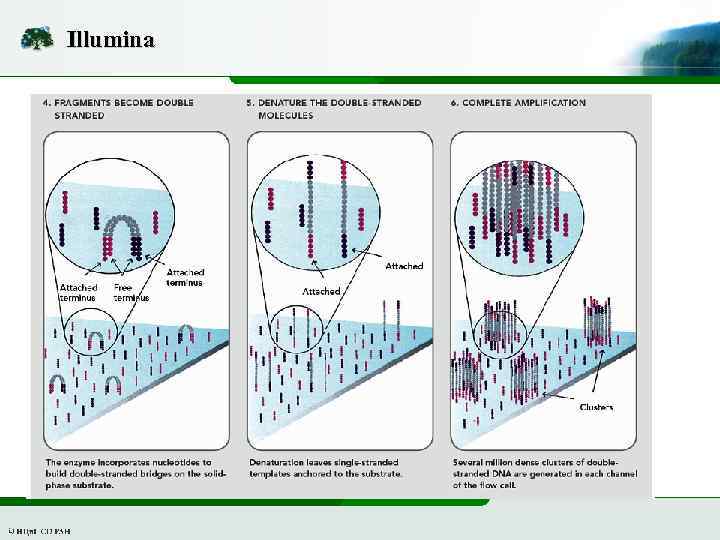 Illumina
Illumina
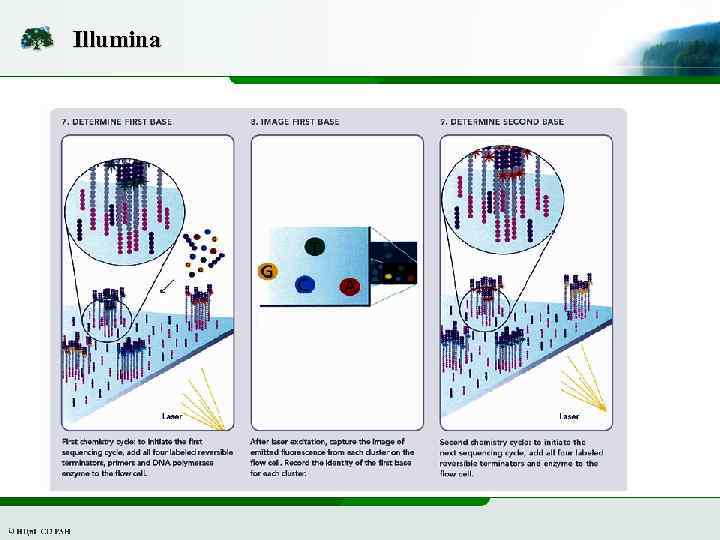 Illumina
Illumina
 Illumina GA и Hi. Seq vs Nova. Seq
Illumina GA и Hi. Seq vs Nova. Seq
 Illumina Next. Seq и Nova Seq Используются только два красителя и длины волн
Illumina Next. Seq и Nova Seq Используются только два красителя и длины волн
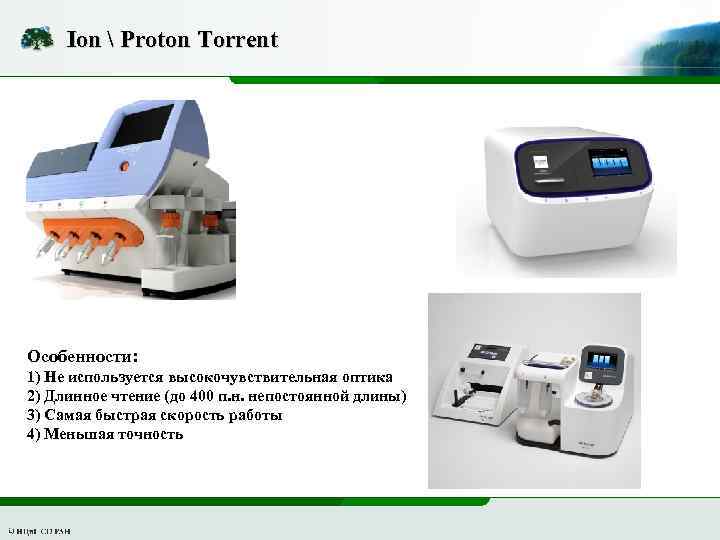 Ion Proton Torrent Особенности: 1) Не используется высокочувствительная оптика 2) Длинное чтение (до 400 п. н. непостоянной длины) 3) Самая быстрая скорость работы 4) Меньшая точность
Ion Proton Torrent Особенности: 1) Не используется высокочувствительная оптика 2) Длинное чтение (до 400 п. н. непостоянной длины) 3) Самая быстрая скорость работы 4) Меньшая точность
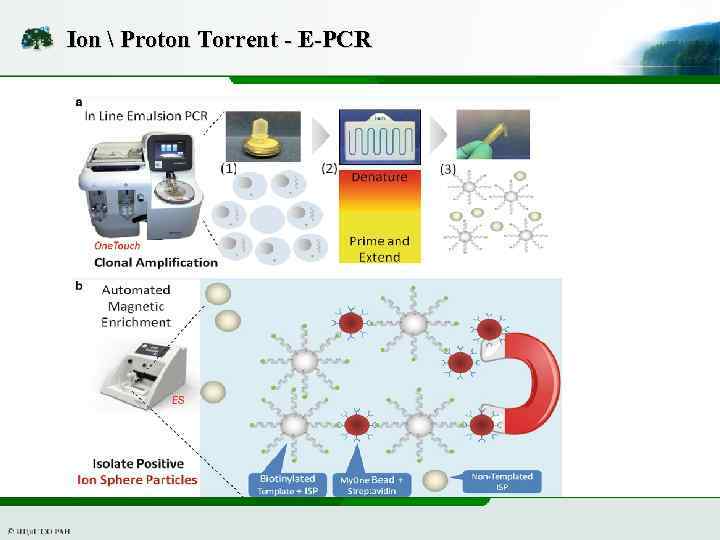 Ion Proton Torrent - E-PCR
Ion Proton Torrent - E-PCR
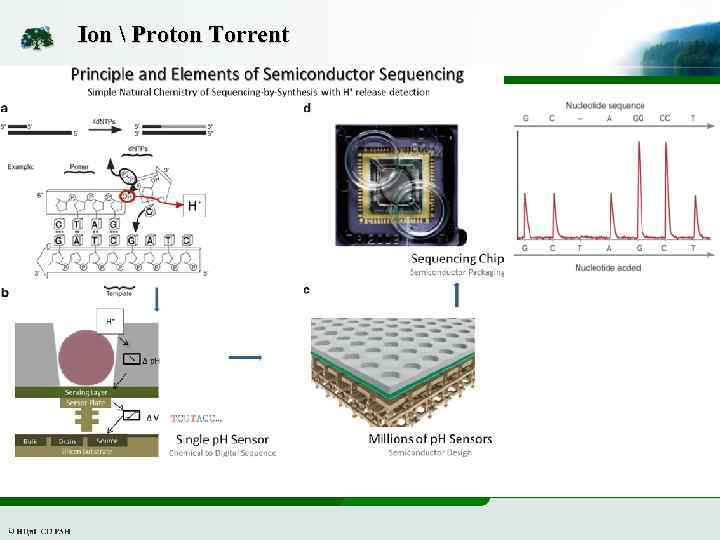 Ion Proton Torrent
Ion Proton Torrent
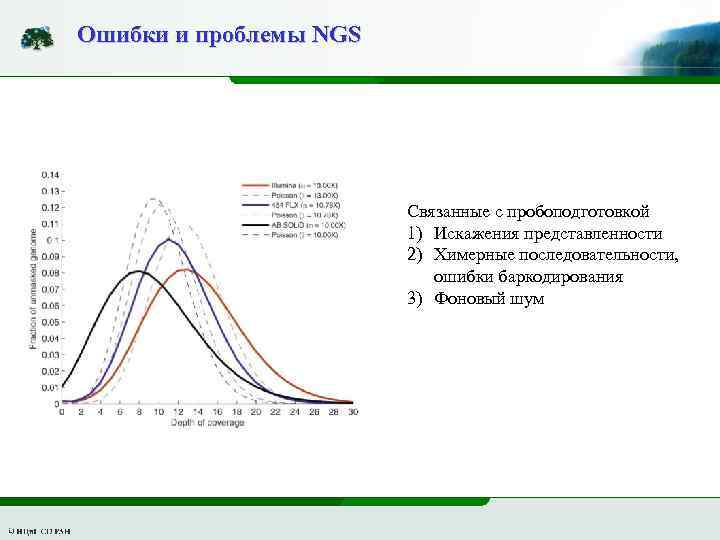 Ошибки и проблемы NGS Связанные с пробоподготовкой 1) Искажения представленности 2) Химерные последовательности, ошибки баркодирования 3) Фоновый шум
Ошибки и проблемы NGS Связанные с пробоподготовкой 1) Искажения представленности 2) Химерные последовательности, ошибки баркодирования 3) Фоновый шум
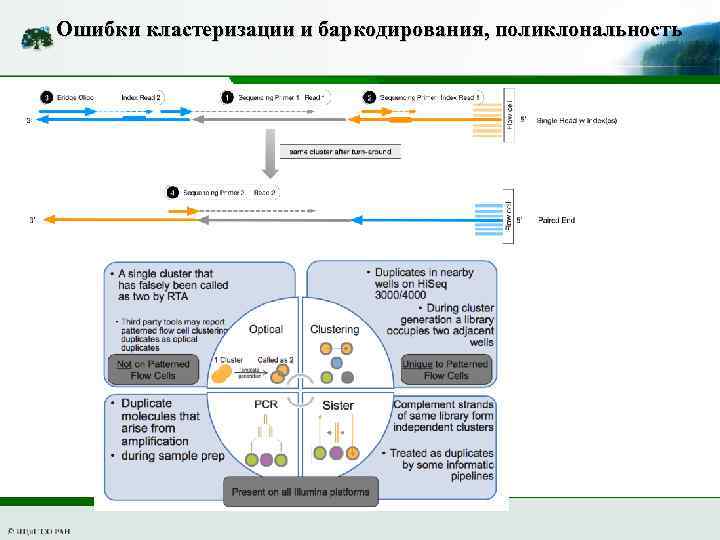 Ошибки кластеризации и баркодирования, поликлональность
Ошибки кластеризации и баркодирования, поликлональность
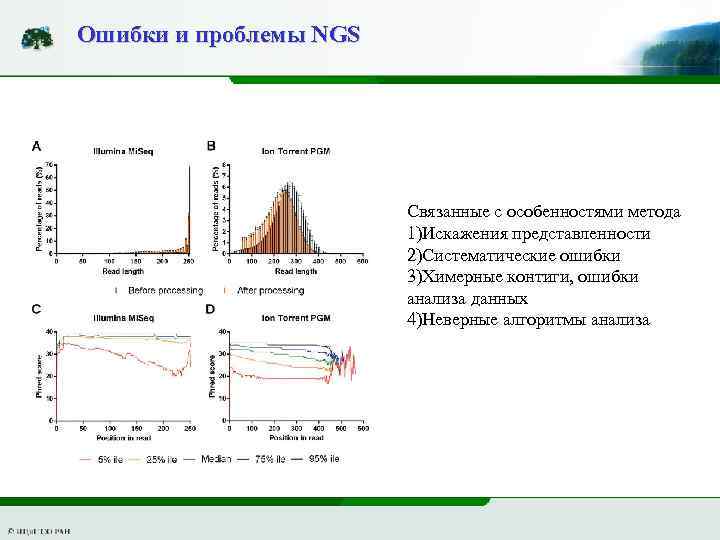 Ошибки и проблемы NGS Связанные с особенностями метода 1)Искажения представленности 2)Систематические ошибки 3)Химерные контиги, ошибки анализа данных 4)Неверные алгоритмы анализа
Ошибки и проблемы NGS Связанные с особенностями метода 1)Искажения представленности 2)Систематические ошибки 3)Химерные контиги, ошибки анализа данных 4)Неверные алгоритмы анализа
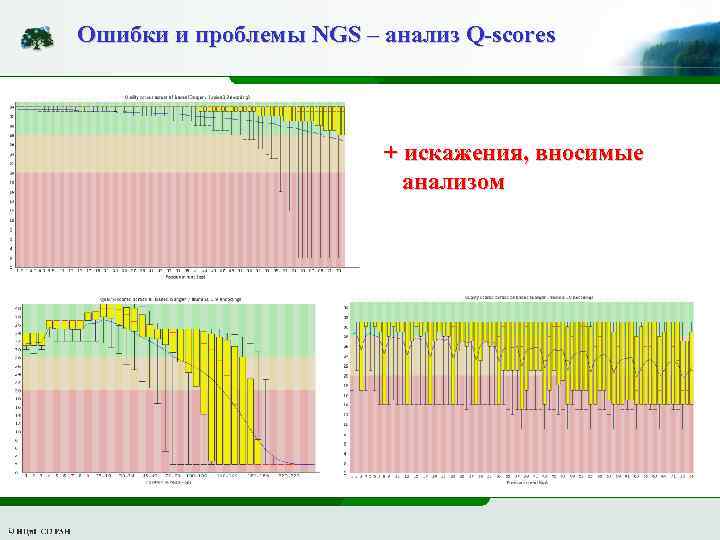 Ошибки и проблемы NGS – анализ Q-scores + искажения, вносимые анализом
Ошибки и проблемы NGS – анализ Q-scores + искажения, вносимые анализом
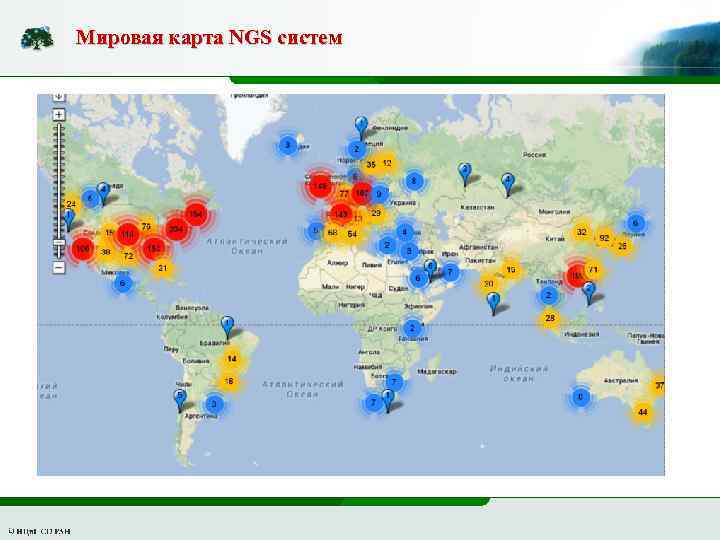 Мировая карта NGS систем
Мировая карта NGS систем
 Спасибо за внимание
Спасибо за внимание


