poster.ppt
- Количество слайдов: 2
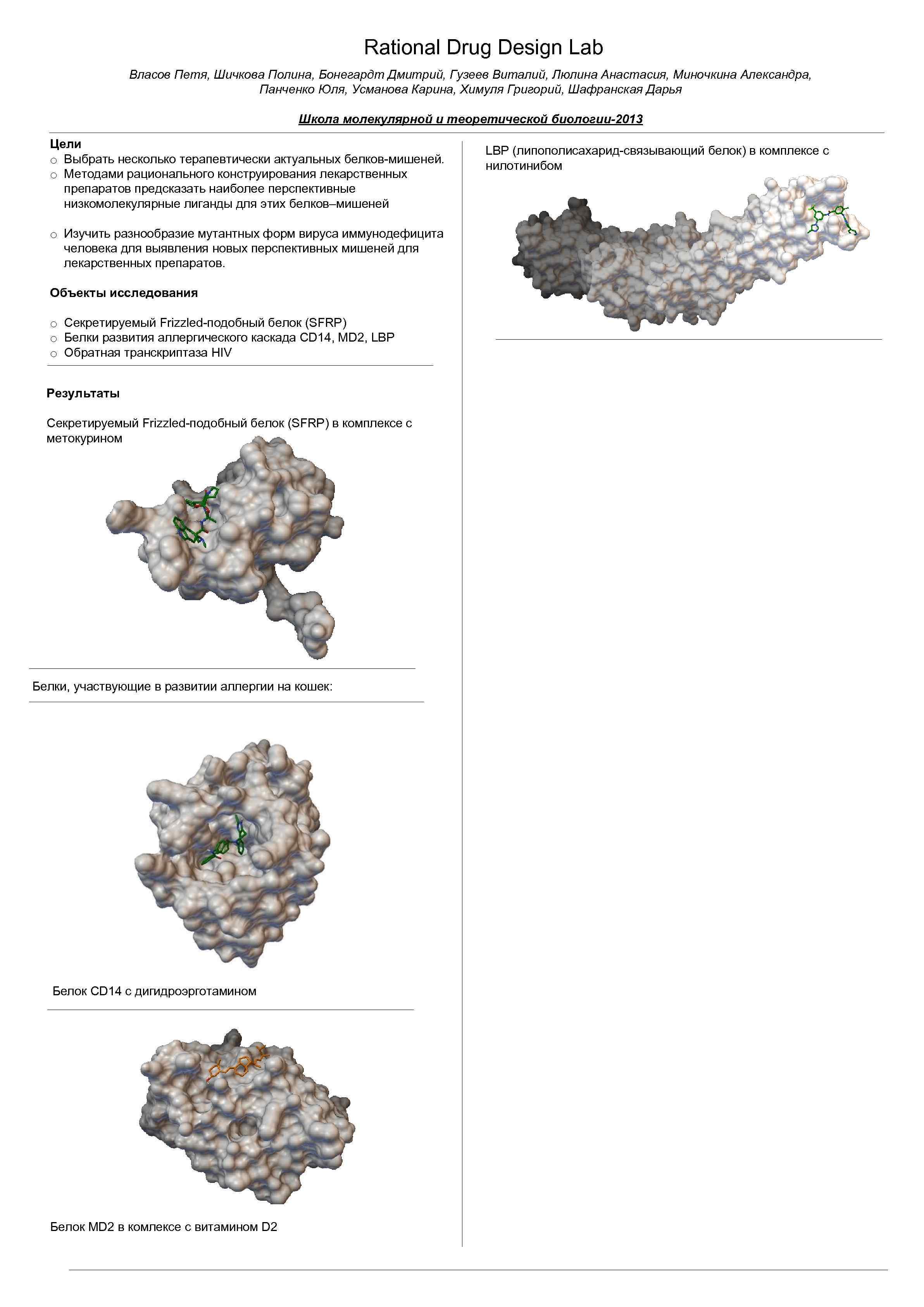
Rational Drug Design Lab Власов Петя, Шичкова Полина, Бонегардт Дмитрий, Гузеев Виталий, Люлина Анастасия, Миночкина Александра, Панченко Юля, Усманова Карина, Химуля Григорий, Шафранская Дарья Школа молекулярной и теоретической биологии-2013 Цели o Выбрать несколько терапевтически актуальных белков-мишеней. o Методами рационального конструирования лекарственных препаратов предсказать наиболее перспективные низкомолекулярные лиганды для этих белков–мишеней o Изучить разнообразие мутантных форм вируса иммунодефицита человека для выявления новых перспективных мишеней для лекарственных препаратов. Объекты исследования o Секретируемый Frizzled-подобный белок (SFRP) o Белки развития аллергического каскада CD 14, MD 2, LBP o Обратная транскриптаза HIV Результаты Секретируемый Frizzled-подобный белок (SFRP) в комплексе с метокурином Белки, участвующие в развитии аллергии на кошек: Белок CD 14 c дигидроэрготамином Белок MD 2 в комлексе с витамином D 2 LBP (липополисахарид-связывающий белок) в комплексе с нилотинибом
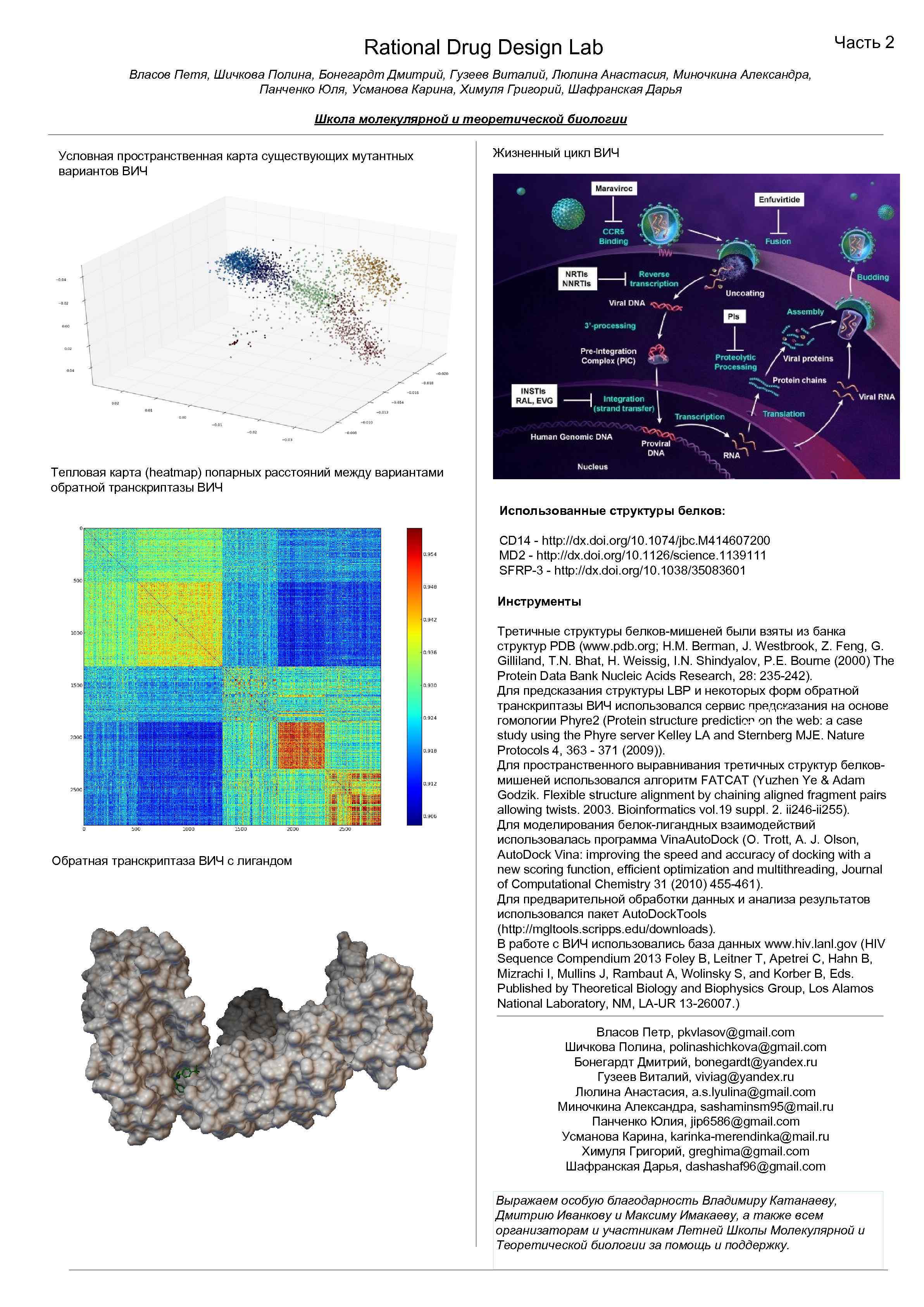
Rational Drug Design Lab Часть 2 Власов Петя, Шичкова Полина, Бонегардт Дмитрий, Гузеев Виталий, Люлина Анастасия, Миночкина Александра, Панченко Юля, Усманова Карина, Химуля Григорий, Шафранская Дарья Школа молекулярной и теоретической биологии Условная пространственная карта существующих мутантных вариантов ВИЧ Жизненный цикл ВИЧ LAMP-2 & Tadalafil Тепловая карта (heatmap) попарных расстояний между вариантами обратной транскриптазы ВИЧ Использованные структуры белков: CD 14 - http: //dx. doi. org/10. 1074/jbc. M 414607200 MD 2 - http: //dx. doi. org/10. 1126/science. 1139111 SFRP-3 - http: //dx. doi. org/10. 1038/35083601 Инструменты Frizzled & Risperidone Обратная транскриптаза ВИЧ с лигандом x. Wnt-8 & Adapalene Третичные структуры белков-мишеней были взяты из банка структур PDB (www. pdb. org; H. M. Berman, J. Westbrook, Z. Feng, G. Gilliland, T. N. Bhat, H. Weissig, I. N. Shindyalov, P. E. Bourne (2000) The Protein Data Bank Nucleic Acids Research, 28: 235 -242). Для предсказания структуры LBP и некоторых форм обратной транскриптазы ВИЧ использовался сервис Imatinib & предсказания на основе гомологии Phyre 2 (Protein structure prediction on the web: a case IFN-omega study using the Phyre server Kelley LA and Sternberg MJE. Nature Protocols 4, 363 - 371 (2009)). Для пространственного выравнивания третичных структур белковмишеней использовался алгоритм FATCAT (Yuzhen Ye & Adam Godzik. Flexible structure alignment by chaining aligned fragment pairs allowing twists. 2003. Bioinformatics vol. 19 suppl. 2. ii 246 -ii 255). Для моделирования белок-лигандных взаимодействий использовалась программа Vina. Auto. Dock (O. Trott, A. J. Olson, Auto. Dock Vina: improving the speed and accuracy of docking with a new scoring function, efficient optimization and multithreading, Journal of Computational Chemistry 31 (2010) 455 -461). Для предварительной обработки данных и анализа результатов использовался пакет Auto. Dock. Tools (http: //mgltools. scripps. edu/downloads). В работе с ВИЧ использовались база данных www. hiv. lanl. gov (HIV Sequence Compendium 2013 Foley B, Leitner T, Apetrei C, Hahn B, Mizrachi I, Mullins J, Rambaut A, Wolinsky S, and Korber B, Eds. Published by Theoretical Biology and Biophysics Group, Los Alamos National Laboratory, NM, LA-UR 13 -26007. ) Власов Петр, pkvlasov@gmail. com Шичкова Полина, polinashichkova@gmail. com Бонегардт Дмитрий, bonegardt@yandex. ru Гузеев Виталий, viviag@yandex. ru Люлина Анастасия, a. s. lyulina@gmail. com Миночкина Александра, sashaminsm 95@mail. ru Панченко Юлия, jip 6586@gmail. com Усманова Карина, karinka-merendinka@mail. ru Химуля Григорий, greghima@gmail. com Шафранская Дарья, dashashaf 96@gmail. com Выражаем особую благодарность Владимиру Катанаеву, Дмитрию Иванкову и Максиму Имакаеву, а также всем организаторам и участникам Летней Школы Молекулярной и Теоретической биологии за помощь и поддержку.
poster.ppt