Долинная.ppt
- Количество слайдов: 67

Неканонические формы ДНК и их биологическое значение Н. Г. Долинная

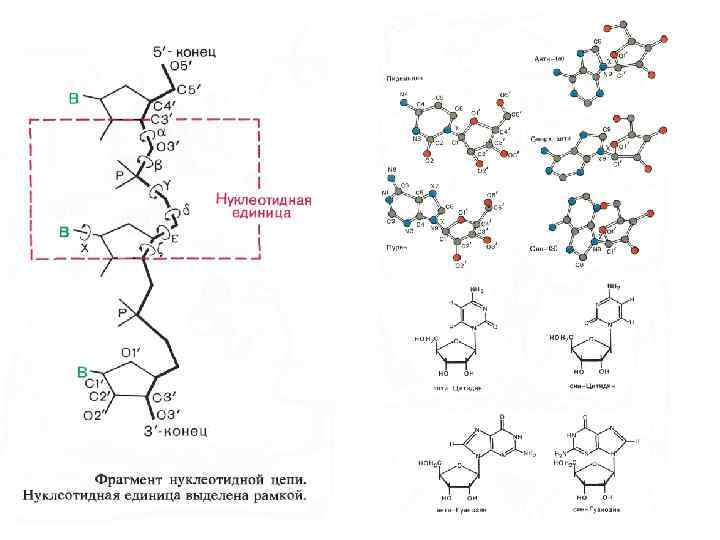
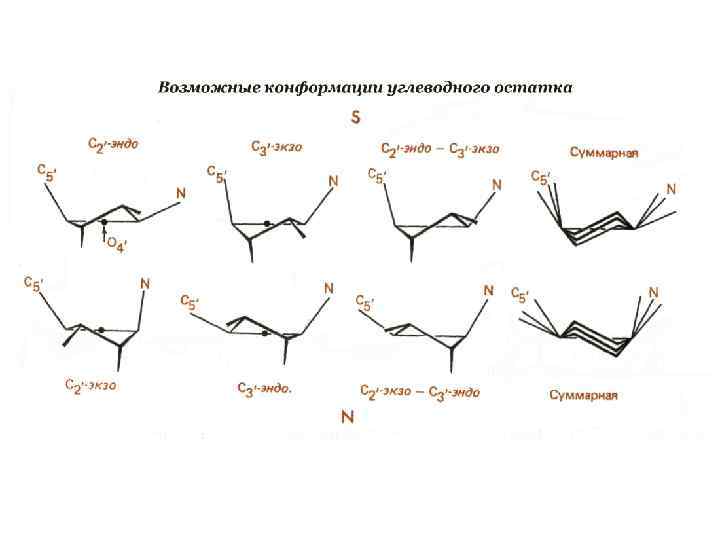
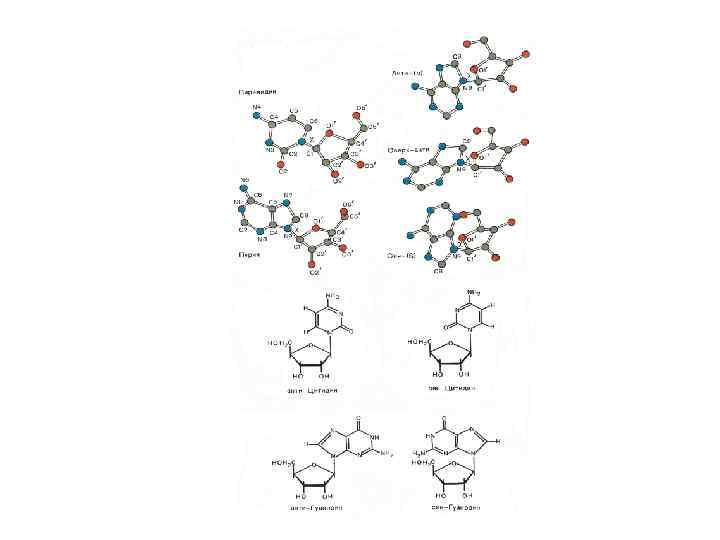
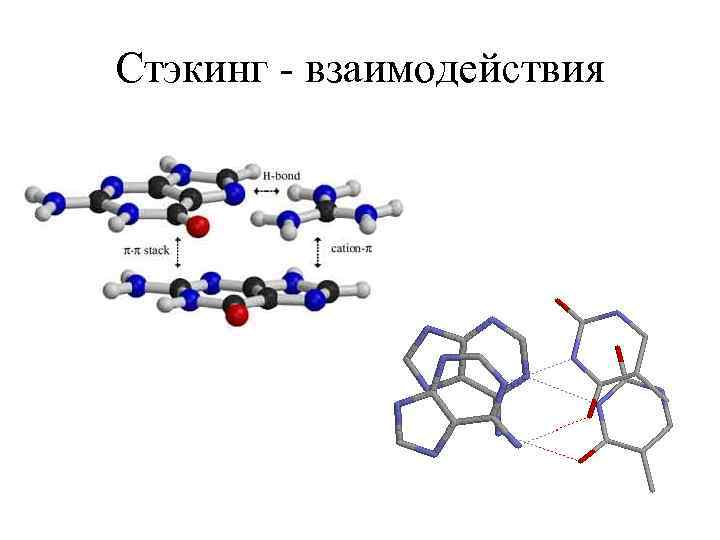
Стэкинг - взаимодействия
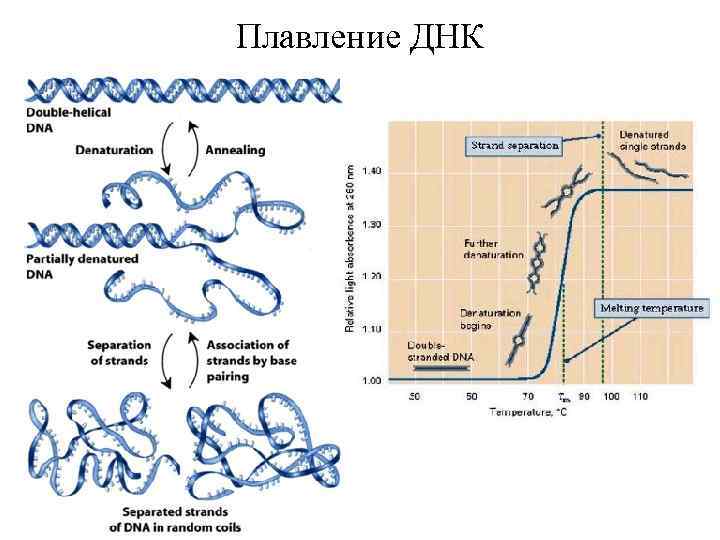
Плавление ДНК
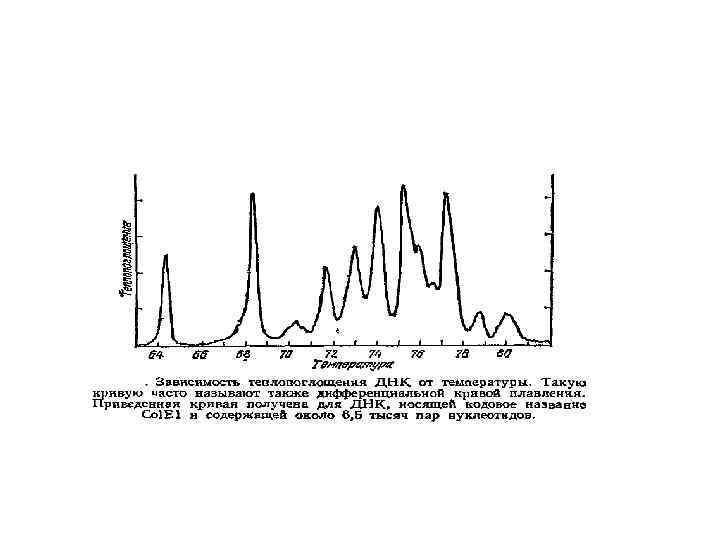

Электронная микроскопия плавления ДНКдуплекса
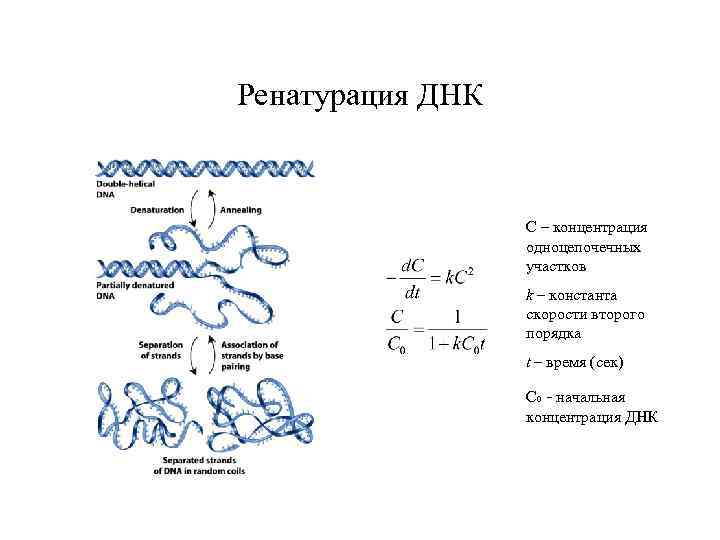
Ренатурация ДНК С – концентрация одноцепочечных участков k – константа скорости второго порядка t – время (сек) С 0 - начальная концентрация ДНК
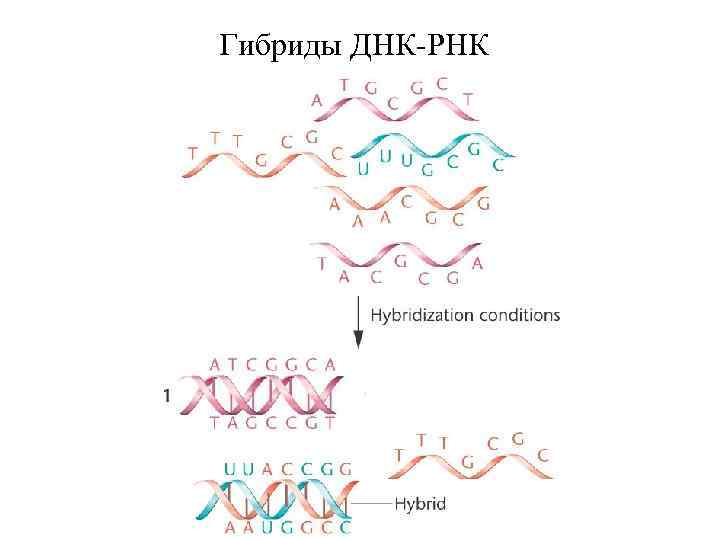
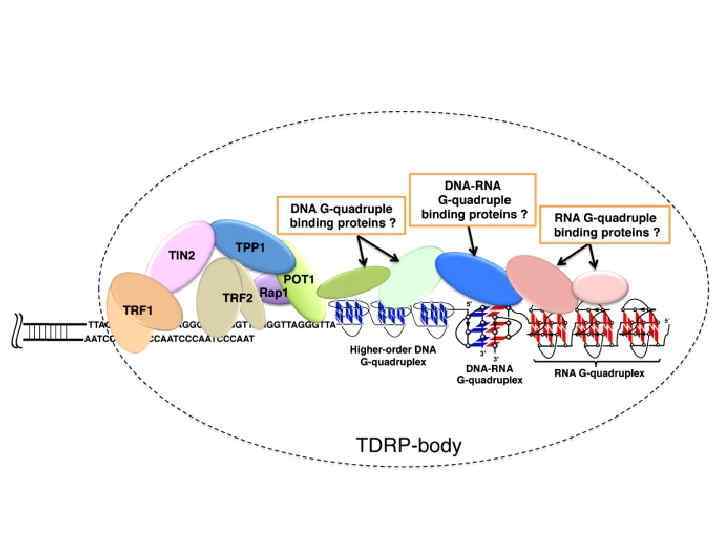
Гибриды ДНК-РНК
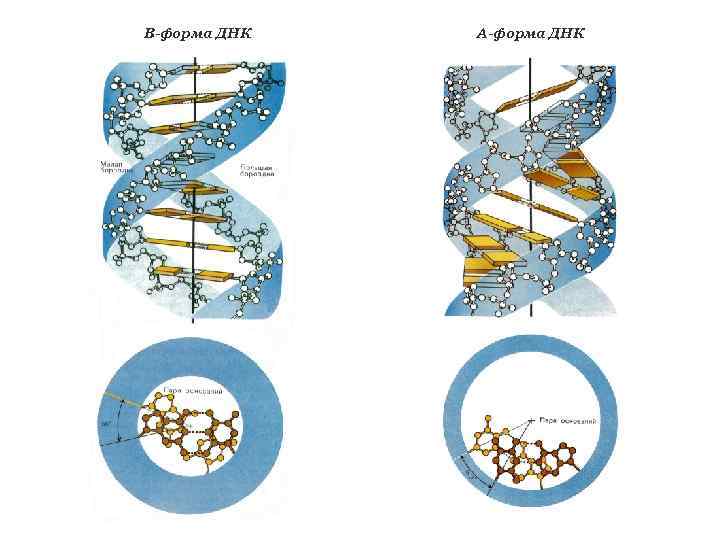
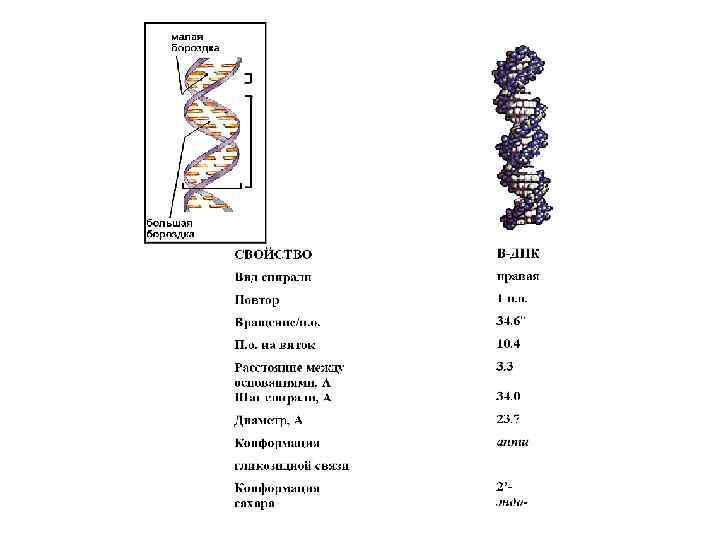
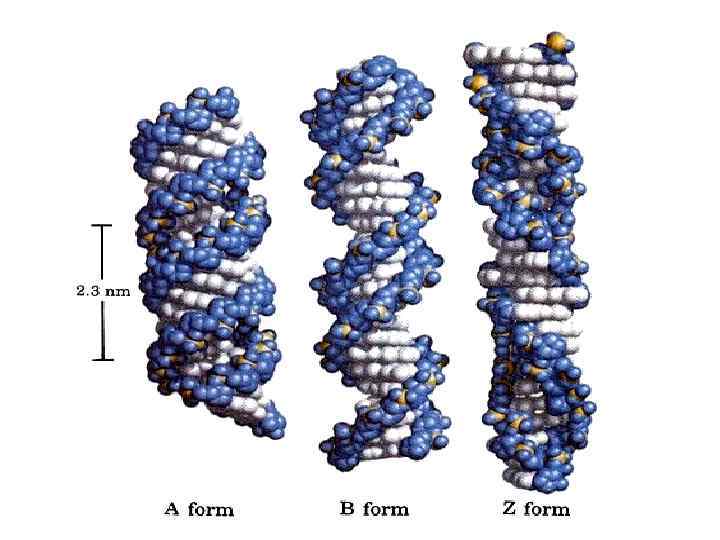
В-форма ДНК А-форма ДНК
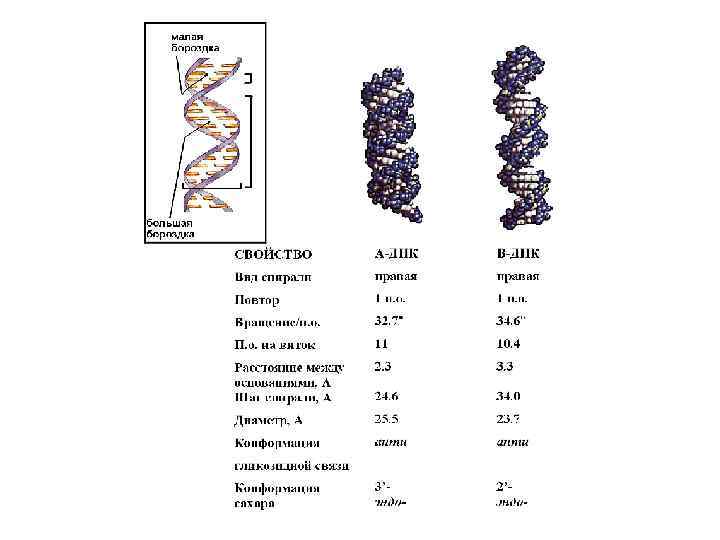

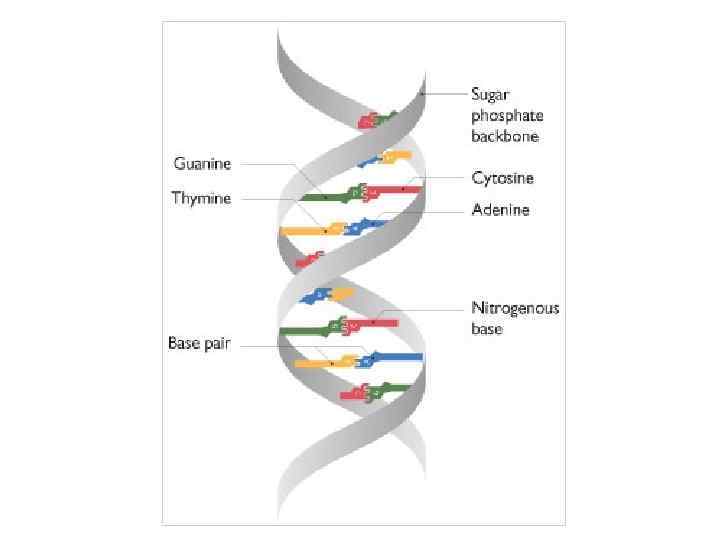
Канонические структуры ДНК (А- и В- формы) m двойные спирали m с антипараллельной ориентацией цепей m правозакрученные m стабилизированы Уотсон-Криковскими парами оснований (A-T, G-C) m плектонимичные дуплексы (для разделения цепей необходимо раскрутить двойную спираль) m вторичная структура всей молекулы может быть выведена из конформации отдельной нуклеотидной пары m линейные (неразветвленные) спирали

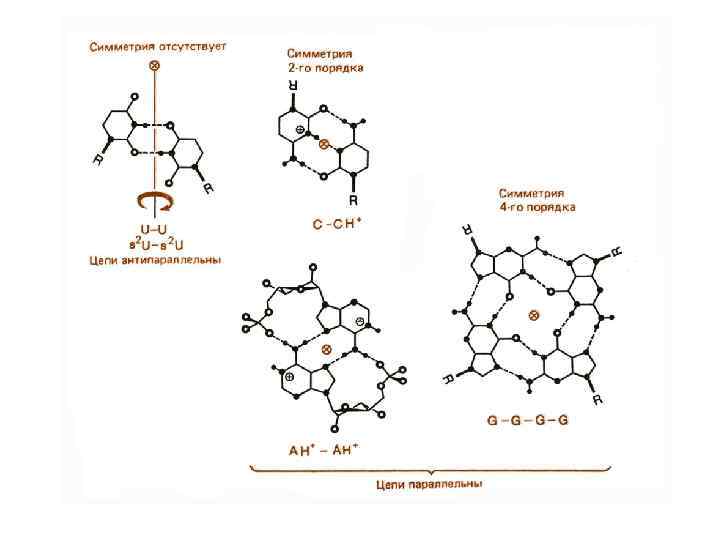
Последовательности ДНК, склонные к образованию неканонических форм m повторяющиеся моно-, ди- и тринуклеотидные последовательности, включая пурин-пиримидиновые и пурин-пуриновые повторы m гомопуриновые–гомопиримидиновые цепи m палиндромные последовательности m зеркально-симметричные последовательности m двойные спирали, содержащие только А-Т пары m oligo. A-тракты, oligo. G-тракты, oligo. C-тракты m более сложные типы внутренней симметрии
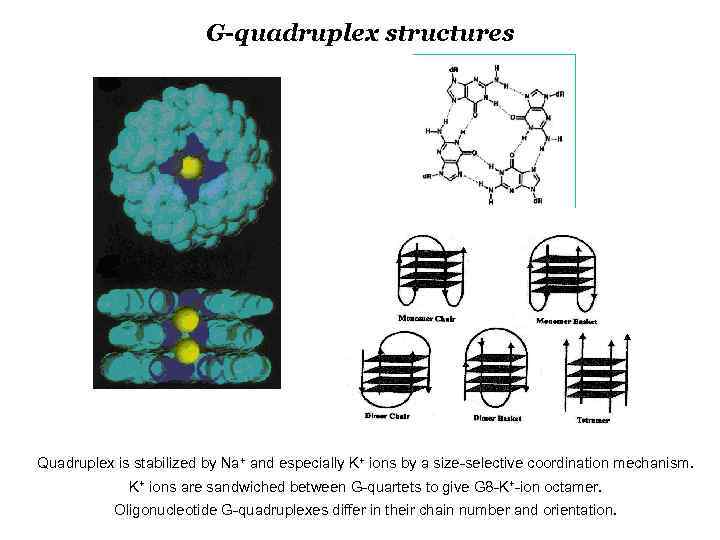
G-quadruplex structures Quadruplex is stabilized by Na+ and especially K+ ions by a size-selective coordination mechanism. K+ ions are sandwiched between G-quartets to give G 8 -K+-ion octamer. Oligonucleotide G-quadruplexes differ in their chain number and orientation.
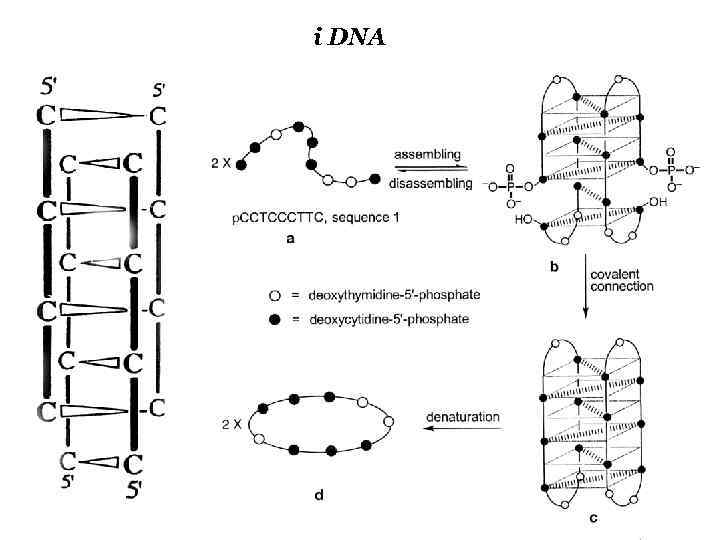
i DNA
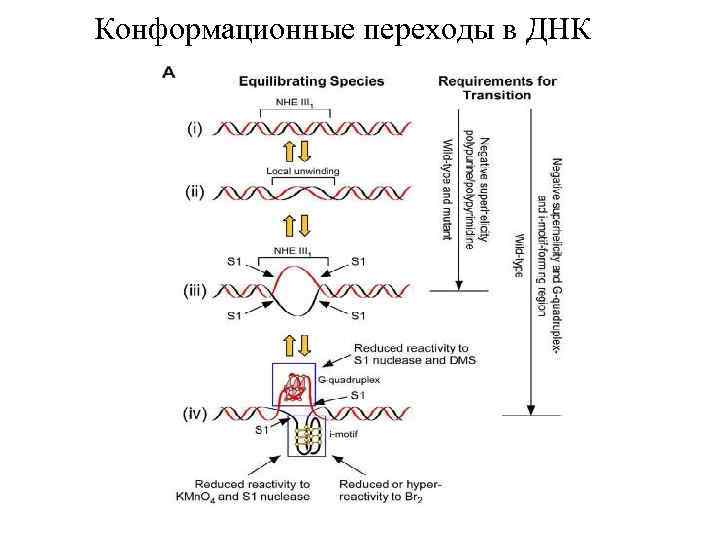
Конформационные переходы в ДНК
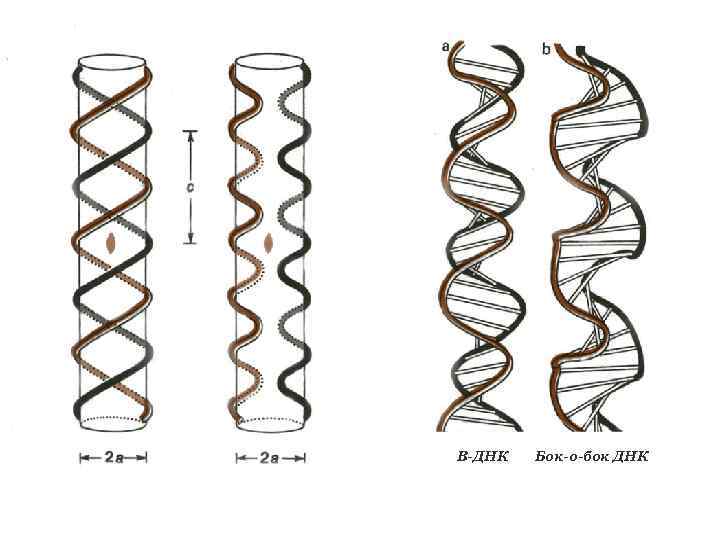
B-ДНК Бок-о-бок ДНК
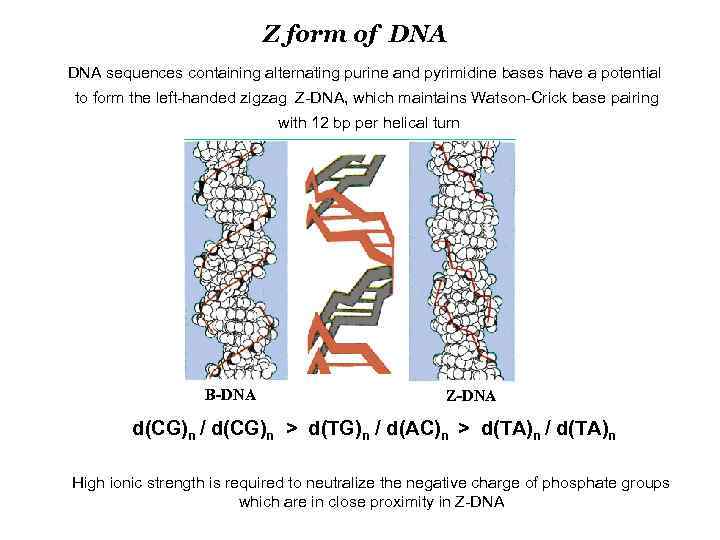
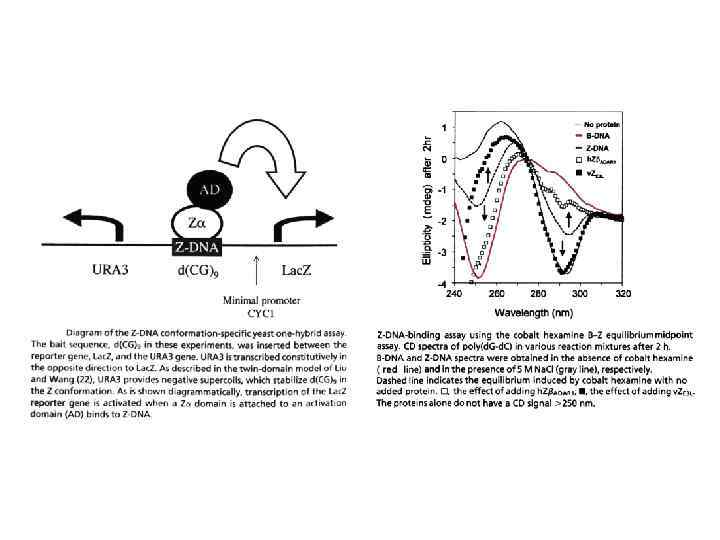
Z form of DNA sequences containing alternating purine and pyrimidine bases have a potential to form the left-handed zigzag Z-DNA, which maintains Watson-Crick base pairing with 12 bp per helical turn B-DNA Z-DNA d(CG)n / d(CG)n > d(TG)n / d(AC)n > d(TA)n / d(TA)n High ionic strength is required to neutralize the negative charge of phosphate groups which are in close proximity in Z-DNA

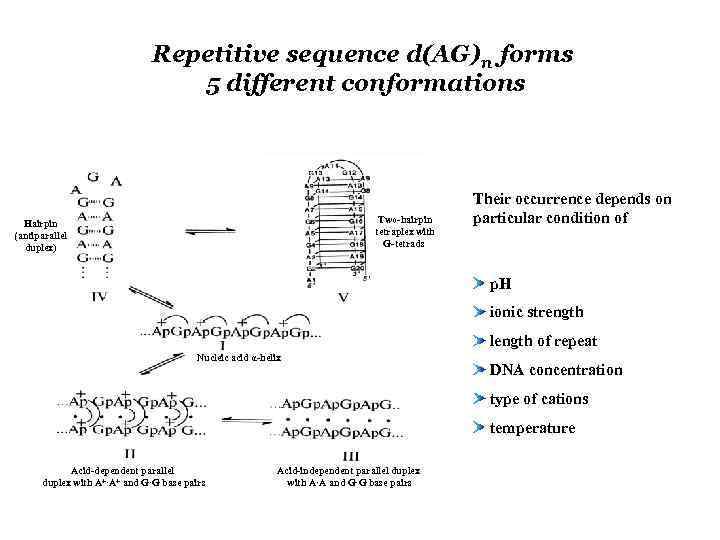
Repetitive sequence d(AG)n forms 5 different conformations Two-hairpin tetraplex with G-tetrads Hairpin (antiparallel duplex) Their occurrence depends on particular condition of p. H ionic strength length of repeat Nucleic acid α-helix DNA concentration type of cations temperature Acid-dependent parallel duplex with A+·A+ and G·G base pairs Acid-independent parallel duplex with A·A and G·G base pairs
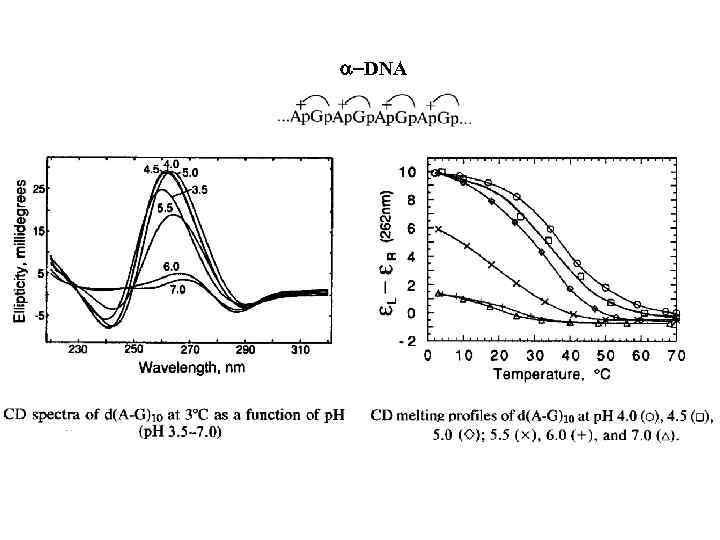
a-DNA
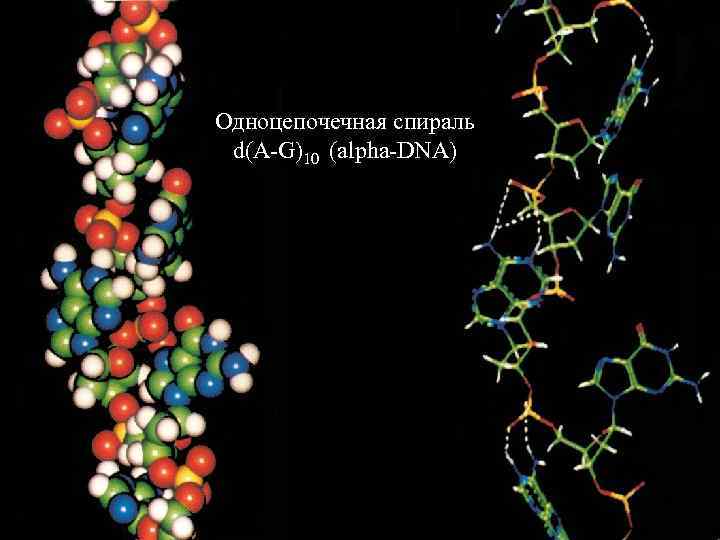
Одноцепочечная спираль d(A-G)10 (alpha-DNA)
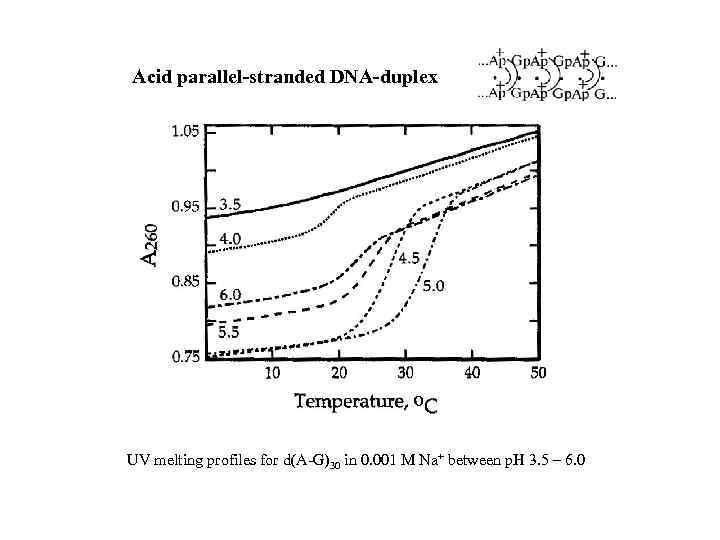
Acid parallel-stranded DNA-duplex UV melting profiles for d(A-G)30 in 0. 001 M Na+ between p. H 3. 5 – 6. 0
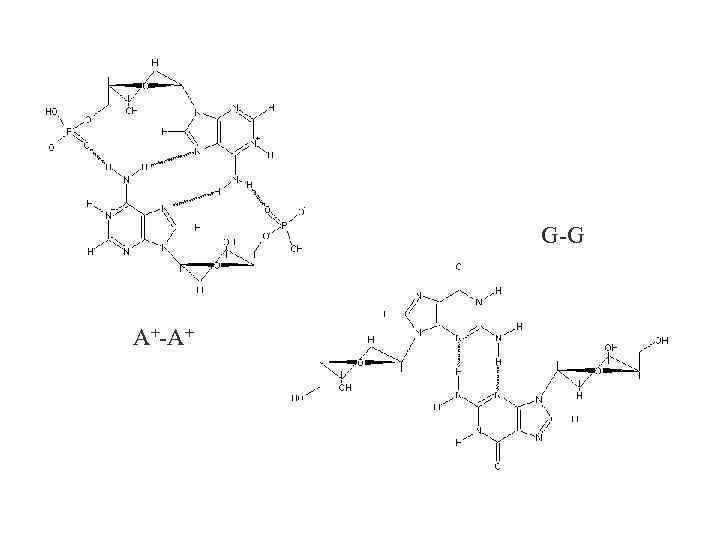
G-G A+-A+
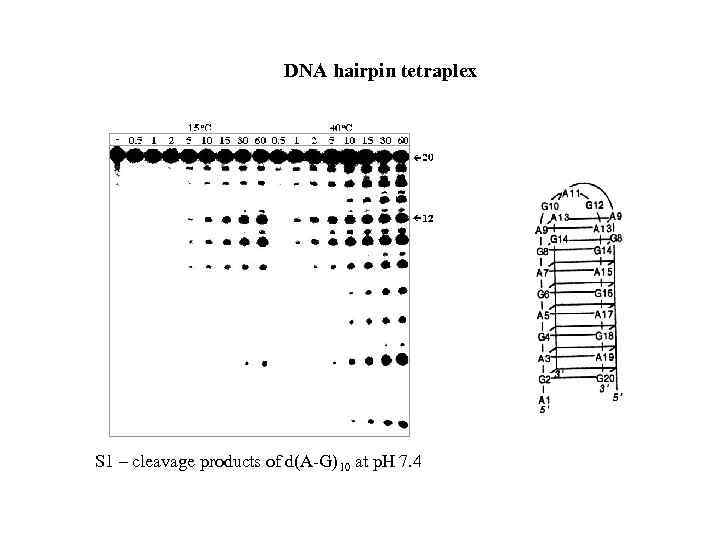
DNA hairpin tetraplex S 1 – cleavage products of d(A-G)10 at p. H 7. 4
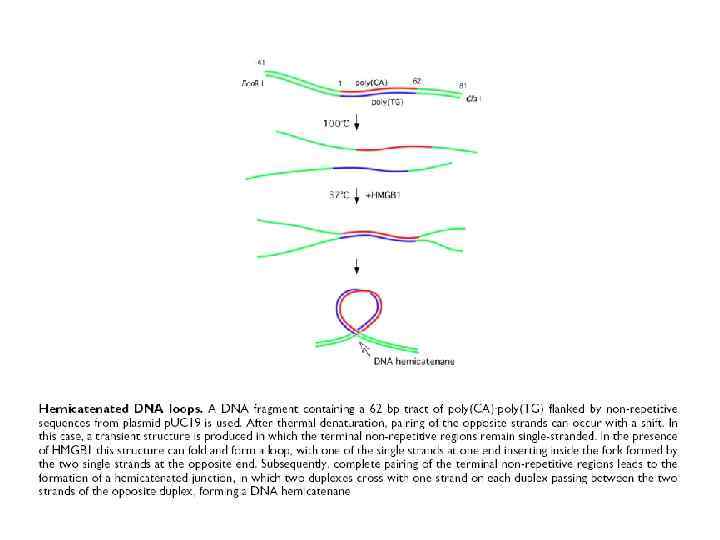
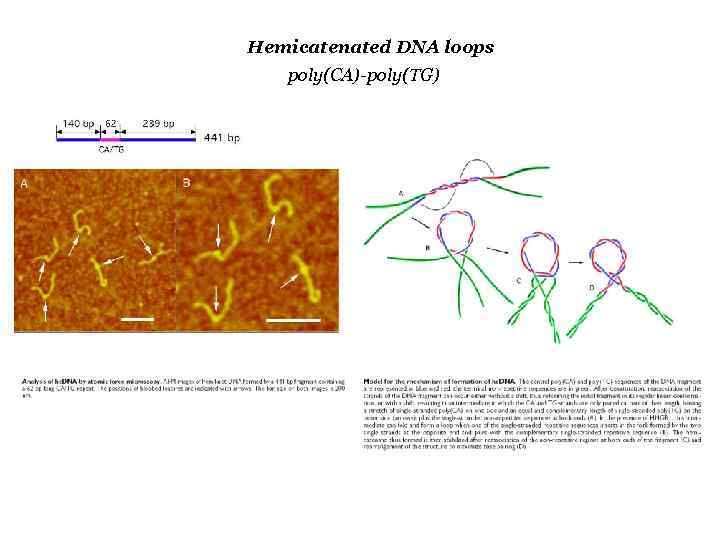
Hemicatenated DNA loops poly(CA)-poly(TG)
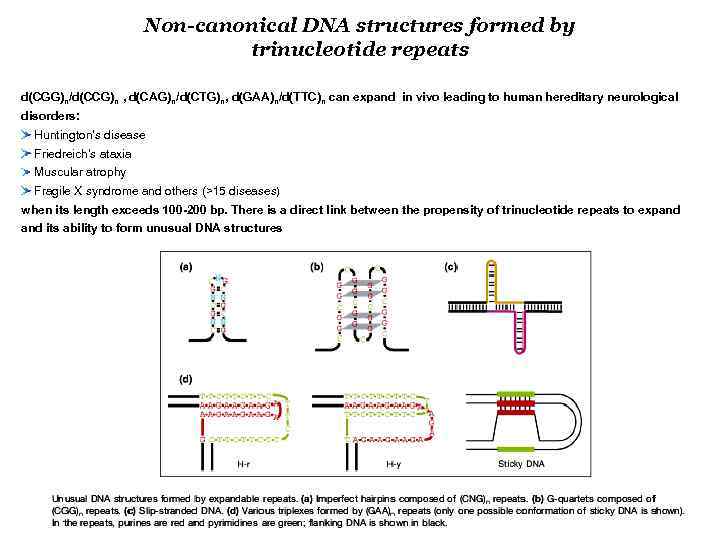
Non-canonical DNA structures formed by trinucleotide repeats d(CGG)n/d(CCG)n , d(CAG)n/d(CTG)n, d(GAA)n/d(TTC)n can expand in vivo leading to human hereditary neurological disorders: Huntington’s disease Friedreich’s ataxia Muscular atrophy Fragile X syndrome and others (>15 diseases) when its length exceeds 100 -200 bp. There is a direct link between the propensity of trinucleotide repeats to expand its ability to form unusual DNA structures
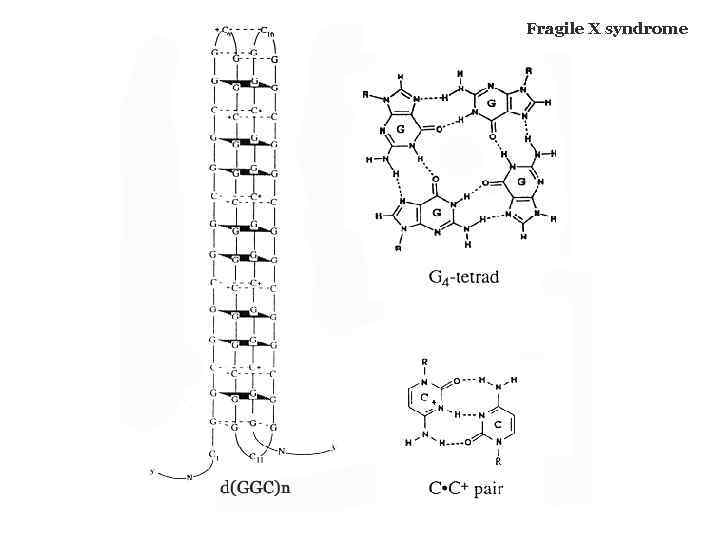
Fragile X syndrome
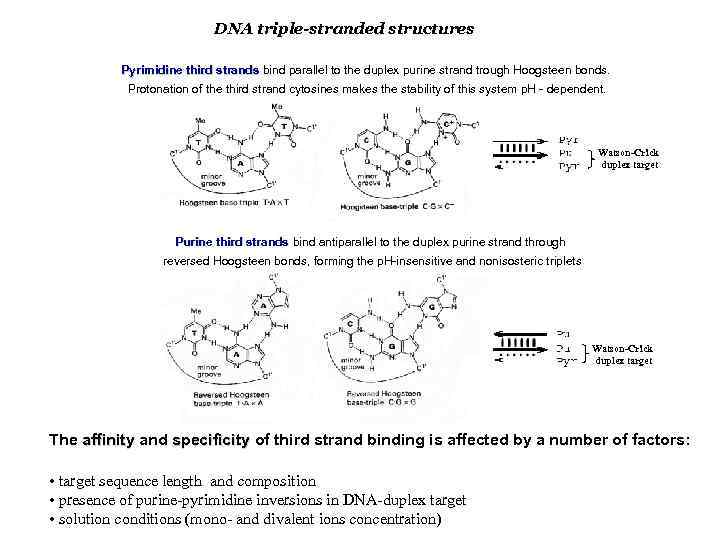
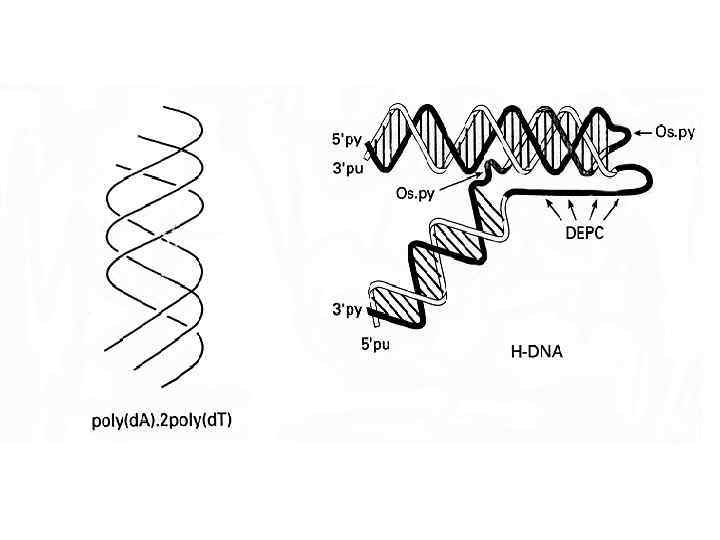
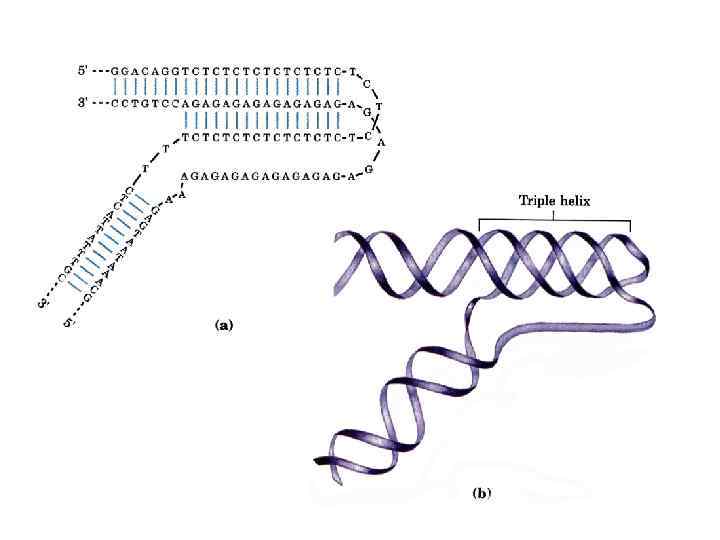
DNA triple-stranded structures Pyrimidine third strands bind parallel to the duplex purine strand trough Hoogsteen bonds. Protonation of the third strand cytosines makes the stability of this system p. H - dependent. Watson-Crick duplex target Purine third strands bind antiparallel to the duplex purine strand through reversed Hoogsteen bonds, forming the p. H-insensitive and nonisosteric triplets Watson-Crick duplex target The affinity and specificity of third strand binding is affected by a number of factors: • target sequence length and composition • presence of purine-pyrimidine inversions in DNA-duplex target • solution conditions (mono- and divalent ions concentration)
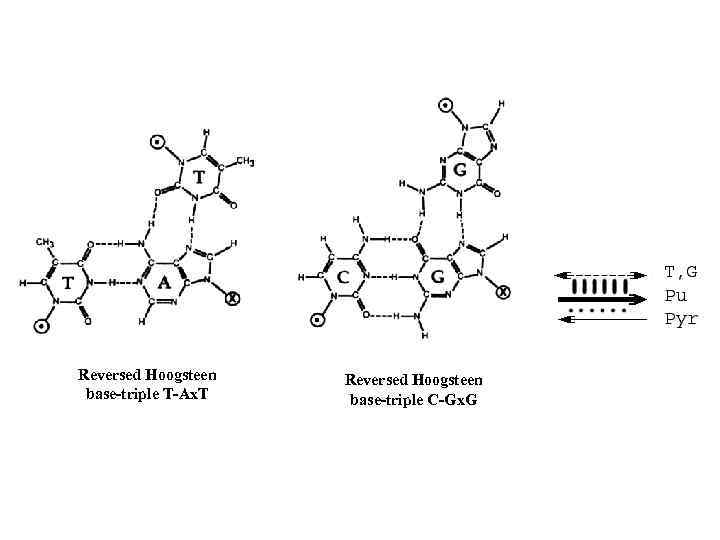
Reversed Hoogsteen base-triple T-Ax. T Reversed Hoogsteen base-triple C-Gx. G
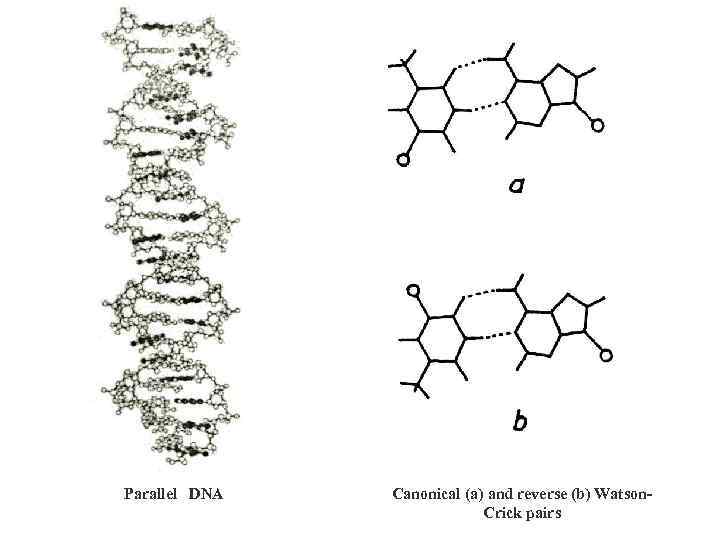
Parallel DNA Canonical (a) and reverse (b) Watson. Crick pairs

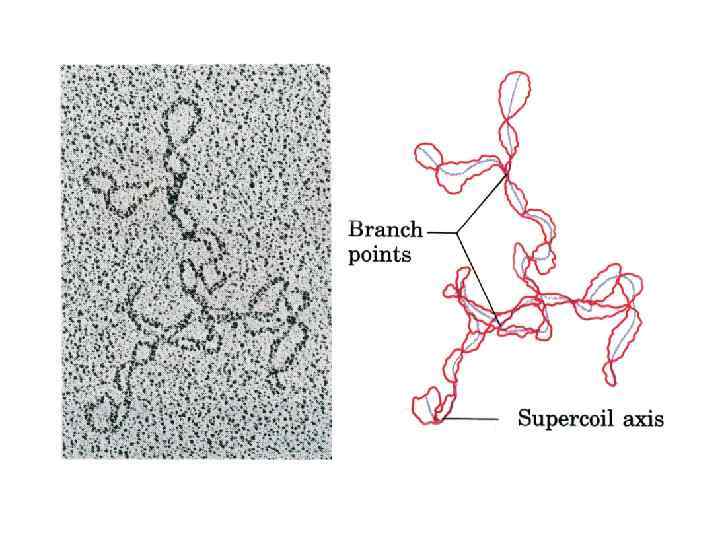
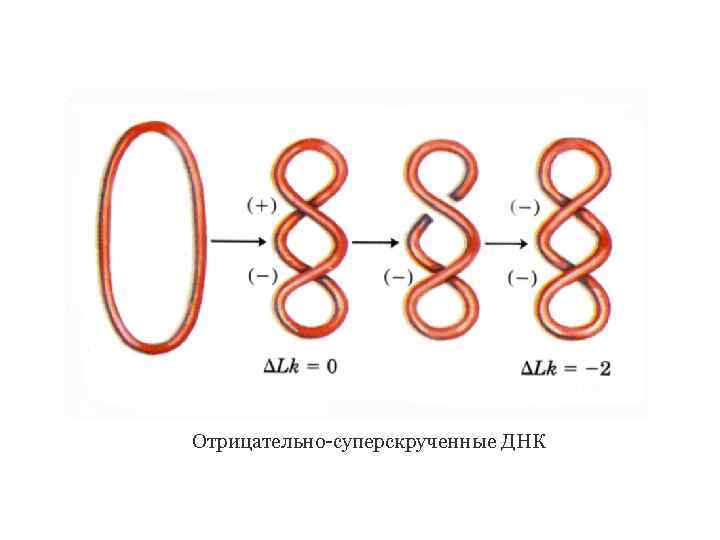
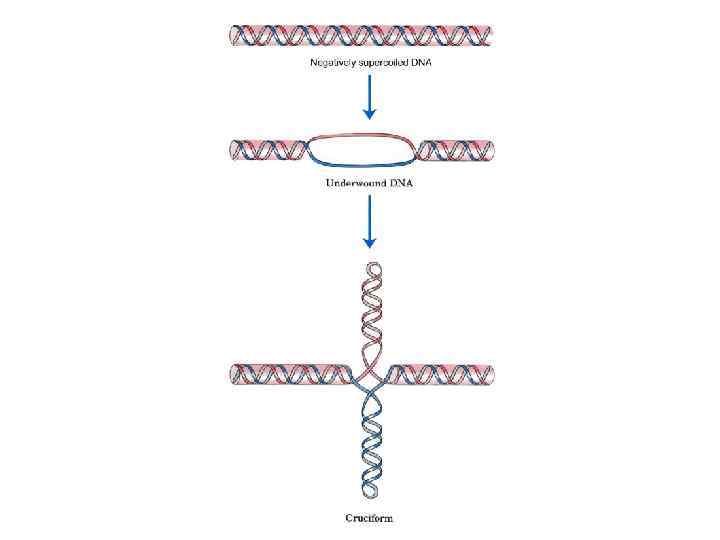
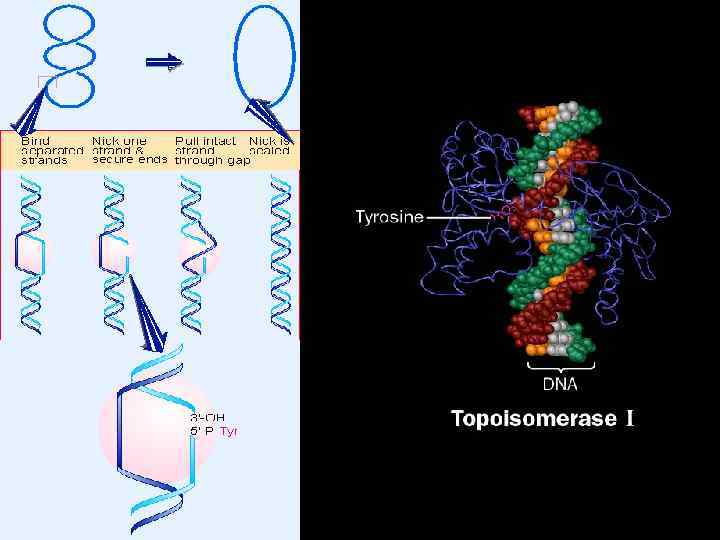
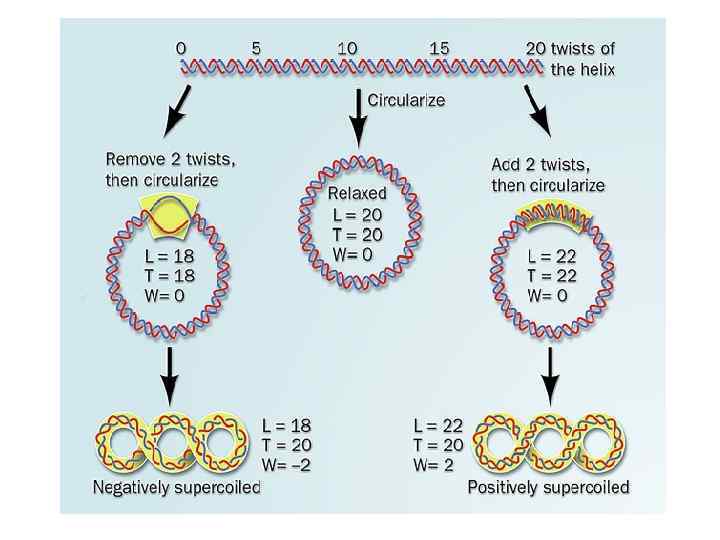
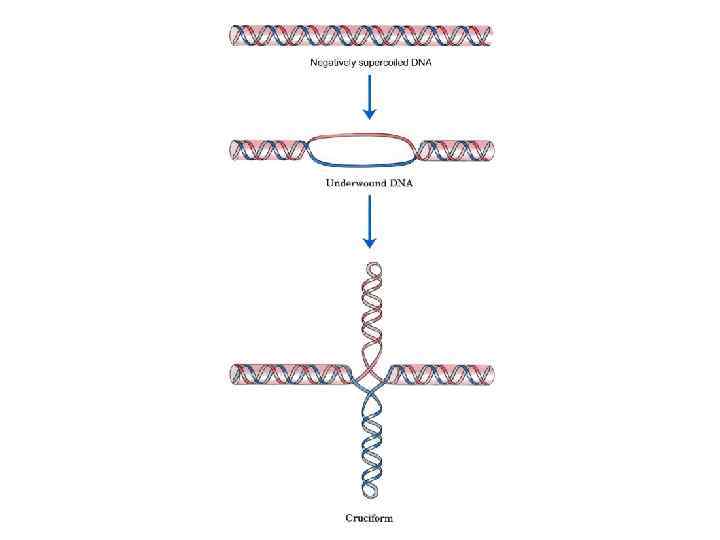
Отрицательно-суперскрученные ДНК

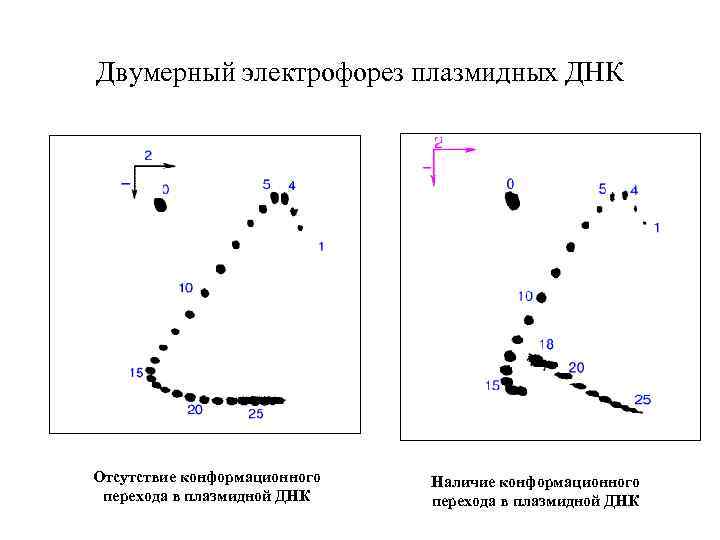
Двумерный электрофорез плазмидных ДНК Отсутствие конформационного перехода в плазмидной ДНК Наличие конформационного перехода в плазмидной ДНК

Последовательности, склонные к формированию неканонических форм повторяющиеся моно-, ди- и тринуклеотидные последовательности, включая пурин-пиримидиновые и пурин-пуриновые повторы Z-ДНК, параллельные дуплексы, полукатенаны, одноцепочечная αДНК гомопуриновые–гомопиримидиновые цепи ДНК-триплексы палиндромные последовательности крестообразные формы зеркально-симметричные последовательности H-ДНК двойные спирали, содержащие только А-Т пары oligo. G-тракты, oligo. C-тракты параллельные дуплексы G-квадруплексы, i-ДНК

Последовательности, образующие неканонические формы ДНК, относительно редки в прокариотах, но широко распространены в эукариотических организмах. Обычно они локализованы в важных участках генома: ► теломеры хромосом ► центромерная область ► горячие точки мутаций ► промоторные участки генов (часто онкогенов) ► локусы экспансии тринуклеотидных повторов ► стык генов легких и тяжелых цепей иммуноглобулина ► горячие точки рекомбинации

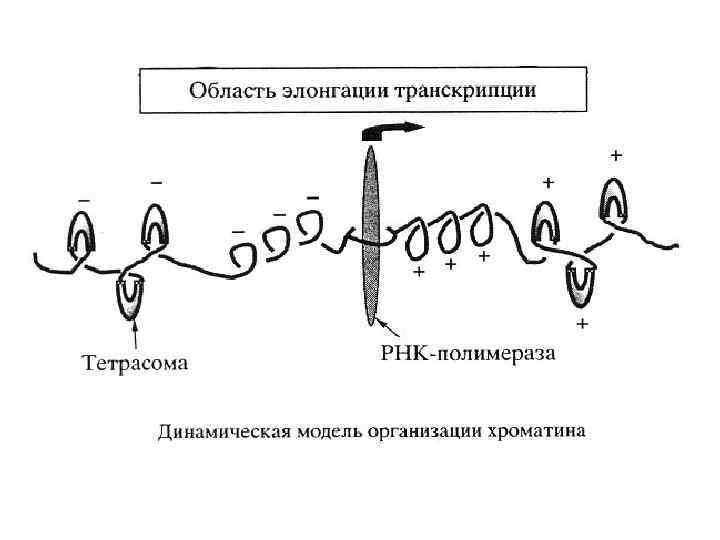
Неканонические формы ДНК узнаются и стабилизируются многочисленными белками (ферментами) и могут влиять на клеточные процессы ► репликации ► транскрипции ► рекомбинации ► элонгации теломер ► организации хроматина ► репарации геномных повреждений ► эпигенетической нестабильности
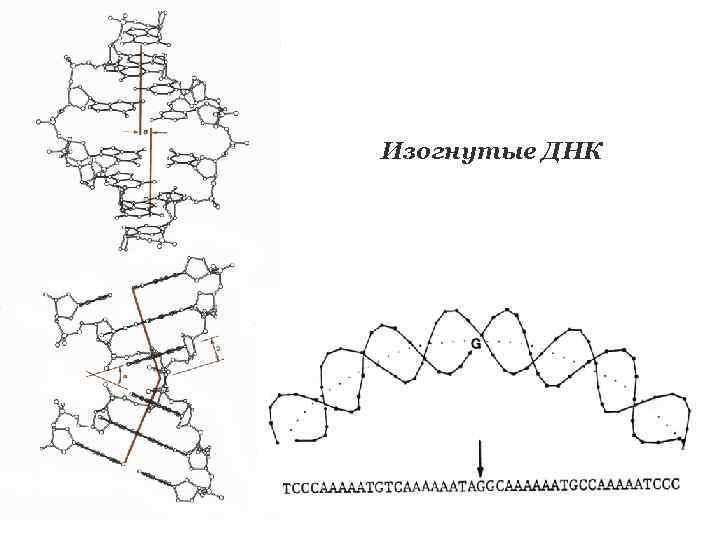
Изогнутые ДНК
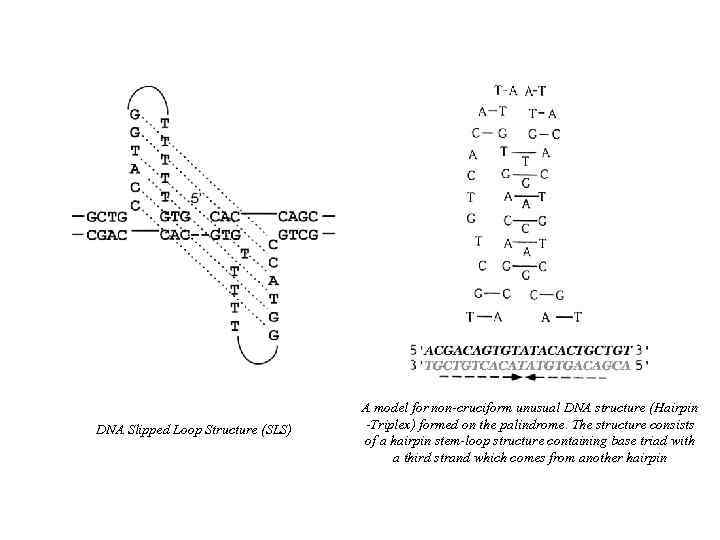
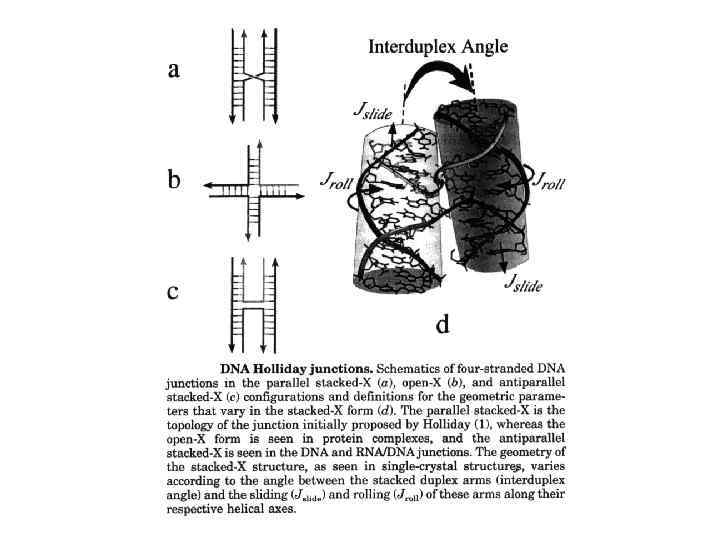
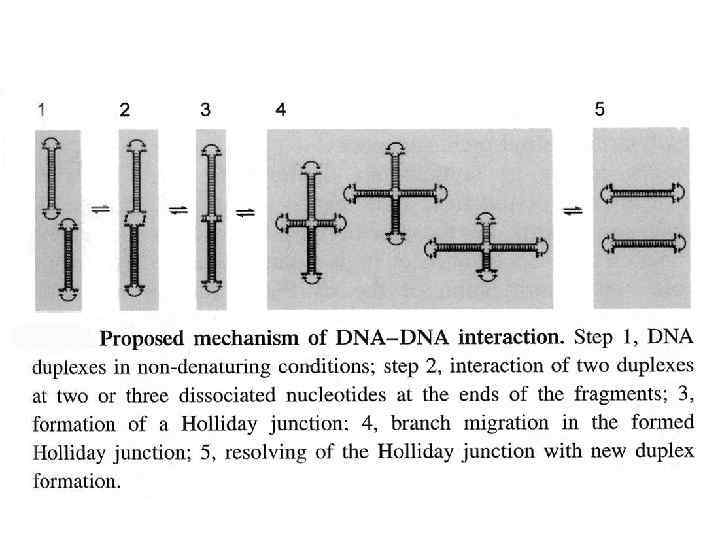
DNA Slipped Loop Structure (SLS) A model for non-cruciform unusual DNA structure (Hairpin -Triplex) formed on the palindrome. The structure consists of a hairpin stem-loop structure containing base triad with a third strand which comes from another hairpin
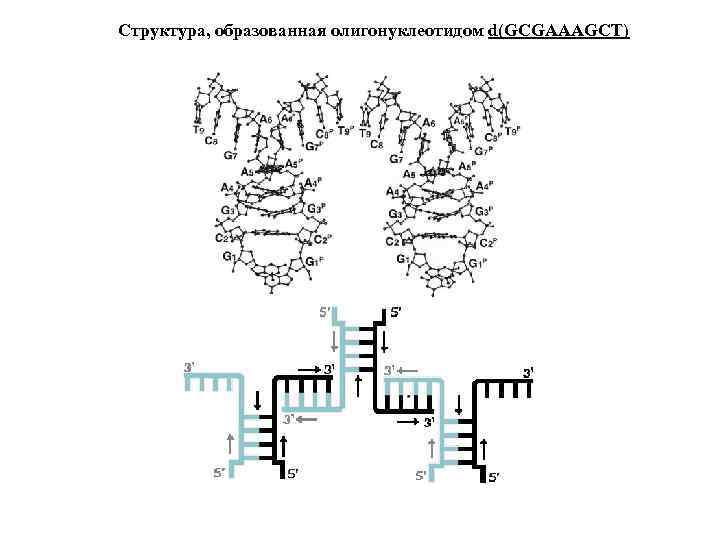
Структура, образованная олигонуклеотидом d(GCGAAAGCT)
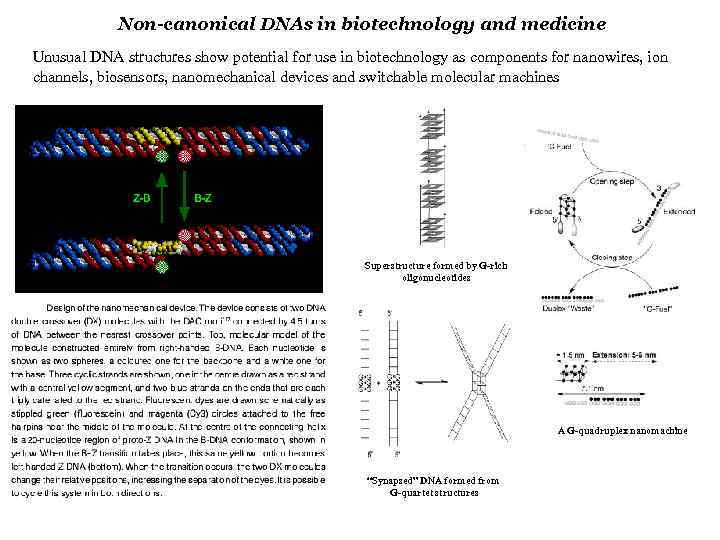
Non-canonical DNAs in biotechnology and medicine Unusual DNA structures show potential for use in biotechnology as components for nanowires, ion channels, biosensors, nanomechanical devices and switchable molecular machines Superstructure formed by G-rich oligonucleotides A G-quadruplex nanomachine “Synapsed” DNA formed from G-quartet structures

Долинная.ppt