8 методы типирования.ppt
- Количество слайдов: 41

Методы типирования
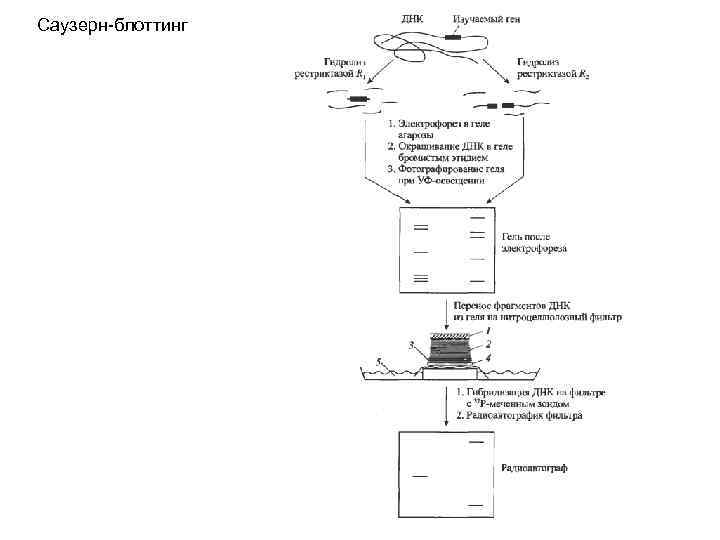
Саузерн-блоттинг
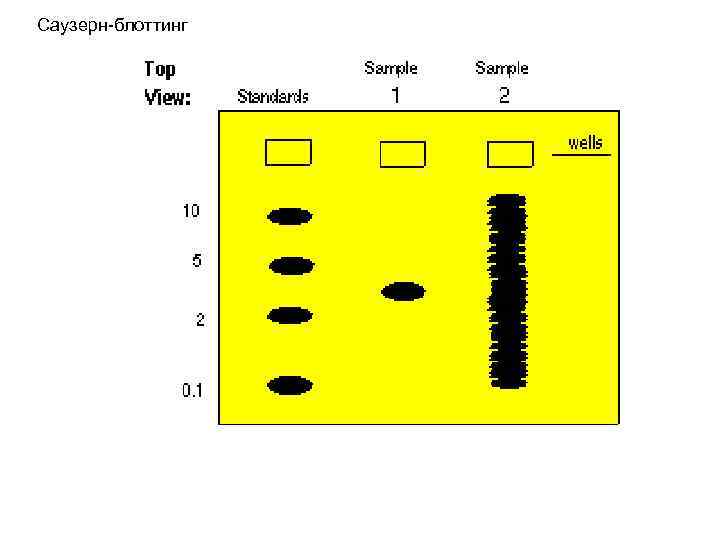
Саузерн-блоттинг
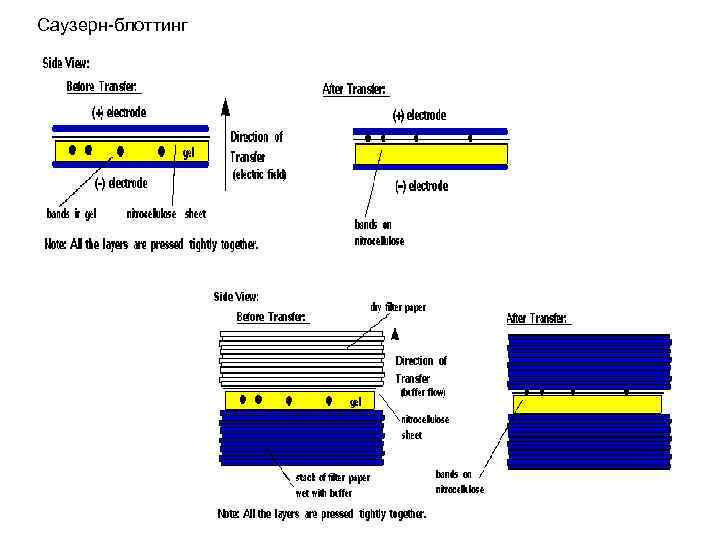
Саузерн-блоттинг
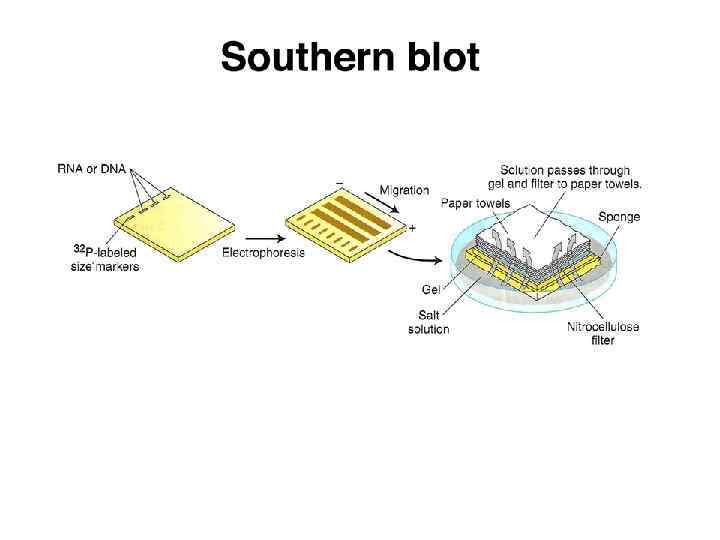
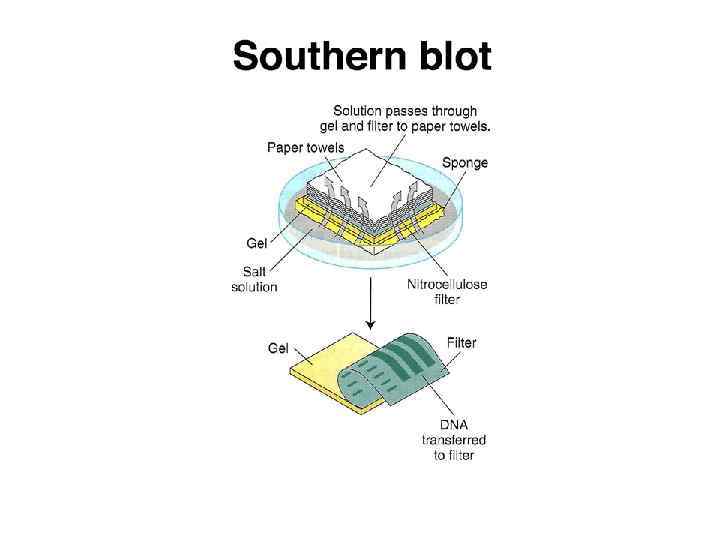
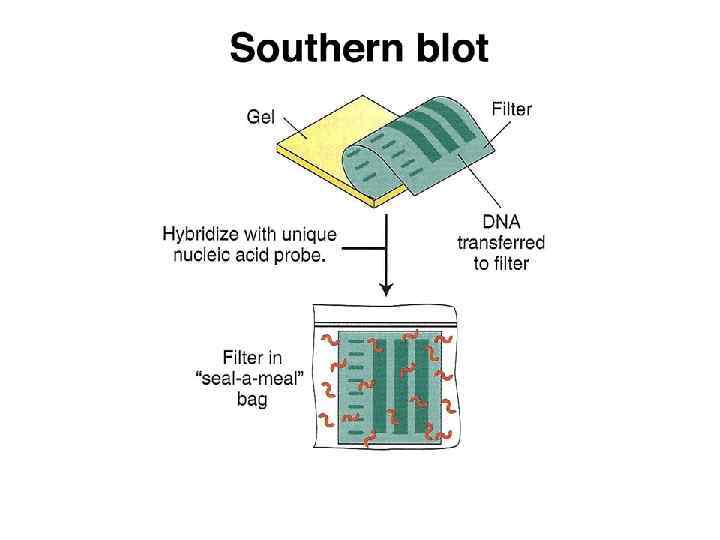
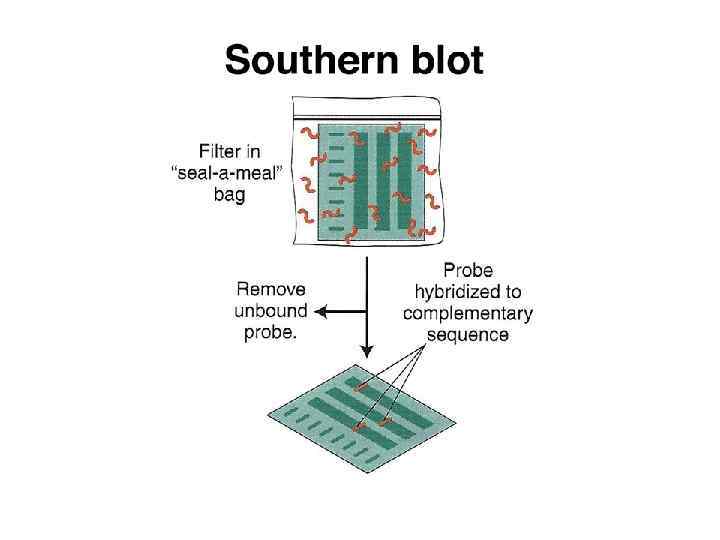
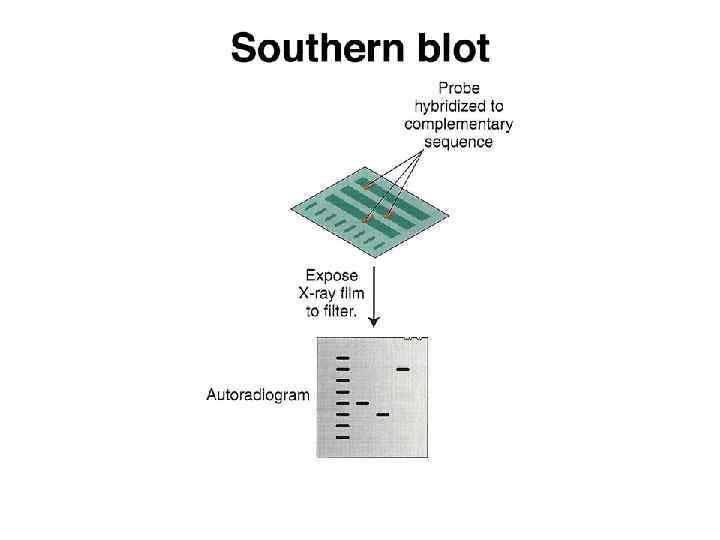
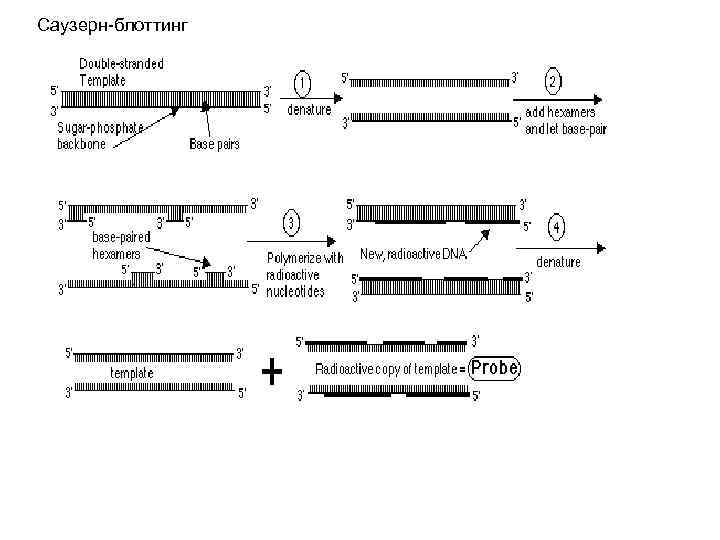
Саузерн-блоттинг
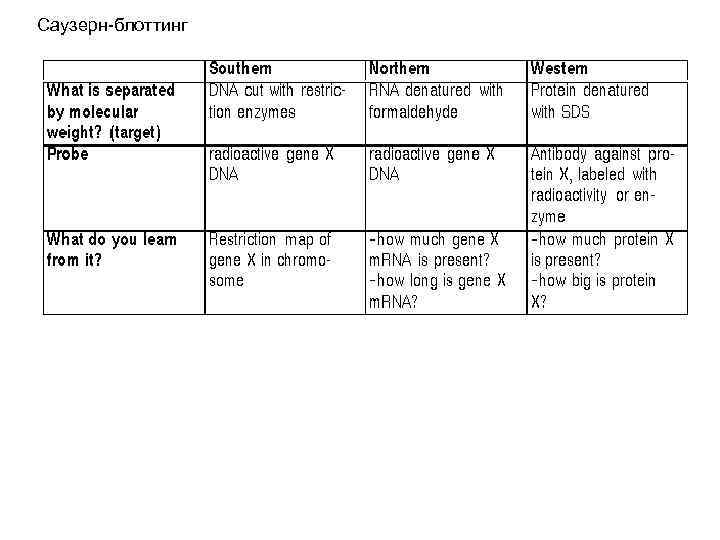
Саузерн-блоттинг
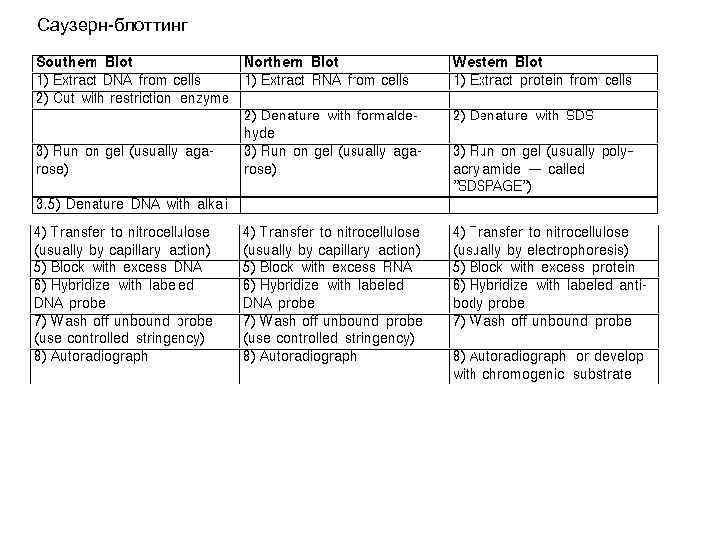
Саузерн-блоттинг
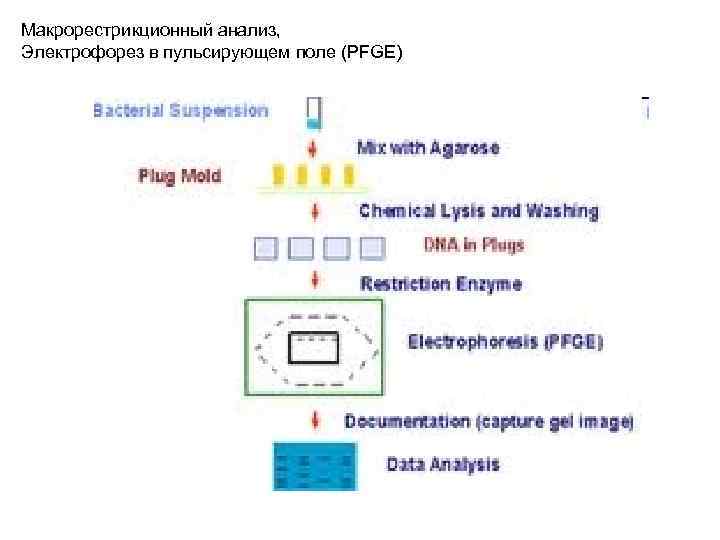
Макрорестрикционный анализ, Электрофорез в пульсирующем поле (PFGE)
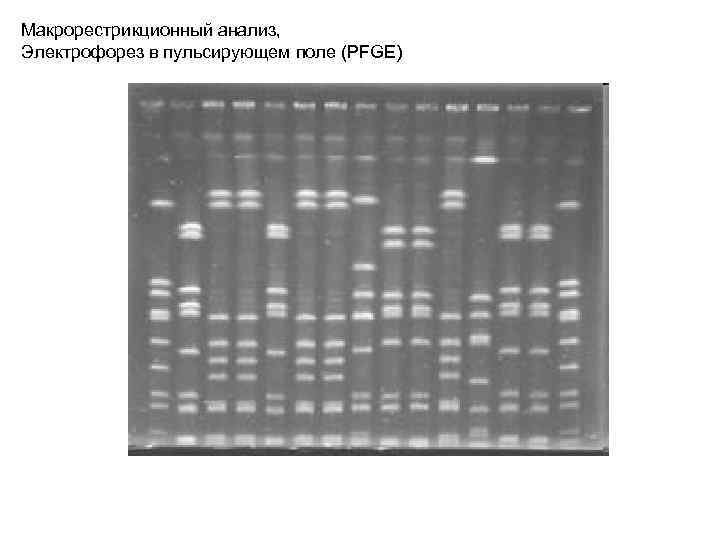
Макрорестрикционный анализ, Электрофорез в пульсирующем поле (PFGE)

Макрорестрикционный анализ, Электрофорез в пульсирующем поле Assignment of Staphylococcus Isolates to Groups by spa Typing, Sma. I Macrorestriction Analysis, and Multilocus Sequence Typing J. Clin. Microbiol. July 2006 vol. 44 no. 7 2533 -2540
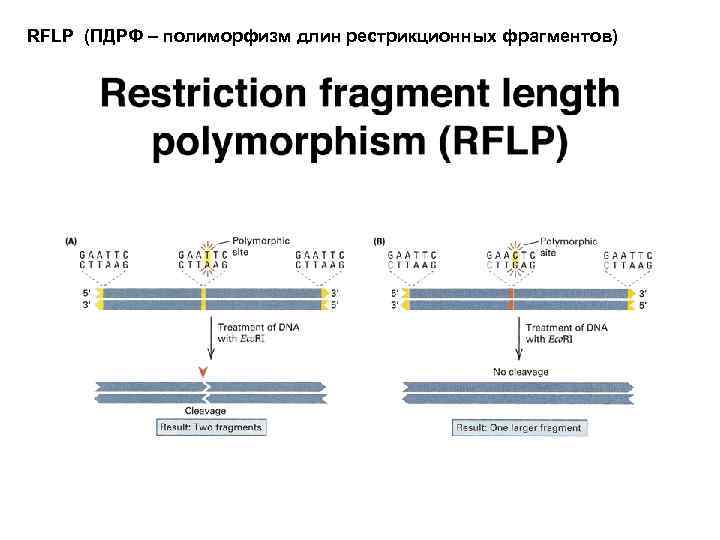
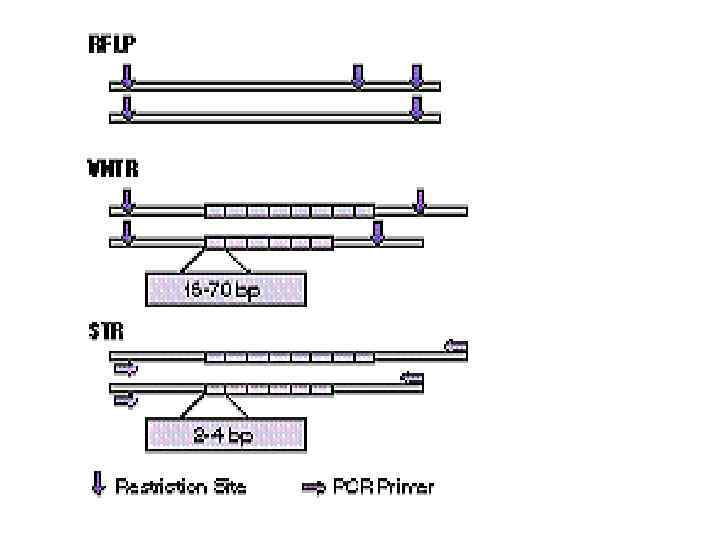
RFLP (ПДРФ – полиморфизм длин рестрикционных фрагментов)
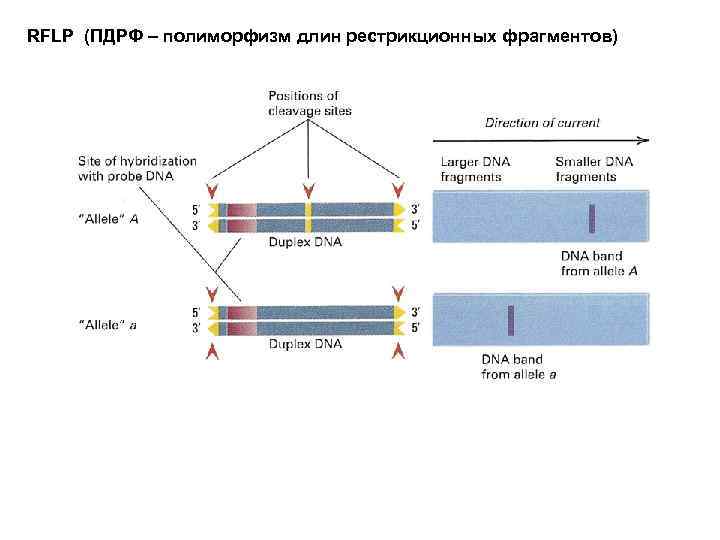
RFLP (ПДРФ – полиморфизм длин рестрикционных фрагментов)
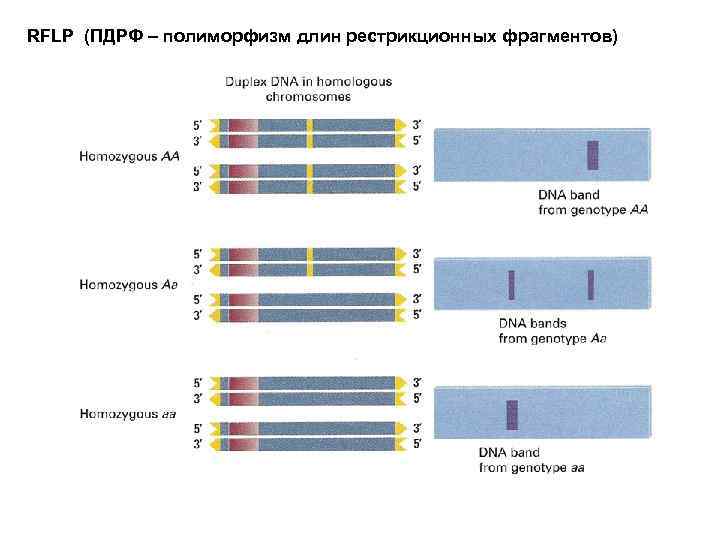
RFLP (ПДРФ – полиморфизм длин рестрикционных фрагментов)
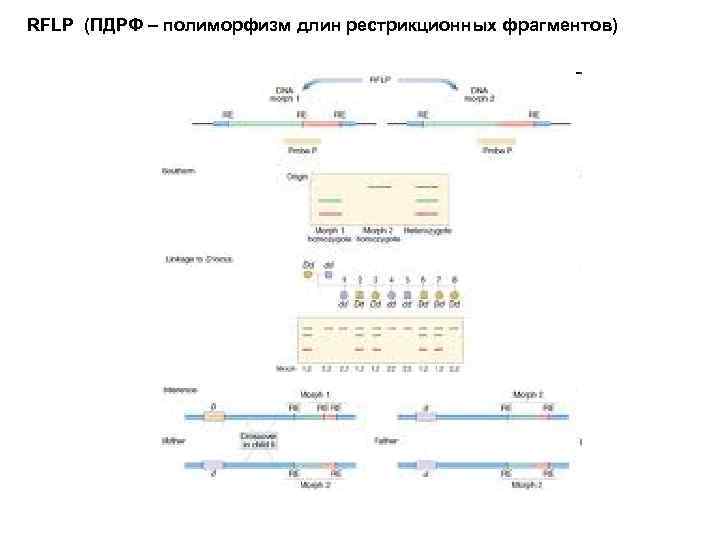
RFLP (ПДРФ – полиморфизм длин рестрикционных фрагментов)

20 Типирование методом локус-специфичной ПЦР-ПДРФ Семейство Xanthomonadaceae Подбор праймеров, специфичных к участкам гена dna. A Примечание: 1. В скобках указан номер нуклеотида в последовательности гена, соответствующий началу и концу представленного участка 2. Праймеры: Xnf 5′-ATGGA(T/A)(G/T)C(T/C)TGG(C/T)CCCG-3′, Тm = 56 ºС Xnr 5′-CGGCA(G/A)GC(A/G)TG(C/T)A(G/A)CAC-3′, Тm = 58 ºС
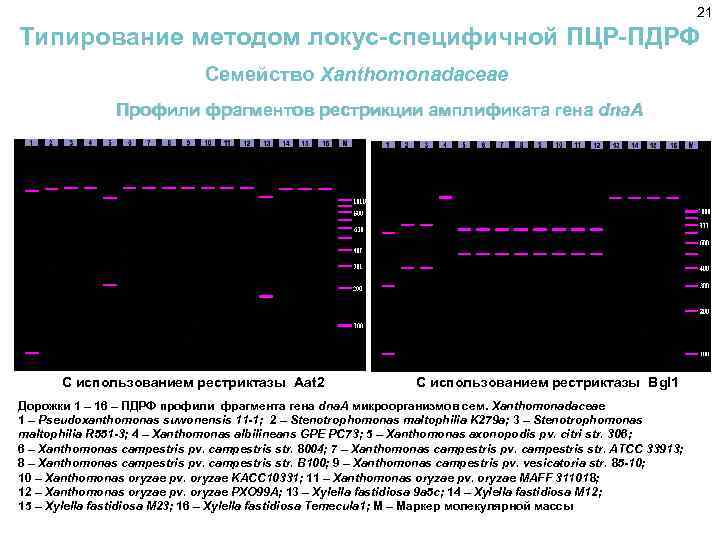
21 Типирование методом локус-специфичной ПЦР-ПДРФ Семейство Xanthomonadaceae Профили фрагментов рестрикции амплификата гена dna. A С использованием рестриктазы Aat 2 С использованием рестриктазы Bgl 1 Дорожки 1 – 16 – ПДРФ профили фрагмента гена dna. A микроорганизмов сем. Xanthomonadaceae 1 – Pseudoxanthomonas suwonensis 11 -1; 2 – Stenotrophomonas maltophilia K 279 a; 3 – Stenotrophomonas maltophilia R 551 -3; 4 – Xanthomonas albilineans GPE PC 73; 5 – Xanthomonas axonopodis pv. citri str. 306; 6 – Xanthomonas campestris pv. campestris str. 8004; 7 – Xanthomonas campestris pv. campestris str. ATCC 33913; 8 – Xanthomonas campestris pv. campestris str. B 100; 9 – Xanthomonas campestris pv. vesicatoria str. 85 -10; 10 – Xanthomonas oryzae pv. oryzae KACC 10331; 11 – Xanthomonas oryzae pv. oryzae MAFF 311018; 12 – Xanthomonas oryzae pv. oryzae PXO 99 A; 13 – Xylella fastidiosa 9 a 5 c; 14 – Xylella fastidiosa M 12; 15 – Xylella fastidiosa M 23; 16 – Xylella fastidiosa Temecula 1; М – Маркер молекулярной массы

22 Типирование методом локус-специфичной ПЦР-ПДРФ Семейство Xanthomonadaceae Профили фрагментов рестрикции амплификата гена dna. A С использованием рестриктазы Sac 1 Дорожки 1 – 16 – ПДРФ профили фрагмента гена dna. A микроорганизмов сем. Xanthomonadaceae 1 – Pseudoxanthomonas suwonensis 11 -1; 2 – Stenotrophomonas maltophilia K 279 a; 3 – Stenotrophomonas maltophilia R 551 -3; 4 – Xanthomonas albilineans GPE PC 73; 5 – Xanthomonas axonopodis pv. citri str. 306; 6 – Xanthomonas campestris pv. campestris str. 8004; 7 – Xanthomonas campestris pv. campestris str. ATCC 33913; 8 – Xanthomonas campestris pv. campestris str. B 100; 9 – Xanthomonas campestris pv. vesicatoria str. 85 -10; 10 – Xanthomonas oryzae pv. oryzae KACC 10331; 11 – Xanthomonas oryzae pv. oryzae MAFF 311018; 12 – Xanthomonas oryzae pv. oryzae PXO 99 A; 13 – Xylella fastidiosa 9 a 5 c; 14 – Xylella fastidiosa M 12; 15 – Xylella fastidiosa M 23; 16 – Xylella fastidiosa Temecula 1; М – Маркер молекулярной массы
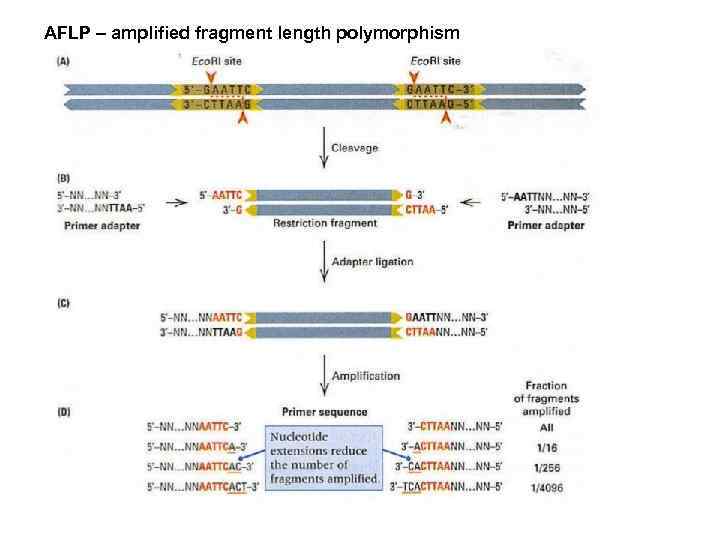
AFLP – amplified fragment length polymorphism
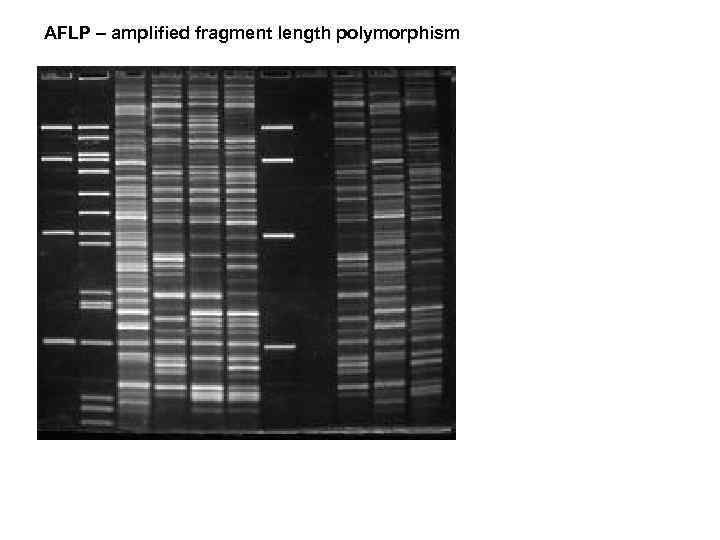
AFLP – amplified fragment length polymorphism
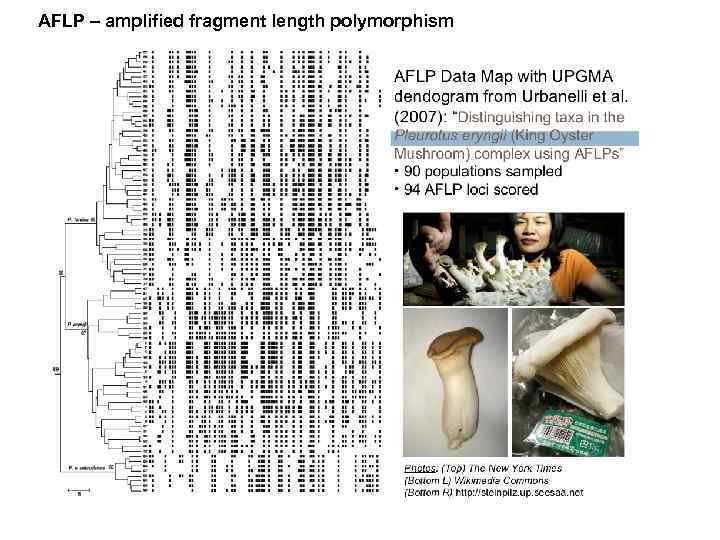
AFLP – amplified fragment length polymorphism
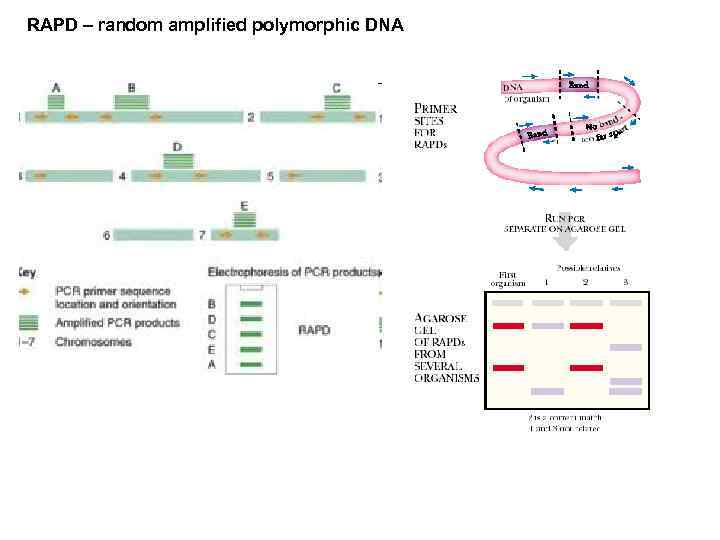
RAPD – random amplified polymorphic DNA
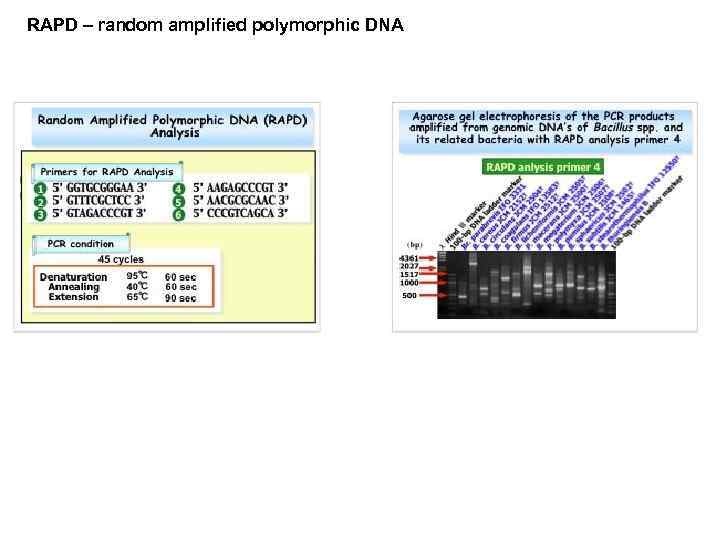
RAPD – random amplified polymorphic DNA
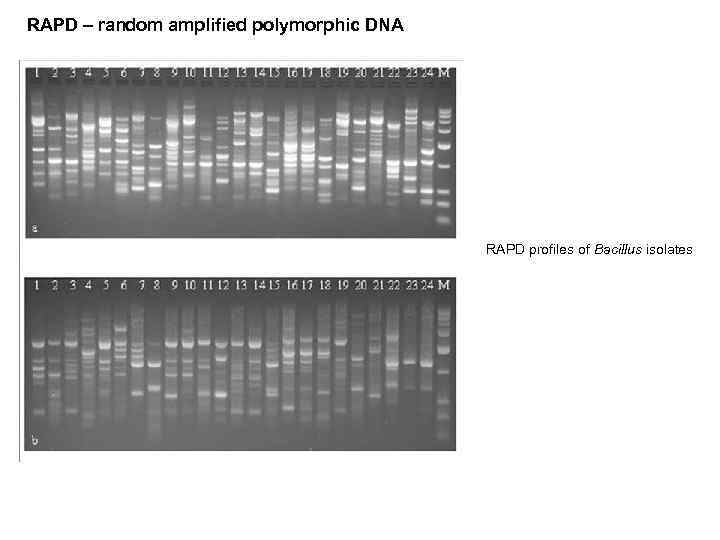
RAPD – random amplified polymorphic DNA RAPD profiles of Bacillus isolates

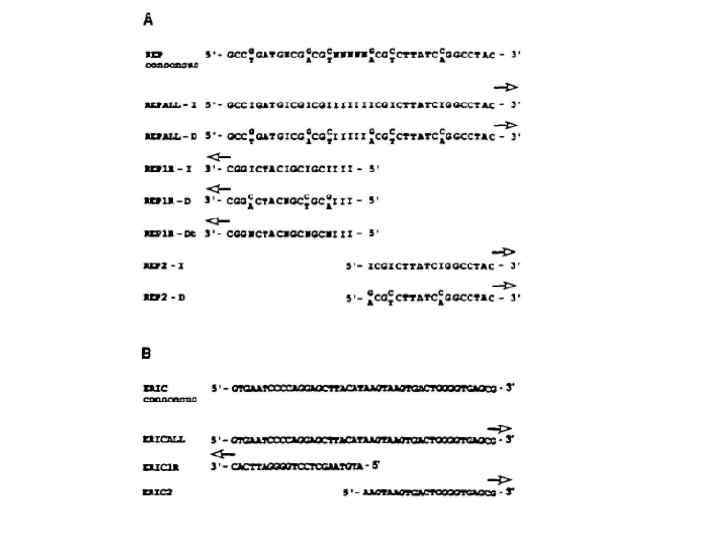
REP-PCR
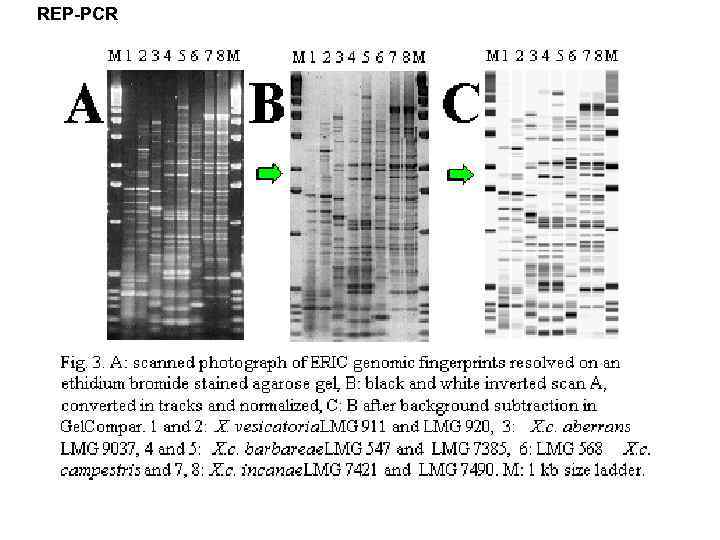
REP-PCR
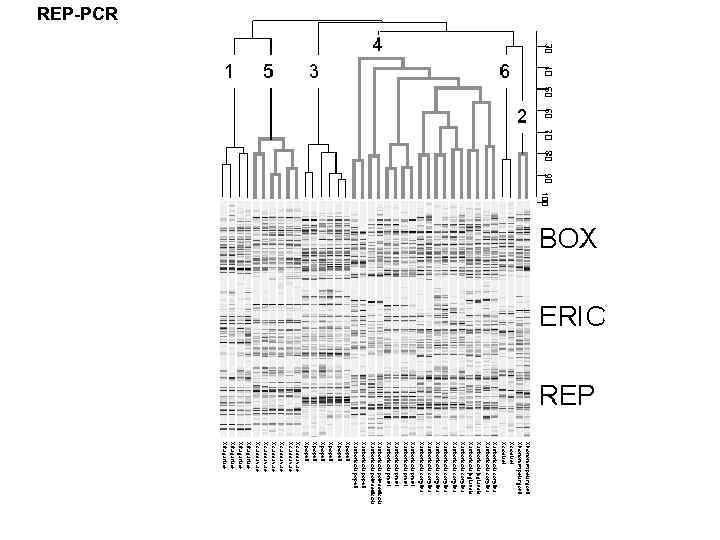
REP-PCR
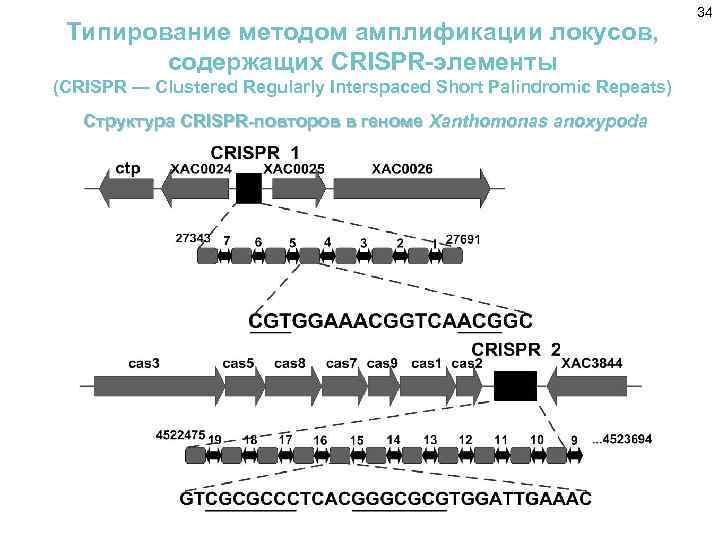
Типирование методом амплификации локусов, содержащих CRISPR-элементы (CRISPR — Clustered Regularly Interspaced Short Palindromic Repeats) Структура CRISPR-повторов в геноме Xanthomonas anoxypoda 34
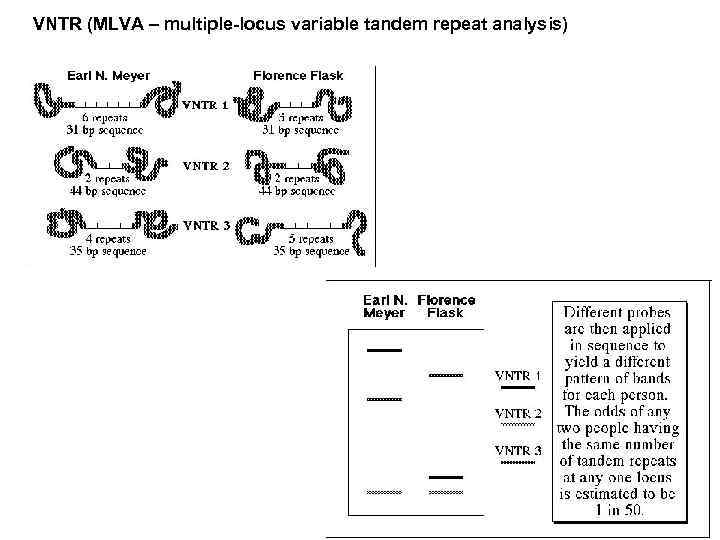
VNTR (MLVA – multiple-locus variable tandem repeat analysis)

Alignment of Lpms 37 repeats and flanking sequences in the three reference strains and three unrelated isolates using Clustal. W. Christine Pourcel et al. J. Clin. Microbiol. 2007; 45: 11901199
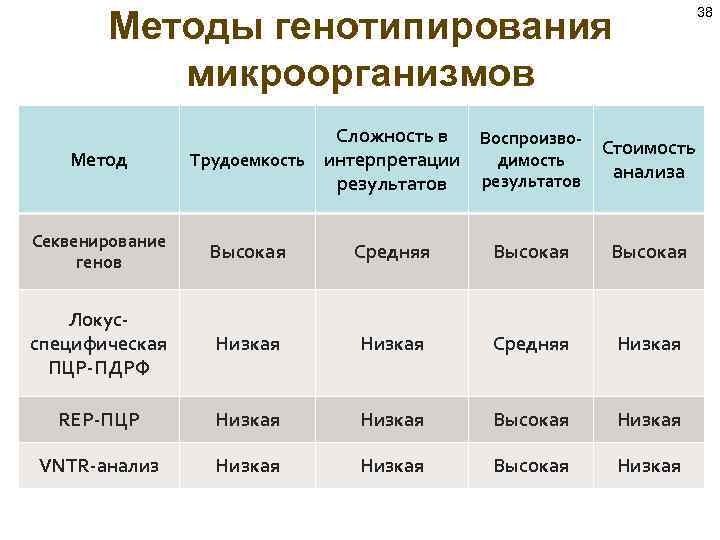
Методы генотипирования микроорганизмов Метод Сложность в Воспроизво. Стоимость Трудоемкость интерпретации димость анализа результатов Секвенирование генов Высокая Средняя Высокая Локусспецифическая ПЦР-ПДРФ Низкая Средняя Низкая REP-ПЦР Низкая Высокая Низкая VNTR-анализ Низкая Высокая Низкая 38
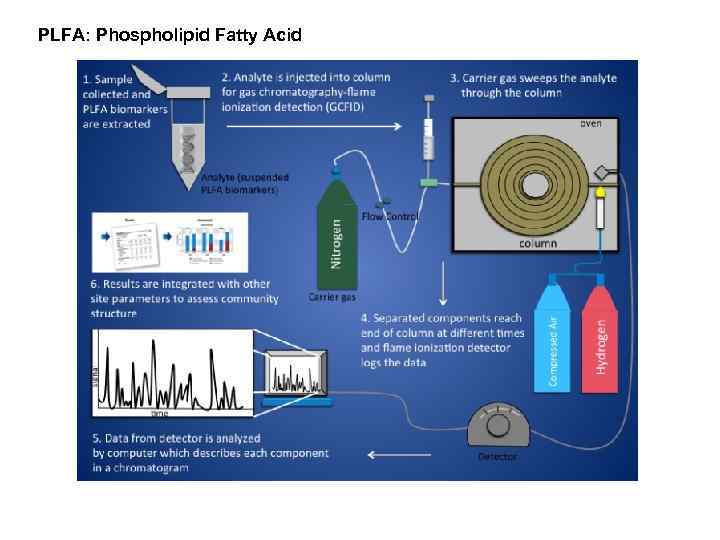
PLFA: Phospholipid Fatty Acid
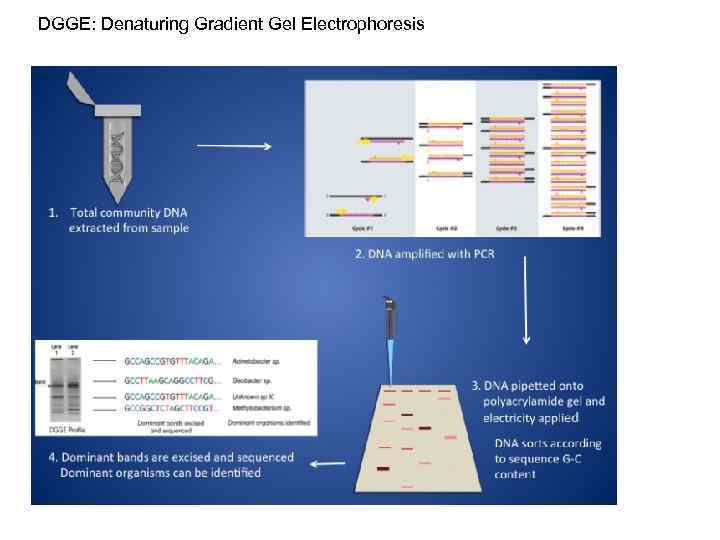
DGGE: Denaturing Gradient Gel Electrophoresis
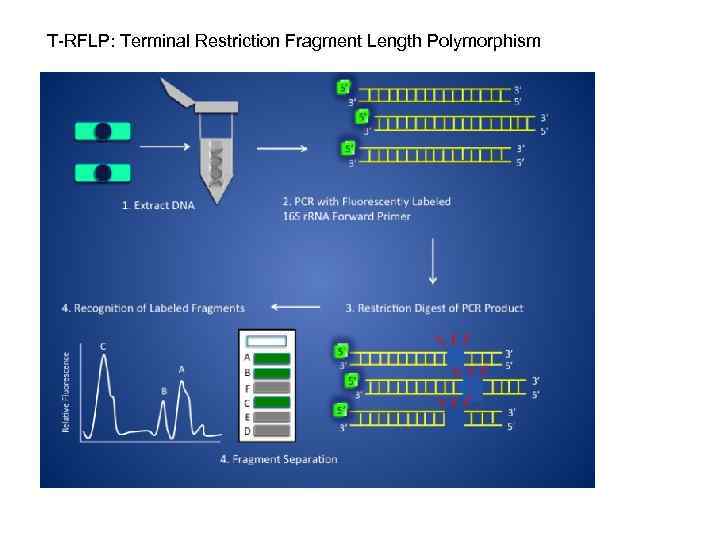
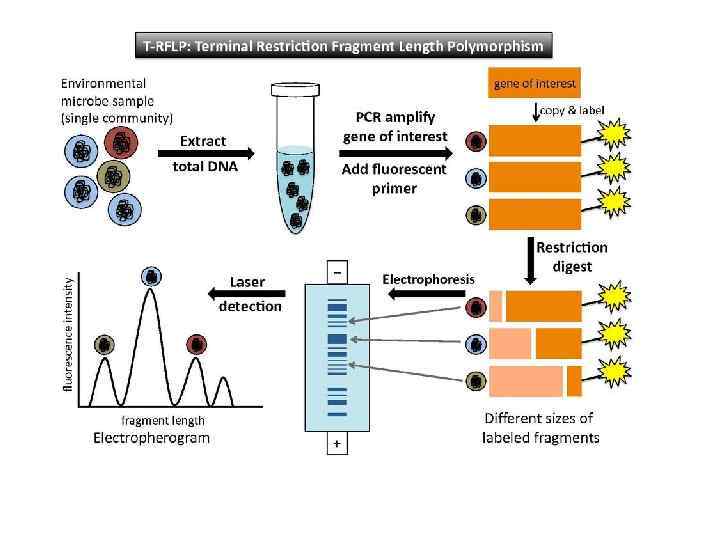
T-RFLP: Terminal Restriction Fragment Length Polymorphism
8 методы типирования.ppt