Б-тех Лекция 3.pptx
- Количество слайдов: 24
 Лекция 12 Статистический анализ последовательностей ДНК Специальный курс лекций «Генетические аспекты биотехнологии животных»
Лекция 12 Статистический анализ последовательностей ДНК Специальный курс лекций «Генетические аспекты биотехнологии животных»
 Рассматриваемые вопросы 1. Причина и скорость возникновения различий в геномах животных 2. Требования к диагностическим и филогенетическим маркерам. Типы маркеров, особенности их анализа и использования 3. Наиболее часто используемые ДНК-маркеры 4. Разрешающая способность маркера. Проблема корректного выбора маркера 5. Генетический полиморфизм, его уровни и типы 6. Основы методов статистического анализа ДНК 7. «Сложности» статистического анализа ДНК. Ортологичные и паралогичные гены. Псевдогены и особенности их анализа. NUMTs
Рассматриваемые вопросы 1. Причина и скорость возникновения различий в геномах животных 2. Требования к диагностическим и филогенетическим маркерам. Типы маркеров, особенности их анализа и использования 3. Наиболее часто используемые ДНК-маркеры 4. Разрешающая способность маркера. Проблема корректного выбора маркера 5. Генетический полиморфизм, его уровни и типы 6. Основы методов статистического анализа ДНК 7. «Сложности» статистического анализа ДНК. Ортологичные и паралогичные гены. Псевдогены и особенности их анализа. NUMTs
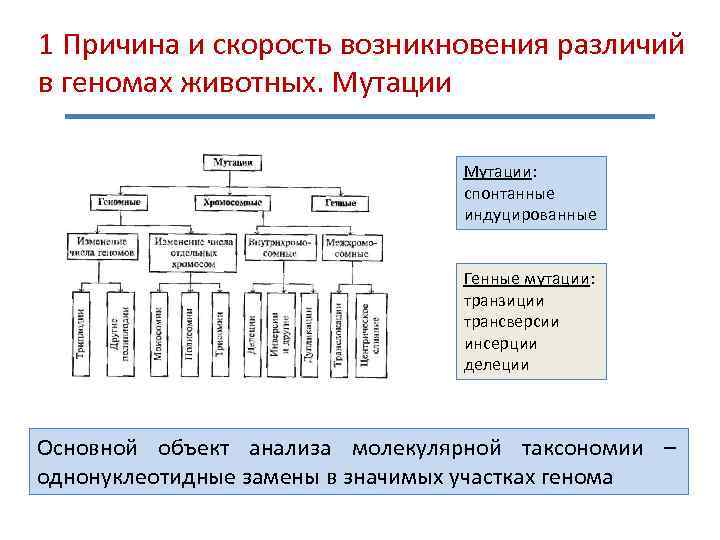 1 Причина и скорость возникновения различий в геномах животных. Мутации: спонтанные индуцированные Генные мутации: транзиции трансверсии инсерции делеции Основной объект анализа молекулярной таксономии – однонуклеотидные замены в значимых участках генома
1 Причина и скорость возникновения различий в геномах животных. Мутации: спонтанные индуцированные Генные мутации: транзиции трансверсии инсерции делеции Основной объект анализа молекулярной таксономии – однонуклеотидные замены в значимых участках генома
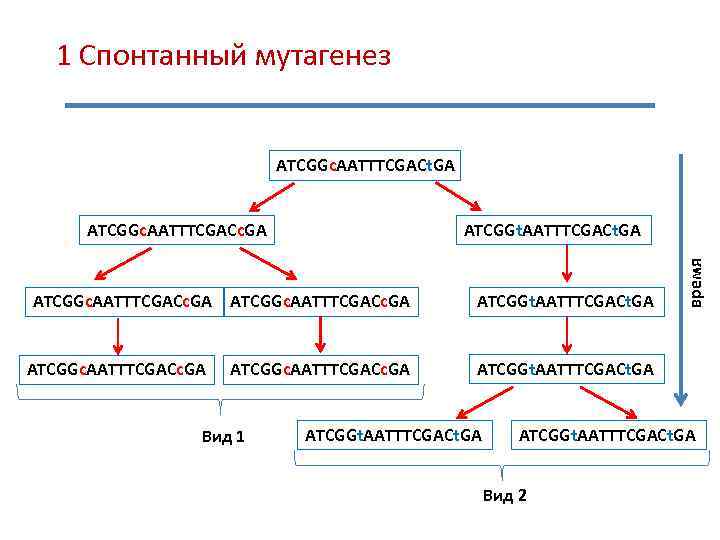 1 Спонтанный мутагенез ATCGGс. AATTTCGACt. GA ATCGGc. AATTTCGACc. GA ATCGGt. AATTTCGACt. GA ATCGGc. AATTTCGACc. GA время ATCGGt. AATTTCGACt. GA ATCGGc. AATTTCGACс. GA ATCGGt. AATTTCGACt. GA Вид 1 ATCGGt. AATTTCGACt. GA Вид 2
1 Спонтанный мутагенез ATCGGс. AATTTCGACt. GA ATCGGc. AATTTCGACc. GA ATCGGt. AATTTCGACt. GA ATCGGc. AATTTCGACc. GA время ATCGGt. AATTTCGACt. GA ATCGGc. AATTTCGACс. GA ATCGGt. AATTTCGACt. GA Вид 1 ATCGGt. AATTTCGACt. GA Вид 2
 2 Требования к молекулярным маркерам Молекулярный маркер (в молекулярной таксономии) – ген, некодирующая область генома или белок, первичная структура которых изменяется со скоростью, соизмеримой со скоростью появления новых таксонов Требования к молекулярным маркерам видовой диагностики: • Наличие в геномах всех особей вида и всех видов анализируемого таксона • Минимальное число копий в геноме • Короткая последовательность (до 1000 букв) • Изменчивость внутри вида меньше, чем различия между видами (не более 1 -2% внутри вида) • Возможность создания универсальных праймеров
2 Требования к молекулярным маркерам Молекулярный маркер (в молекулярной таксономии) – ген, некодирующая область генома или белок, первичная структура которых изменяется со скоростью, соизмеримой со скоростью появления новых таксонов Требования к молекулярным маркерам видовой диагностики: • Наличие в геномах всех особей вида и всех видов анализируемого таксона • Минимальное число копий в геноме • Короткая последовательность (до 1000 букв) • Изменчивость внутри вида меньше, чем различия между видами (не более 1 -2% внутри вида) • Возможность создания универсальных праймеров
 2 Типы ДНК-маркеров Классификация маркеров по происхождению: • Ядерные • Митохондриальные • Пластидные • Цитоплазматические Классификация маркеров по природе: • Белок-кодирующие • РНК-кодирующие • Некодирующие Классификация маркеров по вариабельности: • Консервативные • Полиморфные
2 Типы ДНК-маркеров Классификация маркеров по происхождению: • Ядерные • Митохондриальные • Пластидные • Цитоплазматические Классификация маркеров по природе: • Белок-кодирующие • РНК-кодирующие • Некодирующие Классификация маркеров по вариабельности: • Консервативные • Полиморфные
 2 Ядерные гены как филогенетические маркеры • • Многокопийность Наличие аллелей Интрон-экзонная структура Более низкая (в сравнении с митохондриальными и некодирующими маркерами) скорость эволюции Митохондриальные гены как филогенетические маркеры • Однокопийность • Гаплоидность • Однолинейная материнская передача (в большинстве случаев) • Отсутствие интронов • Высокая скорость эволюции
2 Ядерные гены как филогенетические маркеры • • Многокопийность Наличие аллелей Интрон-экзонная структура Более низкая (в сравнении с митохондриальными и некодирующими маркерами) скорость эволюции Митохондриальные гены как филогенетические маркеры • Однокопийность • Гаплоидность • Однолинейная материнская передача (в большинстве случаев) • Отсутствие интронов • Высокая скорость эволюции
 2 Белок-кодирующие маркеры • Низкая скорость эволюции • Различия в вариабельности нуклеотидных сайтов в зависимости от позиции нуклеотида в кодоне • Значительные различия в вариабельности разных белок -кодирующих маркеров РНК-кодирующие маркеры • Не имеют рамки считывания • Скорость эволюции • ограничена консервативностью вторичной структуры Значительно различаются по степени консервативности и вариабельности Некодирующие маркеры • Высокая изменчивость (в большинстве случаев) • Низкое давление естественного отбора
2 Белок-кодирующие маркеры • Низкая скорость эволюции • Различия в вариабельности нуклеотидных сайтов в зависимости от позиции нуклеотида в кодоне • Значительные различия в вариабельности разных белок -кодирующих маркеров РНК-кодирующие маркеры • Не имеют рамки считывания • Скорость эволюции • ограничена консервативностью вторичной структуры Значительно различаются по степени консервативности и вариабельности Некодирующие маркеры • Высокая изменчивость (в большинстве случаев) • Низкое давление естественного отбора
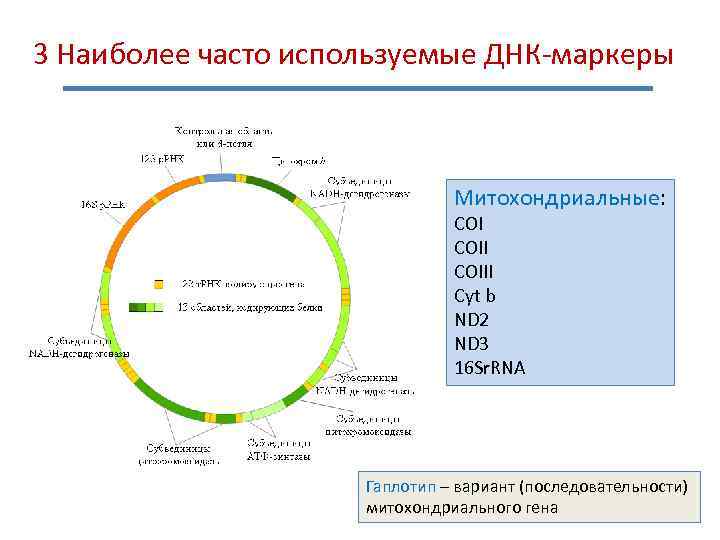 3 Наиболее часто используемые ДНК-маркеры Митохондриальные: COIII Cyt b ND 2 ND 3 16 Sr. RNA Гаплотип – вариант (последовательности) митохондриального гена
3 Наиболее часто используемые ДНК-маркеры Митохондриальные: COIII Cyt b ND 2 ND 3 16 Sr. RNA Гаплотип – вариант (последовательности) митохондриального гена
 3 Наиболее часто используемые ДНК-маркеры
3 Наиболее часто используемые ДНК-маркеры
 3 Наиболее часто используемые ДНК-маркеры Ядерные: EF 1 a ITS 1 ITS 2 r. RNA STR RAPD ITS - Insert Transcribed Spacer STR – Short Tandem Repeats Электрофореграмма результатов STR-анализа
3 Наиболее часто используемые ДНК-маркеры Ядерные: EF 1 a ITS 1 ITS 2 r. RNA STR RAPD ITS - Insert Transcribed Spacer STR – Short Tandem Repeats Электрофореграмма результатов STR-анализа
 4 Разрешающая способность и проблема корректного выбора маркера Разрешающая способность маркера – таксономический уровень, на котором маркер приобретает/теряет филогенетическую или диагностическую информативность Минимум уровня информативности – наименьший таксономический уровень, на котором появляется филогенетический сигнал (обнаруживается полиморфизм маркера) Максимум уровня информативности – наименьший таксономический уровень, на котором происходит вырождение филогенетического сигнала SNP – Single Nucleotide Polymorphism
4 Разрешающая способность и проблема корректного выбора маркера Разрешающая способность маркера – таксономический уровень, на котором маркер приобретает/теряет филогенетическую или диагностическую информативность Минимум уровня информативности – наименьший таксономический уровень, на котором появляется филогенетический сигнал (обнаруживается полиморфизм маркера) Максимум уровня информативности – наименьший таксономический уровень, на котором происходит вырождение филогенетического сигнала SNP – Single Nucleotide Polymorphism
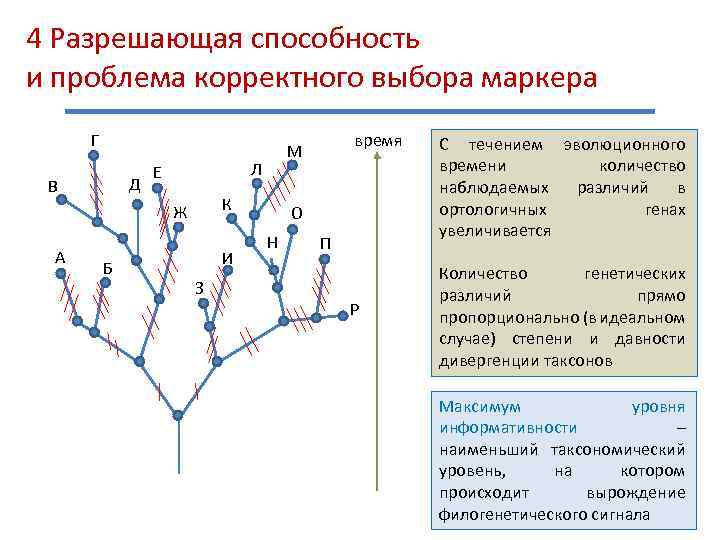 4 Разрешающая способность и проблема корректного выбора маркера Г Д В Л Е К Ж А Б И З время М О Н П Р С течением эволюционного времени количество наблюдаемых различий в ортологичных генах увеличивается Количество генетических различий прямо пропорционально (в идеальном случае) степени и давности дивергенции таксонов Максимум уровня информативности – наименьший таксономический уровень, на котором происходит вырождение филогенетического сигнала
4 Разрешающая способность и проблема корректного выбора маркера Г Д В Л Е К Ж А Б И З время М О Н П Р С течением эволюционного времени количество наблюдаемых различий в ортологичных генах увеличивается Количество генетических различий прямо пропорционально (в идеальном случае) степени и давности дивергенции таксонов Максимум уровня информативности – наименьший таксономический уровень, на котором происходит вырождение филогенетического сигнала
 5 Типы и уровни генетического полиморфизма • • • Внутривидовой полиморфизм Межвидовой полиморфизм Внутриродовой полиморфизм Полиморфизм на уровне семейств -//- • Однонуклеотидный полиморфизм (SNP) • Полиморфизм микросателлитных повторов (полиморфизм длин микросателлитных повторов) • Полиморфизм длин амплифицированных фрагментов (ПДАФ, AFLP) • Полиморфизм длин рестрикционных фрагментов (ПДРФ, RFLP) • RAPD-полиморфизм • Ин-дел полиморфизм • Структурный (интрон-экзонный) полиморфизм • Геномный полиморфизм
5 Типы и уровни генетического полиморфизма • • • Внутривидовой полиморфизм Межвидовой полиморфизм Внутриродовой полиморфизм Полиморфизм на уровне семейств -//- • Однонуклеотидный полиморфизм (SNP) • Полиморфизм микросателлитных повторов (полиморфизм длин микросателлитных повторов) • Полиморфизм длин амплифицированных фрагментов (ПДАФ, AFLP) • Полиморфизм длин рестрикционных фрагментов (ПДРФ, RFLP) • RAPD-полиморфизм • Ин-дел полиморфизм • Структурный (интрон-экзонный) полиморфизм • Геномный полиморфизм
 6 Основы методов статистического анализа ДНК Генетическая дистанция SNP – Single Nucleotide Polymorphism GD=Np/N Генетическая дистанция между двумя последовательностями – доля полиморфных сайтов в последовательностях заданной длины Взвешенная генетическая дистанция между двумя последовательностями – доля полиморфных сайтов в последовательностях заданной длины, с учетом ожидаемой частоты встречаемости каждой нуклеотидной замены
6 Основы методов статистического анализа ДНК Генетическая дистанция SNP – Single Nucleotide Polymorphism GD=Np/N Генетическая дистанция между двумя последовательностями – доля полиморфных сайтов в последовательностях заданной длины Взвешенная генетическая дистанция между двумя последовательностями – доля полиморфных сайтов в последовательностях заданной длины, с учетом ожидаемой частоты встречаемости каждой нуклеотидной замены
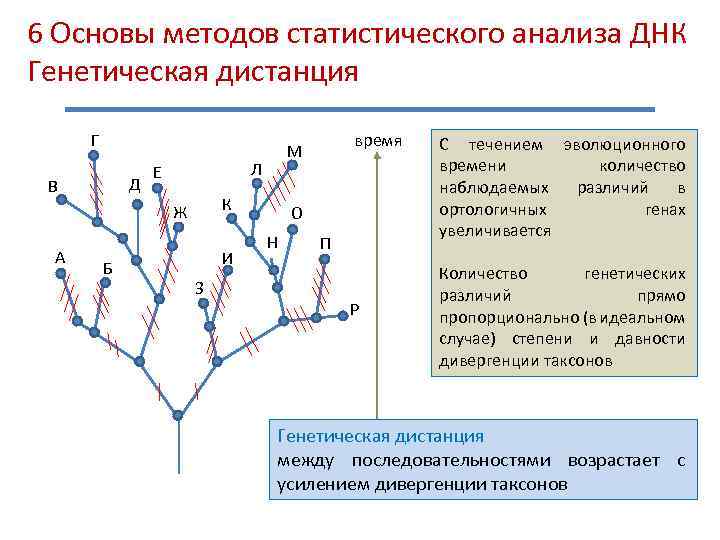 6 Основы методов статистического анализа ДНК Генетическая дистанция Г Д В Л Е К Ж А Б И З время М О Н П Р С течением эволюционного времени количество наблюдаемых различий в ортологичных генах увеличивается Количество генетических различий прямо пропорционально (в идеальном случае) степени и давности дивергенции таксонов Генетическая дистанция между последовательностями возрастает с усилением дивергенции таксонов
6 Основы методов статистического анализа ДНК Генетическая дистанция Г Д В Л Е К Ж А Б И З время М О Н П Р С течением эволюционного времени количество наблюдаемых различий в ортологичных генах увеличивается Количество генетических различий прямо пропорционально (в идеальном случае) степени и давности дивергенции таксонов Генетическая дистанция между последовательностями возрастает с усилением дивергенции таксонов
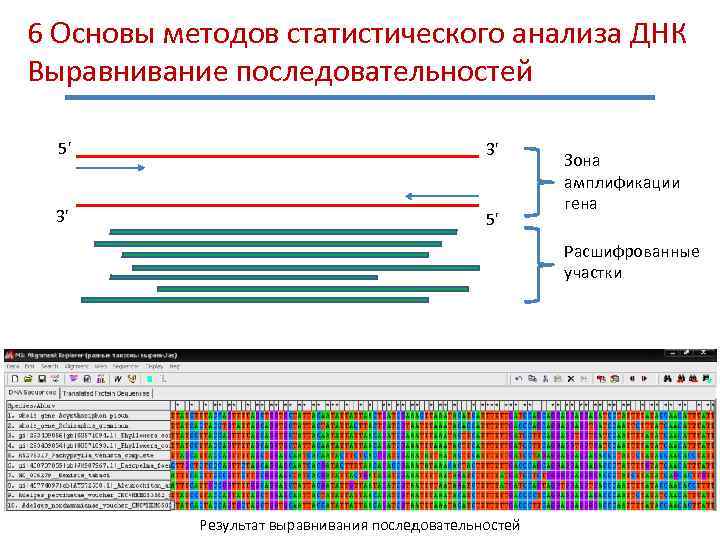 6 Основы методов статистического анализа ДНК Выравнивание последовательностей 5' 3' 3' 5' Зона амплификации гена Расшифрованные участки Результат выравнивания последовательностей
6 Основы методов статистического анализа ДНК Выравнивание последовательностей 5' 3' 3' 5' Зона амплификации гена Расшифрованные участки Результат выравнивания последовательностей
 6 Основы методов статистического анализа ДНК Нуклеотидная / аминокислотная композиция Нуклеотидная/аминокислотная композиция – частота встречаемости конкретных нуклеотидов/аминокислот на протяжении последовательности или в каждом сайте гена/белка (при множественных сравнениях)
6 Основы методов статистического анализа ДНК Нуклеотидная / аминокислотная композиция Нуклеотидная/аминокислотная композиция – частота встречаемости конкретных нуклеотидов/аминокислот на протяжении последовательности или в каждом сайте гена/белка (при множественных сравнениях)
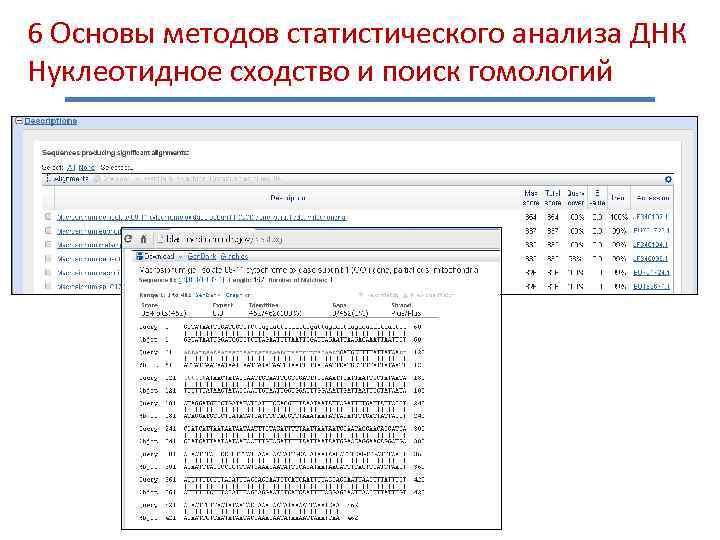 6 Основы методов статистического анализа ДНК Нуклеотидное сходство и поиск гомологий
6 Основы методов статистического анализа ДНК Нуклеотидное сходство и поиск гомологий
 6 Основы методов статистического анализа ДНК Анализ консенсусных последовательностей Индивидуальные последовательности COI Консенсусные последовательности COI
6 Основы методов статистического анализа ДНК Анализ консенсусных последовательностей Индивидуальные последовательности COI Консенсусные последовательности COI
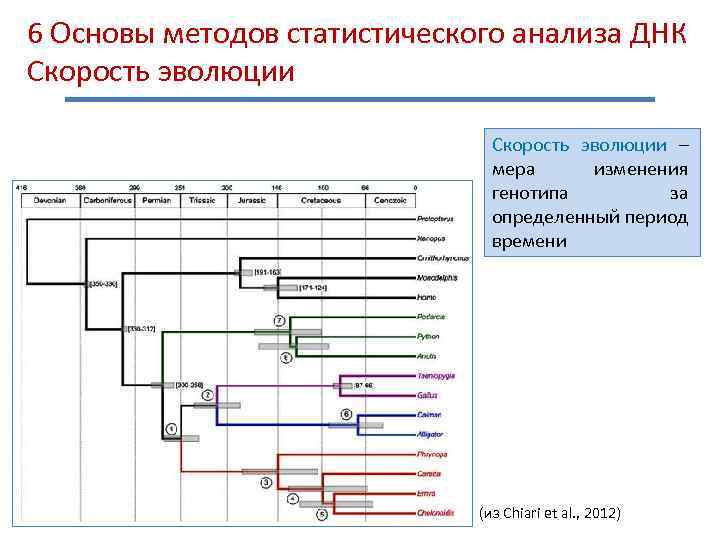 6 Основы методов статистического анализа ДНК Скорость эволюции – мера изменения генотипа за определенный период времени (из Chiari et al. , 2012)
6 Основы методов статистического анализа ДНК Скорость эволюции – мера изменения генотипа за определенный период времени (из Chiari et al. , 2012)
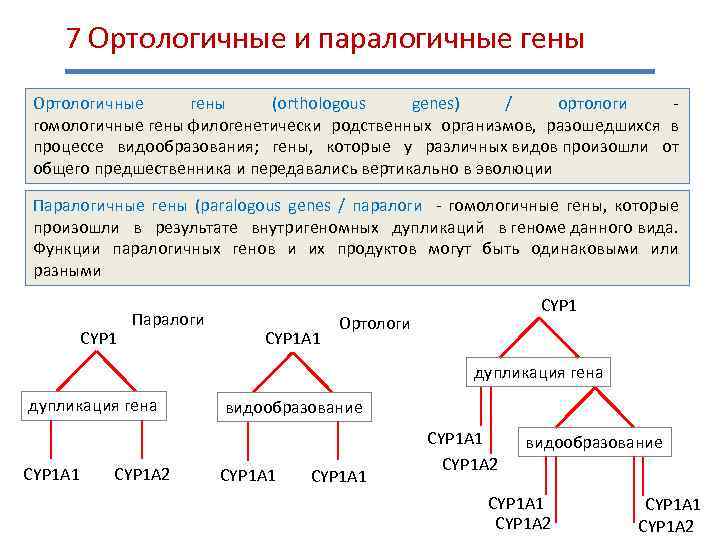 7 Ортологичные и паралогичные гены Ортологичные гены (orthologous genes) / ортологи - гомологичные гены филогенетически родственных организмов, разошедшихся в процессе видообразования; гены, которые у различных видов произошли от общего предшественника и передавались вертикально в эволюции Паралогичные гены (paralogous genes / паралоги - гомологичные гены, которые произошли в результате внутригеномных дупликаций в геноме данного вида. Функции паралогичных генов и их продуктов могут быть одинаковыми или разными CYP 1 Паралоги CYP 1 А 1 CYP 1 Ортологи дупликация гена CYP 1 А 1 CYP 1 А 2 видообразование CYP 1 А 1 CYP 1 А 2
7 Ортологичные и паралогичные гены Ортологичные гены (orthologous genes) / ортологи - гомологичные гены филогенетически родственных организмов, разошедшихся в процессе видообразования; гены, которые у различных видов произошли от общего предшественника и передавались вертикально в эволюции Паралогичные гены (paralogous genes / паралоги - гомологичные гены, которые произошли в результате внутригеномных дупликаций в геноме данного вида. Функции паралогичных генов и их продуктов могут быть одинаковыми или разными CYP 1 Паралоги CYP 1 А 1 CYP 1 Ортологи дупликация гена CYP 1 А 1 CYP 1 А 2 видообразование CYP 1 А 1 CYP 1 А 2
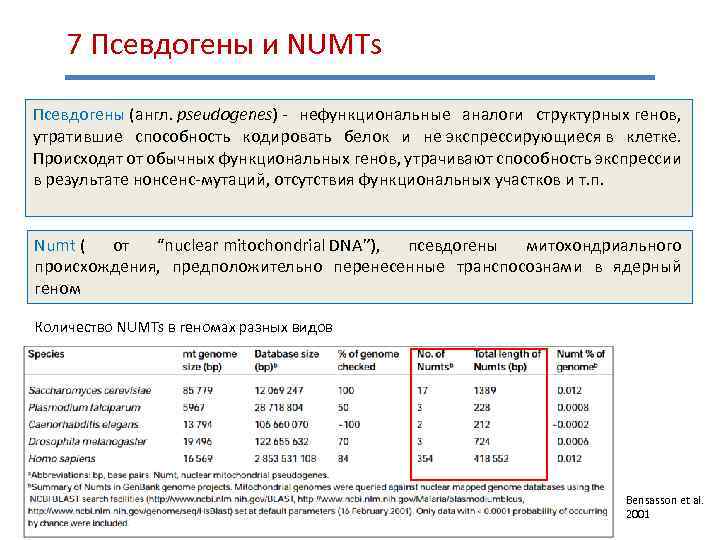 7 Псевдогены и NUMTs Псевдогены (англ. pseudogenes) - нефункциональные аналоги структурных генов, утратившие способность кодировать белок и не экспрессирующиеся в клетке. Происходят от обычных функциональных генов, утрачивают способность экспрессии в результате нонсенс-мутаций, отсутствия функциональных участков и т. п. Numt ( от “nuclear mitochondrial DNA”), псевдогены митохондриального происхождения, предположительно перенесенные транспосознами в ядерный геном Количество NUMTs в геномах разных видов Bensasson et al. 2001
7 Псевдогены и NUMTs Псевдогены (англ. pseudogenes) - нефункциональные аналоги структурных генов, утратившие способность кодировать белок и не экспрессирующиеся в клетке. Происходят от обычных функциональных генов, утрачивают способность экспрессии в результате нонсенс-мутаций, отсутствия функциональных участков и т. п. Numt ( от “nuclear mitochondrial DNA”), псевдогены митохондриального происхождения, предположительно перенесенные транспосознами в ядерный геном Количество NUMTs в геномах разных видов Bensasson et al. 2001
 Спасибо за внимание
Спасибо за внимание


