0ae45e28ff8b3861fb3a8d36de329856.ppt
- Количество слайдов: 21

Компьютерный анализ закономерностей кодирования функциональных сайтов белков в генах эукариот Медведева Ирина Специальность: 03. 01. 09 математическая биология, биоинформатика Научный руководитель: доц. , к. б. н. Иванисенко В. А. ИЦи. Г 2013 1

Функциональный сайт белка – группа аминокислотных остатков, непосредственно участвующая во взаимодействиях белка с лигандами/рецептором или биохимических реакциях, обеспечивающих выполнение его функции. Функциональные сайты обладают свойством компактности в пространственной структуре, т. е. , их аминокислотные остатки сближены в пространстве между собой, но могут быть удаленно распределены по последовательности. Среди различных типов функциональных сайтов можно выделить следующие: • активные центры (посредством которых катализируются химические реакции, включают в себя каталитические сайты и сайты связывания субстрата); • связывающие лиганды (могут связывать либо макромолекулы - белки, ДНК, РНК, - либо небольшие молекулы); • аллостерические (сайты, связывание лигандов с которыми может изменять конформацию белка и, таким образом, регуляторно воздействовать на функцию других удаленных в пространстве сайтов); • регуляторные (могут регулировать ферментативную активность белков с помощью активаторов и ингибиторов). 2
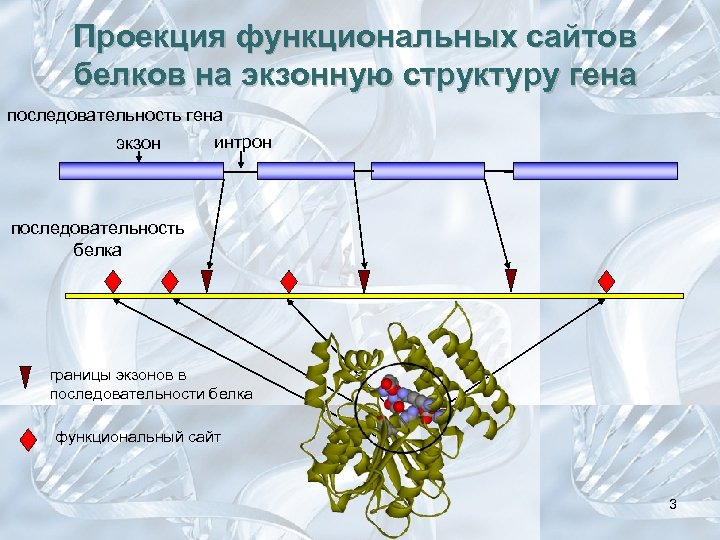
Проекция функциональных сайтов белков на экзонную структуру гена последовательность гена интрон экзон последовательность белка границы экзонов в последовательности белка функциональный сайт 3

Эволюция экзонной структуры • • • Дупликация экзонов Перетасовка экзонов Экзонизация интронов, мобильных элементов Использование домена в качестве эволюционной единицы • Анализ соответствия границ домен-экзон (Kaessmann H. et al. 2002) доменная структура экзонная структура • Анализ соответствия структурных элементов белка с экзонной структурой гена. Исследовалось для отдельных семейств разными авторами: FXYD, митохондриальные порины Для исследованных семейств наблюдается корреляция между экзон-интронными границами и и границами структурных элементов. • Анализ соответствия функциональных элементов белка с экзонной структурой гена. 4
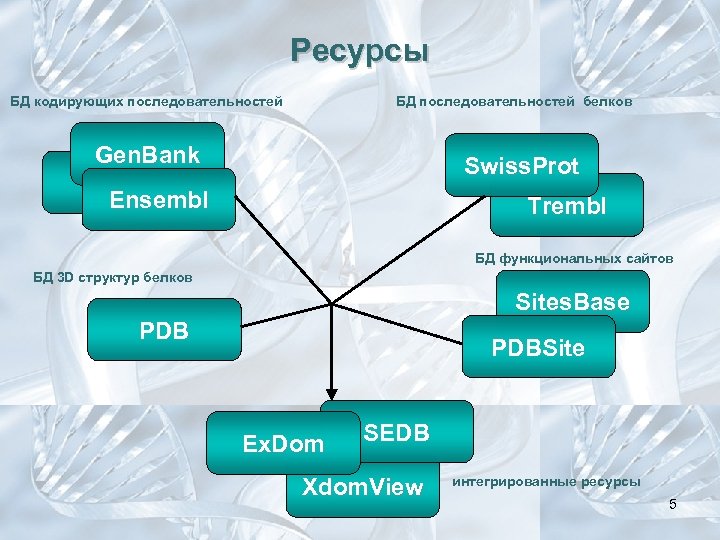
Ресурсы БД кодирующих последовательностей БД последовательностей белков Gen. Bank Swiss. Prot Ensembl Trembl БД функциональных сайтов БД 3 D структур белков Sites. Base PDBSite Ex. Dom SEDB Xdom. View интегрированные ресурсы 5

Цель и задачи исследования Цель: Выявление закономерностей кодирования функциональных сайтов белков с использованием проекций границ экзонов на белковую структуру Ø Разработка компьютерной системы, предназначенной для анализа проекций на аминокислотную последовательность белков экзонной структуры, кодирующих их генов, границ доменов и позиций функциональных сайтов. Создание базы данных, интегрирующей результаты проекции и существующие ресурсы по структурно-функциональной организации белков и генов. Ø Интеграция компьютерной системы с программой BLAST с целью поиска гомологичных экзонов и участков полипептидов, кодируемых одним экзоном; а также программой PDB 3 DScan для осуществления структурного выравнивания анализируемого белка с пространственными структурами фрагментов белков, кодируемых одним экзоном. Ø Анализ закономерностей распределения позиций ДНК, кодирующих функциональные сайты, в экзонной структуре гена Ø Исследование распределения кодонного состава в позициях ДНК, кодирующих функциональные сайты, с учетом информационных генетических сигналов на границах экзонов. 6
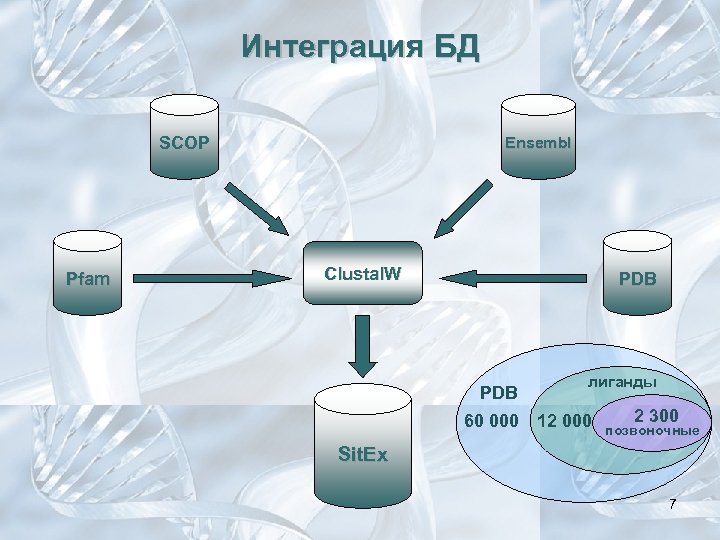
Интеграция БД SCOP Pfam Ensembl Clustal. W PDB 60 000 лиганды 12 000 2 300 позвоночные Sit. Ex 7
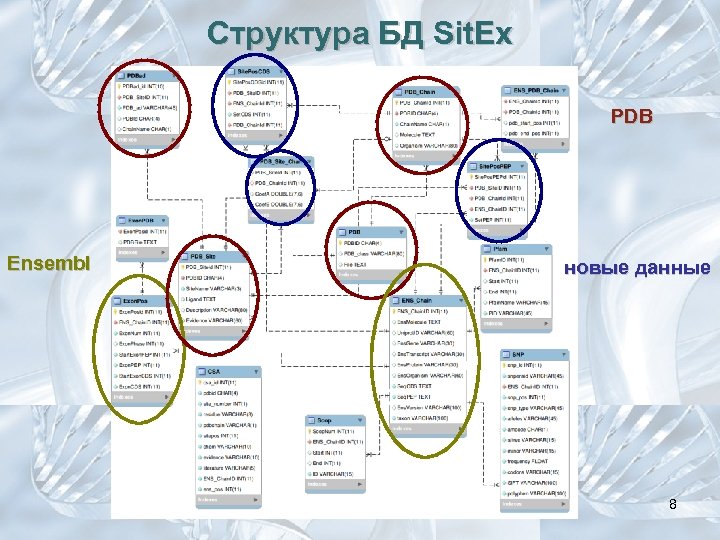
Структура БД Sit. Ex PDB Ensembl новые данные 8
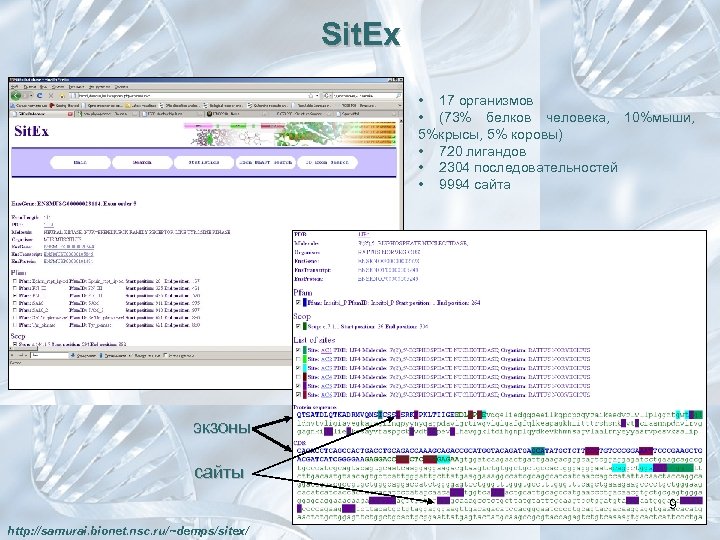
Sit. Ex • 17 организмов • (73% белков человека, 10%мыши, 5%крысы, 5% коровы) • 720 лигандов • 2304 последовательностей • 9994 сайта экзоны сайты 9 http: //samurai. bionet. nsc. ru/~demps/sitex/
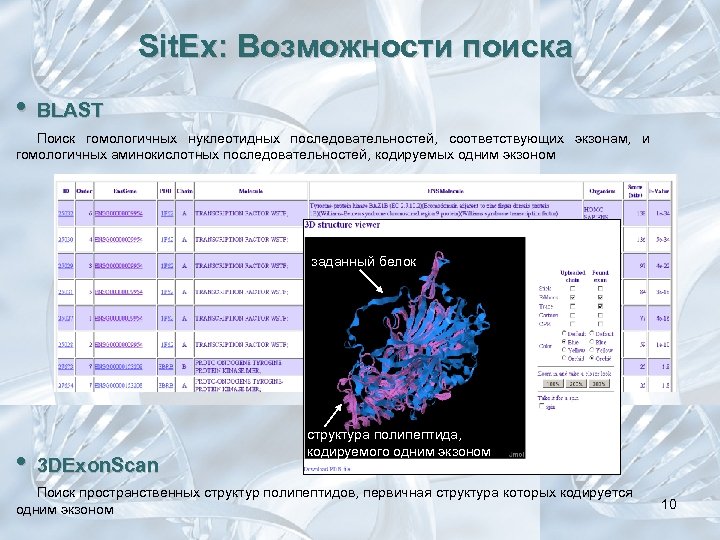
Sit. Ex: Возможности поиска • BLAST Поиск гомологичных нуклеотидных последовательностей, соответствующих экзонам, и гомологичных аминокислотных последовательностей, кодируемых одним экзоном заданный белок • 3 DExon. Scan структура полипептида, кодируемого одним экзоном Поиск пространственных структур полипептидов, первичная структура которых кодируется одним экзоном 10
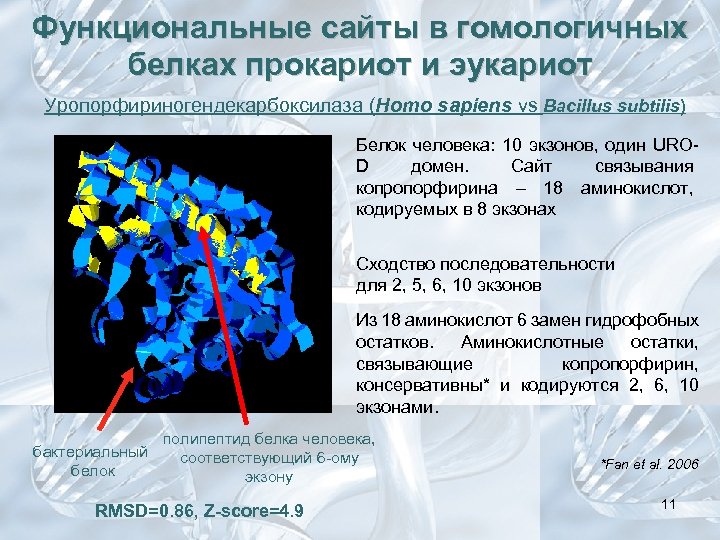
Функциональные сайты в гомологичных белках прокариот и эукариот Уропорфириногендекарбоксилаза (Homo sapiens vs Bacillus subtilis) Белок человека: 10 экзонов, один UROD домен. Сайт связывания копропорфирина – 18 аминокислот, кодируемых в 8 экзонах Сходство последовательности для 2, 5, 6, 10 экзонов Из 18 аминокислот 6 замен гидрофобных остатков. Аминокислотные остатки, связывающие копропорфирин, консервативны* и кодируются 2, 6, 10 экзонами. полипептид белка человека, бактериальный соответствующий 6 -ому белок экзону RMSD=0. 86, Z-score=4. 9 *Fan et al. 2006 11

Исследование экзонной структуры генов, кодирующих белки, которые имеют в составе часто встречающийся домен 2 X 8 B 1 P 0 I 1 AQL 2 H 7 C 3 BL 8 3 BE 8 Экзонная структура участков белка, содержащих домен карбоксилазы типа В. Зеленый цвет экзонов показывает сходство последовательности с первым экзоном домена 2 X 8 B. Сходство по последовательности со вторым экзоном показано оранжевым. Экзоны в составе домена не имеющие гомологии с последовательностью, кодирующей белок со структурой 2 X 8 B, помечены голубым. Красным показаны экзоны, кодирующие полипептиды, обладающие значимым структурным сходством с исходной структурой (Z-score>3. 5). Несмотря на различную кодирующую экзонную структуру домена карбоксилаза типа В в различных белках, сохраняется сходство по последовательности и по структуре. Также домен связывает один общий для всех белков лиганд, при этом сохраняется кодирующая экзонная структура сайта связывания НАД. 12
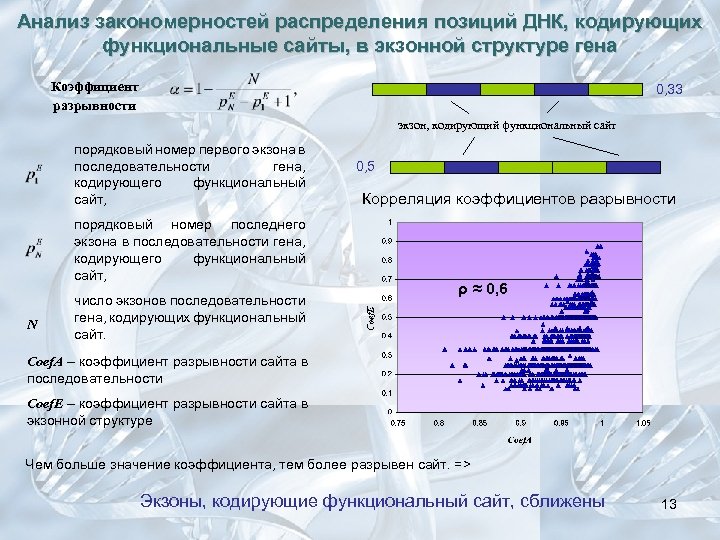
Анализ закономерностей распределения позиций ДНК, кодирующих функциональные сайты, в экзонной структуре гена Коэффициент разрывности 0, 33 экзон, кодирующий функциональный сайт порядковый номер первого экзона в последовательности гена, кодирующего функциональный сайт, порядковый номер последнего экзона в последовательности гена, кодирующего функциональный сайт, N число экзонов последовательности гена, кодирующих функциональный сайт. 0, 5 Корреляция коэффициентов разрывности ρ ≈ 0, 6 Coef. A – коэффициент разрывности сайта в последовательности Coef. E – коэффициент разрывности сайта в экзонной структуре Чем больше значение коэффициента, тем более разрывен сайт. => Экзоны, кодирующие функциональный сайт, сближены 13
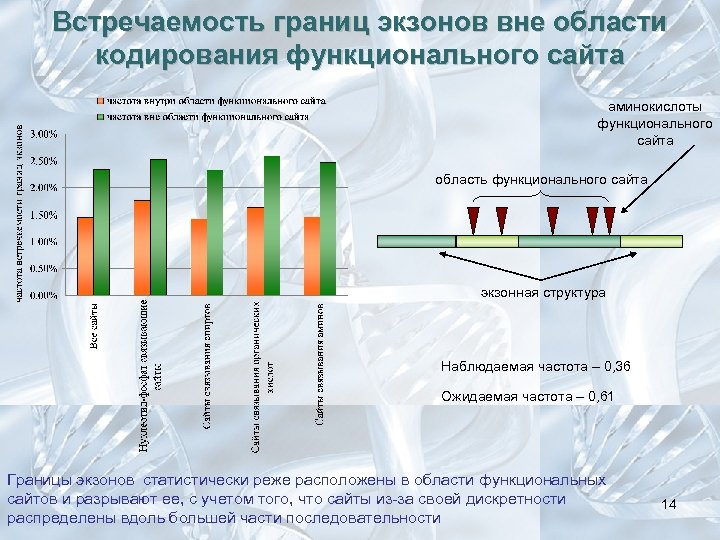
Встречаемость границ экзонов вне области кодирования функционального сайта аминокислоты функционального сайта область функционального сайта экзонная структура Наблюдаемая частота – 0, 36 Ожидаемая частота – 0, 61 Границы экзонов статистически реже расположены в области функциональных сайтов и разрывают ее, с учетом того, что сайты из-за своей дискретности распределены вдоль большей части последовательности 14
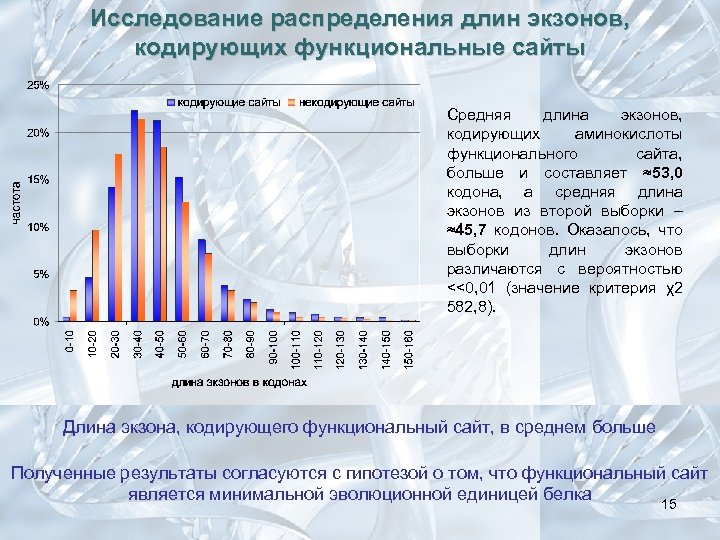
Исследование распределения длин экзонов, кодирующих функциональные сайты Cредняя длина экзонов, кодирующих аминокислоты функционального сайта, больше и составляет ≈53, 0 кодона, а средняя длина экзонов из второй выборки – ≈45, 7 кодонов. Оказалось, что выборки длин экзонов различаются с вероятностью <<0, 01 (значение критерия χ2 582, 8). Длина экзона, кодирующего функциональный сайт, в среднем больше Полученные результаты согласуются с гипотезой о том, что функциональный сайт является минимальной эволюционной единицей белка 15
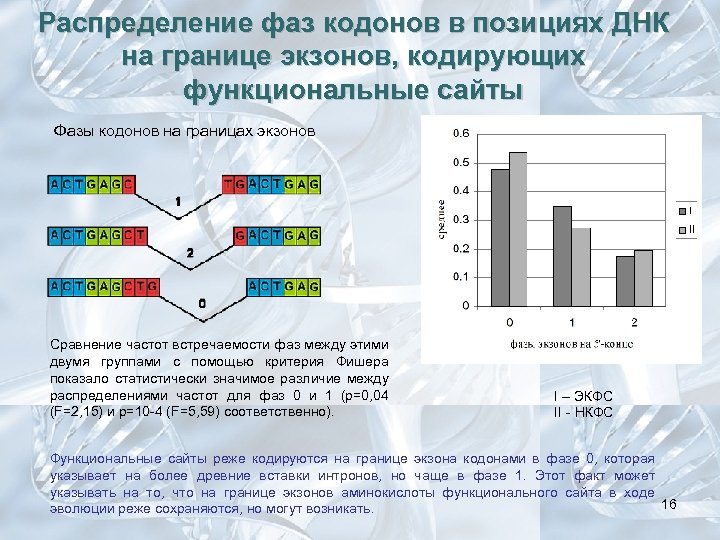
Распределение фаз кодонов в позициях ДНК на границе экзонов, кодирующих функциональные сайты Фазы кодонов на границах экзонов Сравнение частот встречаемости фаз между этими двумя группами с помощью критерия Фишера показало статистически значимое различие между распределениями частот для фаз 0 и 1 (p=0, 04 (F=2, 15) и p=10 -4 (F=5, 59) соответственно). I – ЭКФС II - НКФС Функциональные сайты реже кодируются на границе экзона кодонами в фазе 0, которая указывает на более древние вставки интронов, но чаще в фазе 1. Этот факт может указывать на то, что на границе экзонов аминокислоты функционального сайта в ходе 16 эволюции реже сохраняются, но могут возникать.
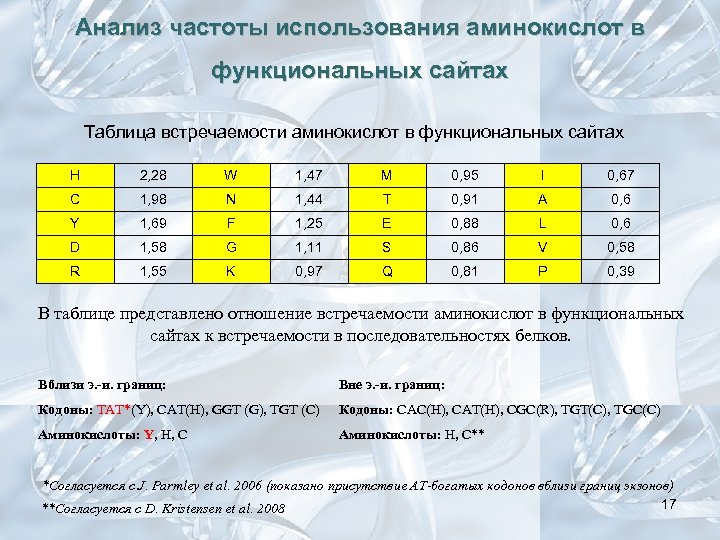
Анализ частоты использования аминокислот в функциональных сайтах Таблица встречаемости аминокислот в функциональных сайтах H 2, 28 W 1, 47 M 0, 95 I 0, 67 C 1, 98 N 1, 44 T 0, 91 A 0, 6 Y 1, 69 F 1, 25 E 0, 88 L 0, 6 D 1, 58 G 1, 11 S 0, 86 V 0, 58 R 1, 55 K 0, 97 Q 0, 81 P 0, 39 В таблице представлено отношение встречаемости аминокислот в функциональных сайтах к встречаемости в последовательностях белков. Вблизи э. -и. границ: Вне э. -и. границ: Кодоны: TAT*(Y), CAT(H), GGT (G), TGT (C) Кодоны: CAC(H), CAT(H), CGC(R), TGT(C), TGC(C) Аминокислоты: Y, H, C Аминокислоты: H, C** *Согласуется с J. Parmley et al. 2006 (показано присутствие AT-богатых кодонов вблизи границ экзонов) 17 **Согласуется с D. Kristensen et al. 2008

Исследование распределения кодонного состава в позициях ДНК, кодирующих функциональные сайты. Различие в использовании кодонов на 5’конце и 3’-конце рассчитывалось с использование критерия χ2 для таблиц 2*J • • Использование кодонов одинаково на всех участках последовательности при кодировании сайтов, но отлично на 5’-конце: A, D, H Более часто используется редко встречающийся кодон при кодировании сайта в последовательности экзона на 5’-конце (менее 5 кодонов): N, P, Q, E, C • Более часто используется редко встречающийся кодон при кодировании сайта в последовательности на 3’-конце (менее 5 кодонов): V • кодоны сайта 5’-конец GCA 17. 36 25. 00 GCC 31. 31 34. 76 GCG 9. 10 7. 93 GCT А послед. 5’конца 20. 66 32. 32 χ2=13. 69, p<0. 01 Показано увеличение кодонов с садержанием аденина и тимина при кодировании аминокислотного остатка в районах границ экзонов: AAT, CCA, CAA, GAA, TGT. Не показано достоверного отличия: F, I, K, L, T, Y, G, R, S 18

Выводы 1) Создана база данных Sit. Ex, содержащая разметку в белковых и геномных последовательностях эукариот границ экзонов, доменов, функциональных сайтов белков и однонуклеотидных полиморфизмов. База данных интегрирована с программами BLAST и 3 DPDBScan для поиска участков в первичных и пространственных структурах белков, имеющих сходство с полипептидами, определяемыми разметкой экзонов в базе данных Sit. Ex. 2) Впервые показано, что функциональные сайты белков имеют тенденцию к кодированию одним или близко расположенными в последовательности гена экзонами. При этом значение показателя разрывности функциональных сайтов по экзонам значимо меньше, чем ожидаемое по случайным причинам. 3) Впервые показано, что длина экзонов, кодирующих функциональные сайты, в среднем значимо превышает длину экзонов, некодирующих функциональные сайты. Показано, что экзоны, кодирующие функциональный сайт обладают большей консервативностью. 19

Выводы 4) Впервые показано, что частота кодонов в позициях ДНК, кодирующих функциональный сайт, в фазе 1 на 5`-конце экзонов статистически значимо превышает частоту кодонов в фазе 1, некодирующих функциональный сайт на 5`-конце экзонов, в то время как частота таких кодонов в фазе 0 значимо меньше, что указывает на более позднее их возникновение. 5) Впервые показано отличие частот использования кодонов в позициях ДНК, кодирующих функциональные сайты, от позиций, не кодирующих функциональные сайты, в районах 5`- и 3`-концов экзонов. В обоих распределениях преобладали неоптимальные кодоны, однако, кодоны, соответствующие функциональным сайтам, характеризовались повышенным AT-составом. Полученные закономерности могут лежать в основе механизма интерференции генетических сигналов, соответствующих сайтам сплайсинга и кодам функциональных сайтов. 20

Список публикаций Статьи в рецензируемых журналах: • Ю. Л. Орлов, А. О. Брагин, И. В. Медведева, К. В. Гунбин, П. С. Деменков, О. В. Вишневский, В. Г. Левицкий, Д. Ю. Ощепков, Н. Л. Подколодный, Д. А. Афонников, И. Гроссе, Н. А. Колчанов. (2012) ICGenomics: программный комплекс анализа символьных последовательностей геномики. Вавиловский журнал генетики и селекции. Том 16, 4/1, 732 -741. • Irina Medvedeva, Pavel Demenkov, Nikolay Kolchanov, Vladimir Ivanisenko. (2012). Sit. Ex: a computer system for analysis of projections of protein functional sites on eukaryotic genes. Nucleic Acids Res. Database issue, pp. D 278 -83. • Медведева И. В. . , Деменков П. С. , Иванисенко В. А. (2009). Анализ распределения аденозин-фосфат связывающих сайтов белков на экзонной структуре гена. Информационный Вестник ВОГи. С, Том 13, № 1, стр. 122 -127. Свидетельства: • Медведева И. В. . , Деменков П. С. , Иванисенко В. А. (2013) Свидетельство о государственной регистрации базы данных № 2013621254. Позиции аминокислот функциональных сайтов белков в экзонной структуре кодирующих генов (Сайт. Экс)/Protein functional sites positions in exon structure of the coding genes (Sit. Ex). Тезисы конференций: • Medvedeva I. V. , Demenkov P. S. , Ivanisenko V. A. Influences of protein functional site encoding features on protein evolution in Eukaryota. // Abstracts of the Eighth International Conference on Bioinformatics of Genome Regulation and Structure (BGRS'2012), Novosibirsk, Russia, June 25 - 29, 2012, p. 209. • Afonnikov D. A. , Ivanisenko V. A. , Ignatieva E. V. , Medvedeva I. V. , Demenkov P. S. , Ivanisenko T. V. , Shah A. R. , Ramachandran S. Analysis of sequence features specifying the adhesion ability of influenza A virus neuraminidase and hemagglutinin. // Abstracts of the Eighth International Conference on Bioinformatics of Genome Regulation and Structure (BGRS'2012), Novosibirsk, Russia, June 25 - 29, 2012, p. 27. • Medvedeva I. V. , Demenkov P. S. , Ivanisenko V. A. Computer system Sit. Ex for analyzing protein functional sites in eukaryotic gene structure. // Program&Abstracts. The young scientists school "Bioinformatics and System biology", Novosibirsk, Russia, June 28 - 29, 2010, p. 27. • Medvedeva I. V. , Demenkov P. S. , Ivanisenko V. A. Computer system Sit. Ex for analyzing protein functional sites in eukaryotic gene structure. // Abstracts of the Seventh International Conference on Bioinformatics of Genome Regulation and Structure (BGRS'2010), Novosibirsk, Russia, June 20 - 27, 2010, p. 182. • Medvedeva I. V. , Ivanisenko V. A. Protein functional site projection on exon structure of gene. // Abstracts of the Sixth International Conference on Bioinformatics of Genome Regulation and Structure (BGRS'2008), Novosibirsk, Russia, June 22 - 28, 2008, p. 159. • Medvedeva I. V. , Demenkov P. S. , Ivanisenko V. A. (2007) Analysis of protein functional site distribution on gene structure. Proceedings of the 2007 international conference on bioinformatics and computational biology. Vol. 2, pp. 45221 455.
0ae45e28ff8b3861fb3a8d36de329856.ppt