2d0481f7170a0e20602dc126702727f0.ppt
- Количество слайдов: 30
 Epigenetika - metylace DNA
Epigenetika - metylace DNA
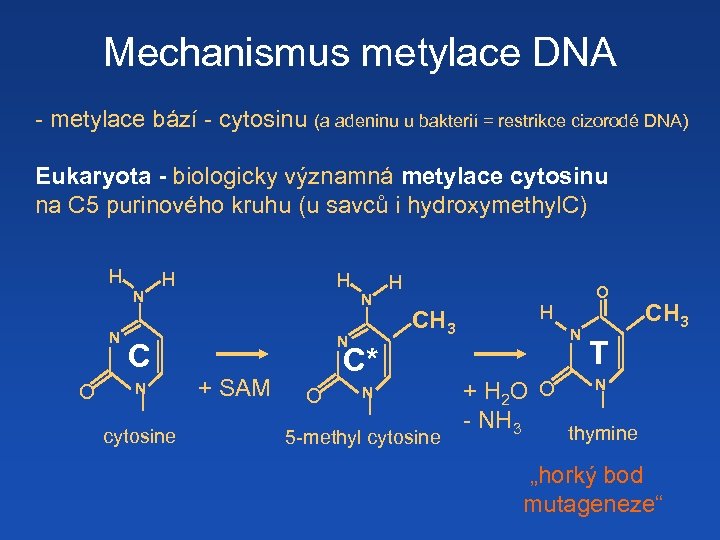 Mechanismus metylace DNA - metylace bází - cytosinu (a adeninu u bakterií = restrikce cizorodé DNA) Eukaryota - biologicky významná metylace cytosinu na C 5 purinového kruhu (u savců i hydroxymethyl. C) H N N O H H N N C N cytosine + SAM H CH 3 C* O N 5 -methyl cytosine O H N + H 2 O O - NH 3 CH 3 T N thymine „horký bod mutageneze“
Mechanismus metylace DNA - metylace bází - cytosinu (a adeninu u bakterií = restrikce cizorodé DNA) Eukaryota - biologicky významná metylace cytosinu na C 5 purinového kruhu (u savců i hydroxymethyl. C) H N N O H H N N C N cytosine + SAM H CH 3 C* O N 5 -methyl cytosine O H N + H 2 O O - NH 3 CH 3 T N thymine „horký bod mutageneze“
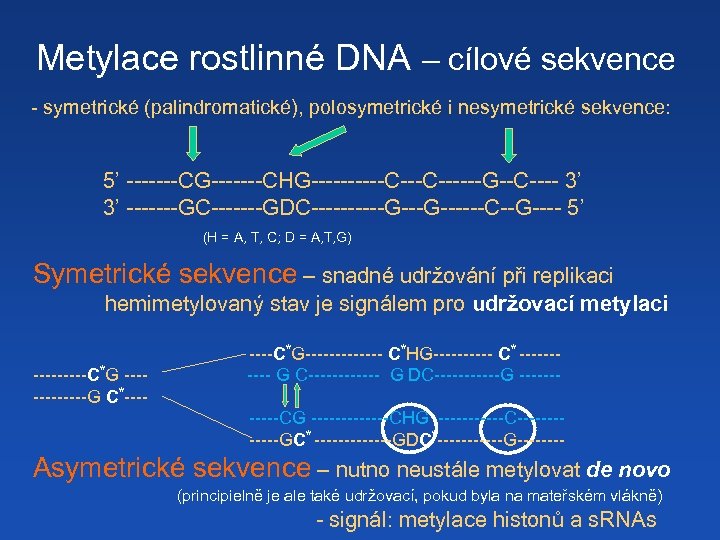 Metylace rostlinné DNA – cílové sekvence - symetrické (palindromatické), polosymetrické i nesymetrické sekvence: 5’ -------CG-------CHG-----C------G--C---- 3’ 3’ -------GC-------GDC-----G------C--G---- 5’ (H = A, T, C; D = A, T, G) Symetrické sekvence – snadné udržování při replikaci hemimetylovaný stav je signálem pro udržovací metylaci -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG -------CHG ------C------GC* -------GDC*------G---- Asymetrické sekvence – nutno neustále metylovat de novo (principielně je ale také udržovací, pokud byla na mateřském vlákně) - signál: metylace histonů a s. RNAs
Metylace rostlinné DNA – cílové sekvence - symetrické (palindromatické), polosymetrické i nesymetrické sekvence: 5’ -------CG-------CHG-----C------G--C---- 3’ 3’ -------GC-------GDC-----G------C--G---- 5’ (H = A, T, C; D = A, T, G) Symetrické sekvence – snadné udržování při replikaci hemimetylovaný stav je signálem pro udržovací metylaci -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG -------CHG ------C------GC* -------GDC*------G---- Asymetrické sekvence – nutno neustále metylovat de novo (principielně je ale také udržovací, pokud byla na mateřském vlákně) - signál: metylace histonů a s. RNAs
 Metylace DNA u Eukaryot nemetylovaná DNA: kvasinka Saccharomyces cerevisiae, octomilka Drosophila (málo), kroužkovci, hlístice Caenorhabditis savci: 3 -8 % cytosinových zbytků, CG sekvence (u embryonálních kmenových buněk i v non-CG kontextu) - nízký výskyt CG v repetitivních heterochromatinových oblastech (mutageneze metyl. C) rostliny: 25 -30 % cytosinových zbytků (~ velikosti genomu) - především v repetitivních heterochromatinových oblastech (pravidelný výskyt nemetylovaných míst – SAR, MAR) - u větších genomů (obiloviny) ostrovy transkripčně aktivní DNA s nižším obsahem met. C - met. C (CG) je ale i v kódujících sekvencích exprimovaných genů!!! (savčích i rostlinných)
Metylace DNA u Eukaryot nemetylovaná DNA: kvasinka Saccharomyces cerevisiae, octomilka Drosophila (málo), kroužkovci, hlístice Caenorhabditis savci: 3 -8 % cytosinových zbytků, CG sekvence (u embryonálních kmenových buněk i v non-CG kontextu) - nízký výskyt CG v repetitivních heterochromatinových oblastech (mutageneze metyl. C) rostliny: 25 -30 % cytosinových zbytků (~ velikosti genomu) - především v repetitivních heterochromatinových oblastech (pravidelný výskyt nemetylovaných míst – SAR, MAR) - u větších genomů (obiloviny) ostrovy transkripčně aktivní DNA s nižším obsahem met. C - met. C (CG) je ale i v kódujících sekvencích exprimovaných genů!!! (savčích i rostlinných)
 Úloha a projevy metylace DNA - dědičná (mitoticky a částečně i meioticky) modulace transkripce - genové exprese - obranný mechanismus vůči invazní DNA (transpozóny) - regulace genové exprese - ontogeneze, diferenciace a buněčná paměť, reakce na stres (i bez metylace DNA) - parentální imprinting - modulace struktury chromatinu (příčina i následek) - časování DNA replikace - regulace homologní rekombinace (meiosa) - nástroj evoluce - genomů polyploidních rostlin (rozsáhlé změny metylace) - nových genů (mutageneze pseudogenů)
Úloha a projevy metylace DNA - dědičná (mitoticky a částečně i meioticky) modulace transkripce - genové exprese - obranný mechanismus vůči invazní DNA (transpozóny) - regulace genové exprese - ontogeneze, diferenciace a buněčná paměť, reakce na stres (i bez metylace DNA) - parentální imprinting - modulace struktury chromatinu (příčina i následek) - časování DNA replikace - regulace homologní rekombinace (meiosa) - nástroj evoluce - genomů polyploidních rostlin (rozsáhlé změny metylace) - nových genů (mutageneze pseudogenů)
 Cílová místa metylace DNA v chromatinové struktuře/sekvenci Silnější metylace exonů - souvislost s preferenčním výskytem nukleozómů na exonech (spoludefinování hranic exonů) - současně zvýšený výskyt polymerázy II - zbrždění nukleozómem Preferenční výskyt met. C na vnější straně nukleozómů - souvisí s preferenčním výskytem Cp. G na vnější straně (stérické důvody) - lépe přístupný pro metyltransferázy
Cílová místa metylace DNA v chromatinové struktuře/sekvenci Silnější metylace exonů - souvislost s preferenčním výskytem nukleozómů na exonech (spoludefinování hranic exonů) - současně zvýšený výskyt polymerázy II - zbrždění nukleozómem Preferenční výskyt met. C na vnější straně nukleozómů - souvisí s preferenčním výskytem Cp. G na vnější straně (stérické důvody) - lépe přístupný pro metyltransferázy
 Mutace zprostředkované metylací C deaminace met. C G reparace C T met. C T G C G replikace G T A Možná role v evoluci genů (hypotetický scénář): - zdvojení sekvencí (např. po polyploidizaci) navodí metylaci - metylace navodí reversibilní inaktivaci - mutace met. C může navodit irreversibilní inaktivaci - kopie genu může být postupně masivně mutována (bez selekčního tlaku) - vznik a reaktivace genu s novou funkcí (x model EAC)
Mutace zprostředkované metylací C deaminace met. C G reparace C T met. C T G C G replikace G T A Možná role v evoluci genů (hypotetický scénář): - zdvojení sekvencí (např. po polyploidizaci) navodí metylaci - metylace navodí reversibilní inaktivaci - mutace met. C může navodit irreversibilní inaktivaci - kopie genu může být postupně masivně mutována (bez selekčního tlaku) - vznik a reaktivace genu s novou funkcí (x model EAC)
 Genom Arabidopsis - statistika Value Feature DNA molecule Chr. 1 Length (bp) Top arm (bp) Bottom arm (bp) 29, 105, 111 14, 449, 213 14, 655, 898 Base composition (%GC) Overall Coding Non-coding Number of genes Gene density (kb per gene ) Average gene Length (bp) Average peptide Length (bp) Exons Number Total length (bp) Average per gene Average size (bp) Number of genes With ESTs (%) Number of ESTs Chr. 2 Chr. 3 Chr. 4 Chr. 5 SUM 19, 646, 945 3, 607, 091 16, 039, 854 23, 172, 617 13, 590, 268 9, 582, 349 17, 549, 867 3, 052, 108 14, 497, 759 25, 53, 409 11, 132, 192 14, 803, 217 115, 409, 949 33. 4 44. 0 32. 4 35. 5 44. 0 32. 9 35. 4 44. 3 33. 0 35. 5 44. 1 32. 8 34. 5 44. 1 32. 5 6, 543 4. 0 4, 036 4. 9 5, 220 4. 5 3, 825 4. 6 5, 874 4. 4 2, 078 1, 949 1, 925 2, 138 1, 974 446 421 424 448 429 35, 482 8, 772, 559 5. 4 247 19, 631 5, 100, 288 4. 9 259 26, 570 6, 654, 507 5. 1 250 20, 073 5, 150, 883 5. 2 256 31, 226 7, 571, 013 5. 3 242 60. 8 56. 9 59. 8 61. 4 30, 522 14, 989 20, 732 16, 605 22, 885 25, 498 132, 982 33, 249, 250 105, 773 Nižší obsah CG v nekódujících sekvencích může odrážet mutace C* → T
Genom Arabidopsis - statistika Value Feature DNA molecule Chr. 1 Length (bp) Top arm (bp) Bottom arm (bp) 29, 105, 111 14, 449, 213 14, 655, 898 Base composition (%GC) Overall Coding Non-coding Number of genes Gene density (kb per gene ) Average gene Length (bp) Average peptide Length (bp) Exons Number Total length (bp) Average per gene Average size (bp) Number of genes With ESTs (%) Number of ESTs Chr. 2 Chr. 3 Chr. 4 Chr. 5 SUM 19, 646, 945 3, 607, 091 16, 039, 854 23, 172, 617 13, 590, 268 9, 582, 349 17, 549, 867 3, 052, 108 14, 497, 759 25, 53, 409 11, 132, 192 14, 803, 217 115, 409, 949 33. 4 44. 0 32. 4 35. 5 44. 0 32. 9 35. 4 44. 3 33. 0 35. 5 44. 1 32. 8 34. 5 44. 1 32. 5 6, 543 4. 0 4, 036 4. 9 5, 220 4. 5 3, 825 4. 6 5, 874 4. 4 2, 078 1, 949 1, 925 2, 138 1, 974 446 421 424 448 429 35, 482 8, 772, 559 5. 4 247 19, 631 5, 100, 288 4. 9 259 26, 570 6, 654, 507 5. 1 250 20, 073 5, 150, 883 5. 2 256 31, 226 7, 571, 013 5. 3 242 60. 8 56. 9 59. 8 61. 4 30, 522 14, 989 20, 732 16, 605 22, 885 25, 498 132, 982 33, 249, 250 105, 773 Nižší obsah CG v nekódujících sekvencích může odrážet mutace C* → T
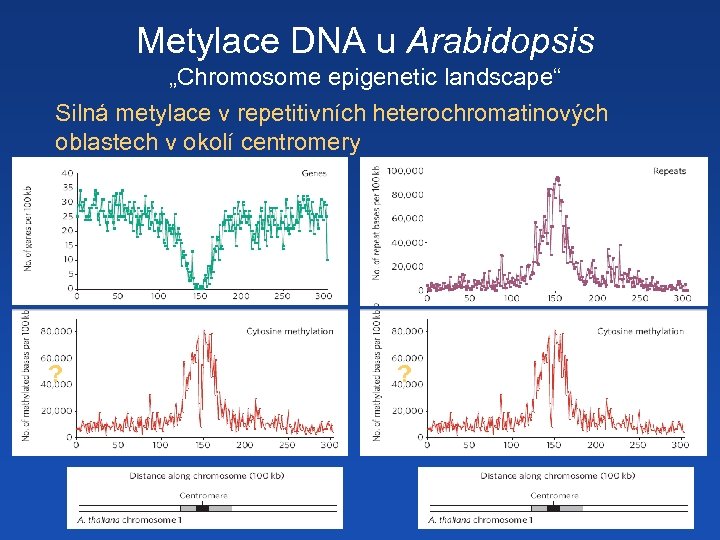 Metylace DNA u Arabidopsis „Chromosome epigenetic landscape“ Silná metylace v repetitivních heterochromatinových oblastech v okolí centromery ? ?
Metylace DNA u Arabidopsis „Chromosome epigenetic landscape“ Silná metylace v repetitivních heterochromatinových oblastech v okolí centromery ? ?
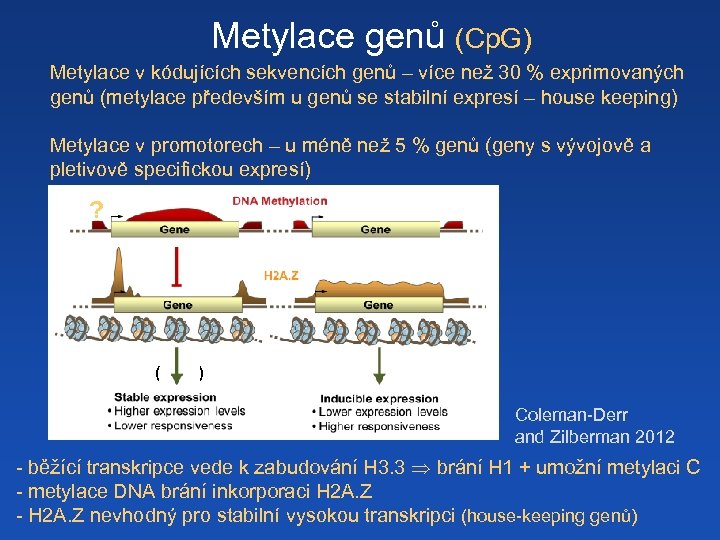 Metylace genů (Cp. G) Metylace v kódujících sekvencích genů – více než 30 % exprimovaných genů (metylace především u genů se stabilní expresí – house keeping) Metylace v promotorech – u méně než 5 % genů (geny s vývojově a pletivově specifickou expresí) ? ( ) Coleman-Derr and Zilberman 2012 - běžící transkripce vede k zabudování H 3. 3 brání H 1 + umožní metylaci C - metylace DNA brání inkorporaci H 2 A. Z - H 2 A. Z nevhodný pro stabilní vysokou transkripci (house-keeping genů)
Metylace genů (Cp. G) Metylace v kódujících sekvencích genů – více než 30 % exprimovaných genů (metylace především u genů se stabilní expresí – house keeping) Metylace v promotorech – u méně než 5 % genů (geny s vývojově a pletivově specifickou expresí) ? ( ) Coleman-Derr and Zilberman 2012 - běžící transkripce vede k zabudování H 3. 3 brání H 1 + umožní metylaci C - metylace DNA brání inkorporaci H 2 A. Z - H 2 A. Z nevhodný pro stabilní vysokou transkripci (house-keeping genů)
 Rostlinné cytosin 5 -metyltransferázy - 3 rodiny u Arabidopsis MET 1 (metyltransferase 1) CMT 3 a CMT 2 (chromomethyltransferase, „chromomethylase 3/2“) DRM 2 (a DRM 1) (domain rearranged methyltransferase 2/1)
Rostlinné cytosin 5 -metyltransferázy - 3 rodiny u Arabidopsis MET 1 (metyltransferase 1) CMT 3 a CMT 2 (chromomethyltransferase, „chromomethylase 3/2“) DRM 2 (a DRM 1) (domain rearranged methyltransferase 2/1)
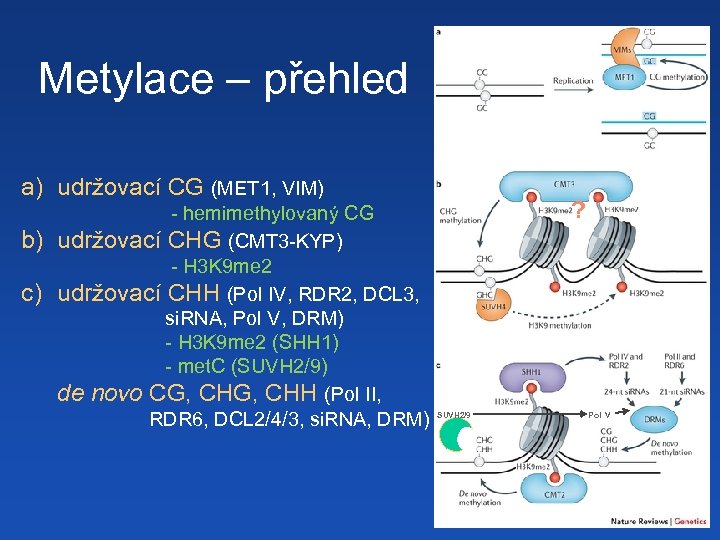 Metylace – přehled a) udržovací CG (MET 1, VIM) b) c) - hemimethylovaný CG udržovací CHG (CMT 3 -KYP) - H 3 K 9 me 2 udržovací CHH (Pol IV, RDR 2, DCL 3, si. RNA, Pol V, DRM) - H 3 K 9 me 2 (SHH 1) - met. C (SUVH 2/9) de novo CG, CHH (Pol II, RDR 6, DCL 2/4/3, si. RNA, DRM) ? SUVH 2/9 Pol V
Metylace – přehled a) udržovací CG (MET 1, VIM) b) c) - hemimethylovaný CG udržovací CHG (CMT 3 -KYP) - H 3 K 9 me 2 udržovací CHH (Pol IV, RDR 2, DCL 3, si. RNA, Pol V, DRM) - H 3 K 9 me 2 (SHH 1) - met. C (SUVH 2/9) de novo CG, CHH (Pol II, RDR 6, DCL 2/4/3, si. RNA, DRM) ? SUVH 2/9 Pol V
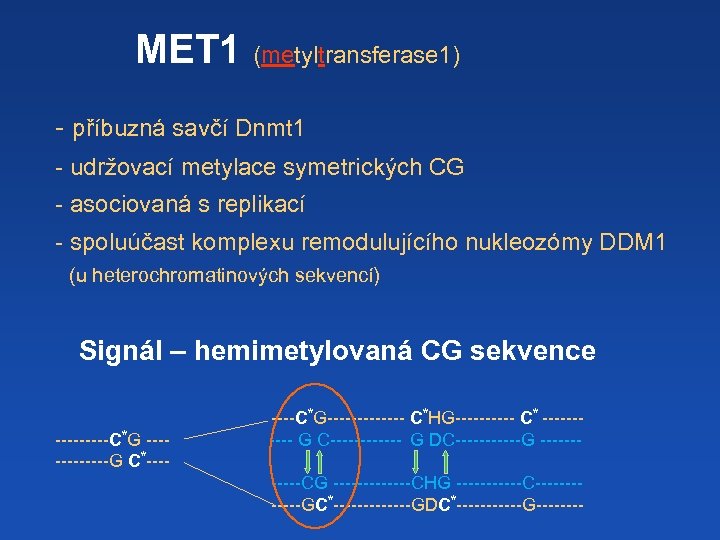 MET 1 (metyltransferase 1) - příbuzná savčí Dnmt 1 - udržovací metylace symetrických CG - asociovaná s replikací - spoluúčast komplexu remodulujícího nukleozómy DDM 1 (u heterochromatinových sekvencí) Signál – hemimetylovaná CG sekvence -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG -------CHG ------C------GC*-------GDC*------G----
MET 1 (metyltransferase 1) - příbuzná savčí Dnmt 1 - udržovací metylace symetrických CG - asociovaná s replikací - spoluúčast komplexu remodulujícího nukleozómy DDM 1 (u heterochromatinových sekvencí) Signál – hemimetylovaná CG sekvence -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG -------CHG ------C------GC*-------GDC*------G----
 CMT 3 (chromomethylase 3) - unikátní pro rostliny a houby (příbuzné savčím Dnmt 1, ale navíc obsahují chromodoménu = doménu interagující s met. K histonu - asociovaná především s konstitutivním heterochromatinem (repetitivní sekvence, TE - retrotranspozóny) - „udržovací“ metylace sekvencí CHG - kooperace s DDM 1 (nukleozómy remodelující protein) Aktivita podmíněna dimetylací histonu H 3 na lyzinu K 9 (interakce zprostředkovaná chromodoménou) -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG ------- CHG ------C------GC* -------GDC*------G----
CMT 3 (chromomethylase 3) - unikátní pro rostliny a houby (příbuzné savčím Dnmt 1, ale navíc obsahují chromodoménu = doménu interagující s met. K histonu - asociovaná především s konstitutivním heterochromatinem (repetitivní sekvence, TE - retrotranspozóny) - „udržovací“ metylace sekvencí CHG - kooperace s DDM 1 (nukleozómy remodelující protein) Aktivita podmíněna dimetylací histonu H 3 na lyzinu K 9 (interakce zprostředkovaná chromodoménou) -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG ------- CHG ------C------GC* -------GDC*------G----
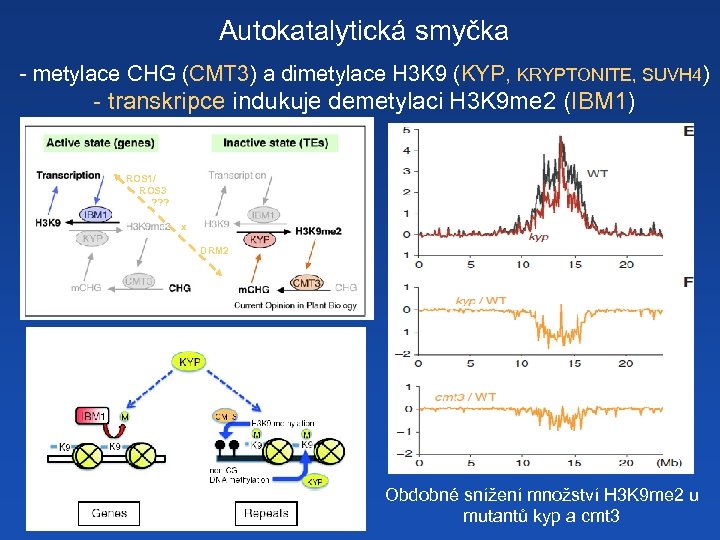 Autokatalytická smyčka - metylace CHG (CMT 3) a dimetylace H 3 K 9 (KYP, KRYPTONITE, SUVH 4) - transkripce indukuje demetylaci H 3 K 9 me 2 (IBM 1) ROS 1/ ROS 3 ? ? ? x DRM 2 Obdobné snížení množství H 3 K 9 me 2 u mutantů kyp a cmt 3
Autokatalytická smyčka - metylace CHG (CMT 3) a dimetylace H 3 K 9 (KYP, KRYPTONITE, SUVH 4) - transkripce indukuje demetylaci H 3 K 9 me 2 (IBM 1) ROS 1/ ROS 3 ? ? ? x DRM 2 Obdobné snížení množství H 3 K 9 me 2 u mutantů kyp a cmt 3
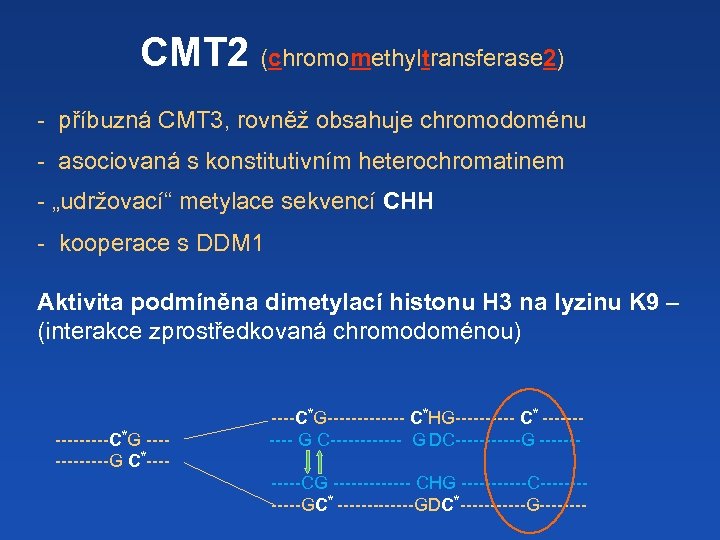 CMT 2 (chromomethyltransferase 2) - příbuzná CMT 3, rovněž obsahuje chromodoménu - asociovaná s konstitutivním heterochromatinem - „udržovací“ metylace sekvencí CHH - kooperace s DDM 1 Aktivita podmíněna dimetylací histonu H 3 na lyzinu K 9 – (interakce zprostředkovaná chromodoménou) -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG ------- CHG ------C------GC* -------GDC*------G----
CMT 2 (chromomethyltransferase 2) - příbuzná CMT 3, rovněž obsahuje chromodoménu - asociovaná s konstitutivním heterochromatinem - „udržovací“ metylace sekvencí CHH - kooperace s DDM 1 Aktivita podmíněna dimetylací histonu H 3 na lyzinu K 9 – (interakce zprostředkovaná chromodoménou) -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G DC------G ------CG ------- CHG ------C------GC* -------GDC*------G----
 DRM 2 a 1 (domain rearranged methyltransferase) - příbuzné savčím Dnmt 3, ale mají přeskupené domény - DRM 1 – v časné fázi vývoje semen -„udržovací metylace“ asymetrických sekvencí CHH (CHG) (euchromatin a okraje heterochromatinu) - de novo metylace všech sekvencí - regulace genové exprese, silencing - nutná spoluúčast katalyticky neaktivního paralogu DRM 3 u A. t. Cílové sekvence jsou určeny přítomností homologních si. RNA = RNA-directed DNA Methylation (Rd. DM) -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G HC------G ------CG -------CHG ------C------GC* -------GHC*------G----
DRM 2 a 1 (domain rearranged methyltransferase) - příbuzné savčím Dnmt 3, ale mají přeskupené domény - DRM 1 – v časné fázi vývoje semen -„udržovací metylace“ asymetrických sekvencí CHH (CHG) (euchromatin a okraje heterochromatinu) - de novo metylace všech sekvencí - regulace genové exprese, silencing - nutná spoluúčast katalyticky neaktivního paralogu DRM 3 u A. t. Cílové sekvence jsou určeny přítomností homologních si. RNA = RNA-directed DNA Methylation (Rd. DM) -----C*G ------G C*----C*G------- C*HG----- C* ----- G C------ G HC------G ------CG -------CHG ------C------GC* -------GHC*------G----
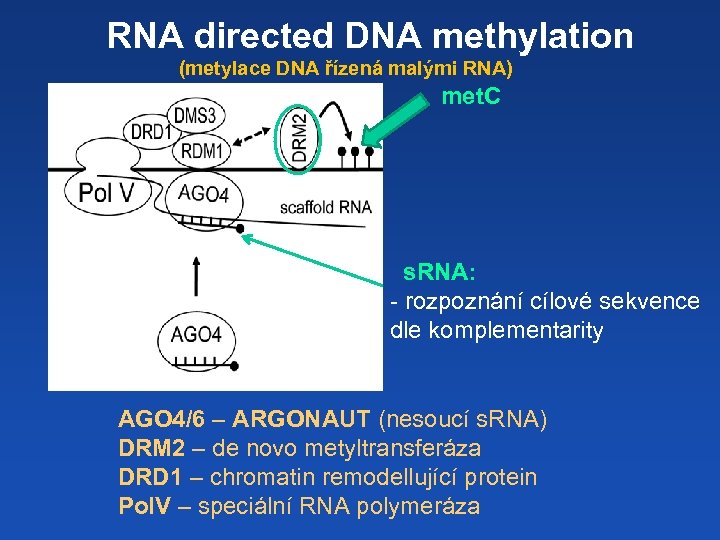 RNA directed DNA methylation (metylace DNA řízená malými RNA) met. C s. RNA: - rozpoznání cílové sekvence dle komplementarity AGO 4/6 – ARGONAUT (nesoucí s. RNA) DRM 2 – de novo metyltransferáza DRD 1 – chromatin remodellující protein Pol. V – speciální RNA polymeráza
RNA directed DNA methylation (metylace DNA řízená malými RNA) met. C s. RNA: - rozpoznání cílové sekvence dle komplementarity AGO 4/6 – ARGONAUT (nesoucí s. RNA) DRM 2 – de novo metyltransferáza DRD 1 – chromatin remodellující protein Pol. V – speciální RNA polymeráza
 Udržovací metylace DNA Heterochromatin s histonem H 1 - chromatin remodelující factor DDM 1 - metylace řízena: H 3 K 9 me 2 (CHH, CHG) – CMT 2, CMT 3 CG hemimetyl. stav – MET 1 Chromatin bez histonu H 1 - geny, okraje TE, … - metylace řízena: CG hemimetylace – MET 1 popř. si. RNA (Rd. DM) – DRM 2 (Rd. DM – H 3 K 9 me 2, demet. H 3 K 4, see later) + chromatin remodelující factor DRD 1
Udržovací metylace DNA Heterochromatin s histonem H 1 - chromatin remodelující factor DDM 1 - metylace řízena: H 3 K 9 me 2 (CHH, CHG) – CMT 2, CMT 3 CG hemimetyl. stav – MET 1 Chromatin bez histonu H 1 - geny, okraje TE, … - metylace řízena: CG hemimetylace – MET 1 popř. si. RNA (Rd. DM) – DRM 2 (Rd. DM – H 3 K 9 me 2, demet. H 3 K 4, see later) + chromatin remodelující factor DRD 1
 Demetylace DNA 1) při replikaci s vyloučením aktivity udržovacích cytosin metyltransferáz (a histonových metyláz) 2) DNA glykosylázy (odštěpení metylcytosinu, reparací doplněn cytosin) ROS 1 REPRESSOR OF SILENCING – somatické buňky (k demetylaci nutný ROS 3 – protein vázající RNA – s. RNA ? m. RNA) DEMETER-LIKE (DML 2, DML 3) – somatické buňky DME 1 DEMETER – demetylace v endospermu
Demetylace DNA 1) při replikaci s vyloučením aktivity udržovacích cytosin metyltransferáz (a histonových metyláz) 2) DNA glykosylázy (odštěpení metylcytosinu, reparací doplněn cytosin) ROS 1 REPRESSOR OF SILENCING – somatické buňky (k demetylaci nutný ROS 3 – protein vázající RNA – s. RNA ? m. RNA) DEMETER-LIKE (DML 2, DML 3) – somatické buňky DME 1 DEMETER – demetylace v endospermu
 Demetylace DNA ros 1 dml 2 dml 3 rel. změna metylace ROS 1 REPRESSOR OF SILENCING DEMETER-LIKE (DML 2, DML 3) (částečně zastupitelné) - aktivní ochrana reg. sekvencí genů (počátků a konců transkripce) před metylací – pak může být H 2 A. Z! metylace - vývojová aktivace genů (zrání rajčat) - mutace v „demetylačních“ genech se projeví především nárustem metylace v 3’ a 5’ UTR WT WT V metylačních (metyltransferázových) mutantech je utlumena demetylace (zpětná vazba).
Demetylace DNA ros 1 dml 2 dml 3 rel. změna metylace ROS 1 REPRESSOR OF SILENCING DEMETER-LIKE (DML 2, DML 3) (částečně zastupitelné) - aktivní ochrana reg. sekvencí genů (počátků a konců transkripce) před metylací – pak může být H 2 A. Z! metylace - vývojová aktivace genů (zrání rajčat) - mutace v „demetylačních“ genech se projeví především nárustem metylace v 3’ a 5’ UTR WT WT V metylačních (metyltransferázových) mutantech je utlumena demetylace (zpětná vazba).
 Ovlivňování metylace DNA - aplikace 5 -azacytidinu – blokování aktivity MET 1 - dihydroxypropyladenin (DHPA) – ovlivnění hladiny SAM - inaktivace genů MET 1, DDM 1, CMT 3, … (přirozené populace A. thaliana s mutantní CMT 2 odolnější vůči teplotnímu stresu) Projevy: - různé: žádné až výrazné - vývojové změny, pohlavní reverze u knotovky (andromonoecie), fenotyp cycloidea u lnice, … - změny fenotypu způsobené TE
Ovlivňování metylace DNA - aplikace 5 -azacytidinu – blokování aktivity MET 1 - dihydroxypropyladenin (DHPA) – ovlivnění hladiny SAM - inaktivace genů MET 1, DDM 1, CMT 3, … (přirozené populace A. thaliana s mutantní CMT 2 odolnější vůči teplotnímu stresu) Projevy: - různé: žádné až výrazné - vývojové změny, pohlavní reverze u knotovky (andromonoecie), fenotyp cycloidea u lnice, … - změny fenotypu způsobené TE
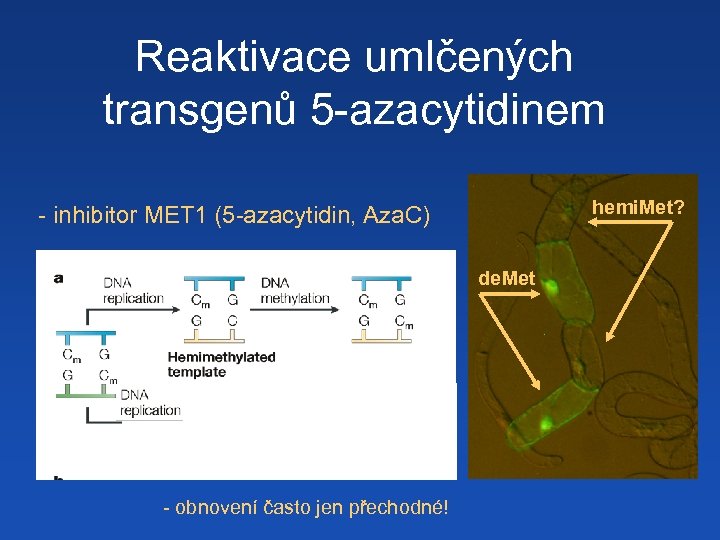 Reaktivace umlčených transgenů 5 -azacytidinem hemi. Met? - inhibitor MET 1 (5 -azacytidin, Aza. C) de. Met + Aza. C Demethylated - obnovení často jen přechodné!
Reaktivace umlčených transgenů 5 -azacytidinem hemi. Met? - inhibitor MET 1 (5 -azacytidin, Aza. C) de. Met + Aza. C Demethylated - obnovení často jen přechodné!
 Analýzy metylace DNA Přímé (strukturní): - spektrofotometrie, HPLC (celkový stav) - %met. C - anti met. C protilátky (na chromozómu …) - lokalizace met. C bohatých úseků chromozómů - pomocí restriktáz citlivých k metylaci - detekce met. C v konkrétním restrikčním místě - hydrogensiřičitanovým sekvenováním - přesné určení C a met. C v určité sekvenci - i v celém genomu (v kombinaci s moderními technikami sekvenování) - přímým sekvenováním vláken genomové DNA (viz genomika) Nepřímé (funkční) – vztah mezi metylací a genovou expresí - např. sledování reaktivace umlčených (trans)genů
Analýzy metylace DNA Přímé (strukturní): - spektrofotometrie, HPLC (celkový stav) - %met. C - anti met. C protilátky (na chromozómu …) - lokalizace met. C bohatých úseků chromozómů - pomocí restriktáz citlivých k metylaci - detekce met. C v konkrétním restrikčním místě - hydrogensiřičitanovým sekvenováním - přesné určení C a met. C v určité sekvenci - i v celém genomu (v kombinaci s moderními technikami sekvenování) - přímým sekvenováním vláken genomové DNA (viz genomika) Nepřímé (funkční) – vztah mezi metylací a genovou expresí - např. sledování reaktivace umlčených (trans)genů
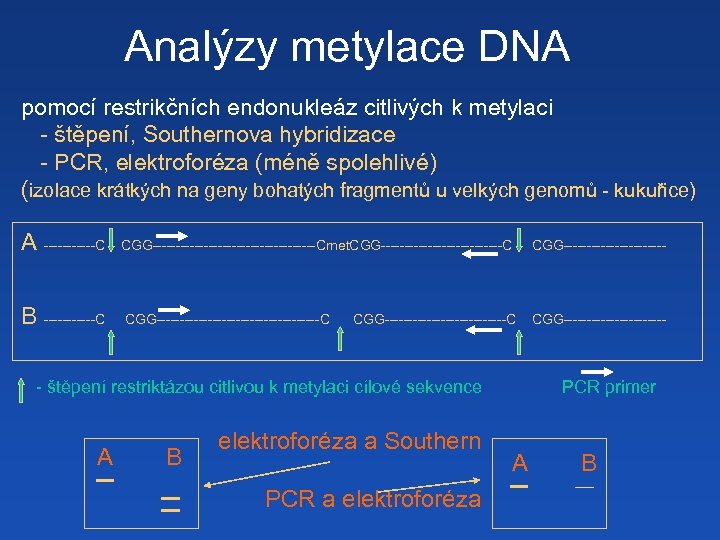 Analýzy metylace DNA pomocí restrikčních endonukleáz citlivých k metylaci - štěpení, Southernova hybridizace - PCR, elektroforéza (méně spolehlivé) (izolace krátkých na geny bohatých fragmentů u velkých genomů - kukuřice) A ------C CGG------------------Cmet. CGG-------------C CGG----------- B ------C CGG------------------C CGG--------------------------C - štěpení restriktázou citlivou k metylaci cílové sekvence A B elektroforéza a Southern PCR a elektroforéza PCR primer A B
Analýzy metylace DNA pomocí restrikčních endonukleáz citlivých k metylaci - štěpení, Southernova hybridizace - PCR, elektroforéza (méně spolehlivé) (izolace krátkých na geny bohatých fragmentů u velkých genomů - kukuřice) A ------C CGG------------------Cmet. CGG-------------C CGG----------- B ------C CGG------------------C CGG--------------------------C - štěpení restriktázou citlivou k metylaci cílové sekvence A B elektroforéza a Southern PCR a elektroforéza PCR primer A B
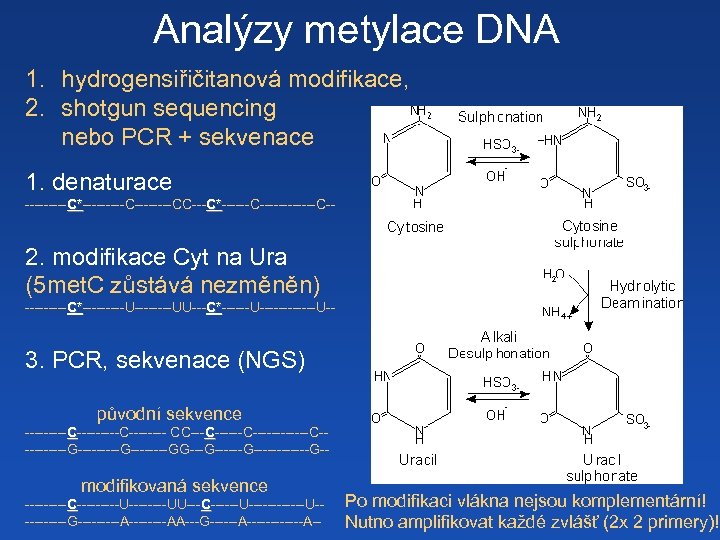 Analýzy metylace DNA 1. hydrogensiřičitanová modifikace, 2. shotgun sequencing nebo PCR + sekvenace 1. denaturace -----C*-----C----CC---C*------C------C-C* C* 2. modifikace Cyt na Ura (5 met. C zůstává nezměněn) -----C*-----U----UU---C*------U------U-C* C* 3. PCR, sekvenace (NGS) původní sekvence ---------C---- CC------C----------G--------GG------G------G-- modifikovaná sekvence -----C-----U----UU---C------U----------G-----A----AA---G------A------A-- Po modifikaci vlákna nejsou komplementární! Nutno amplifikovat každé zvlášť (2 x 2 primery)!
Analýzy metylace DNA 1. hydrogensiřičitanová modifikace, 2. shotgun sequencing nebo PCR + sekvenace 1. denaturace -----C*-----C----CC---C*------C------C-C* C* 2. modifikace Cyt na Ura (5 met. C zůstává nezměněn) -----C*-----U----UU---C*------U------U-C* C* 3. PCR, sekvenace (NGS) původní sekvence ---------C---- CC------C----------G--------GG------G------G-- modifikovaná sekvence -----C-----U----UU---C------U----------G-----A----AA---G------A------A-- Po modifikaci vlákna nejsou komplementární! Nutno amplifikovat každé zvlášť (2 x 2 primery)!
 Stérické důsledky metylace DNA - buněčná interpretace metylace DNA • změny na úrovni histonů - posttranslační modifikace histonů - SRA doména: metylace Lys (SUVH family), - Metyl Cp. G-binding d. : př. deacetylace (HDAC) - zastoupení různých forem histonů (H 2 A. Z) • udržování metylace DNA (CHH - Rd. DM) - SRA doména: SUVH 2/9 – atrahování Pol V • změna vazby dalších interagujících proteinů - regulátorů (aktivátorů a represorů) transkripce - zřejmě důsledkem komplexních změn chromatinu
Stérické důsledky metylace DNA - buněčná interpretace metylace DNA • změny na úrovni histonů - posttranslační modifikace histonů - SRA doména: metylace Lys (SUVH family), - Metyl Cp. G-binding d. : př. deacetylace (HDAC) - zastoupení různých forem histonů (H 2 A. Z) • udržování metylace DNA (CHH - Rd. DM) - SRA doména: SUVH 2/9 – atrahování Pol V • změna vazby dalších interagujících proteinů - regulátorů (aktivátorů a represorů) transkripce - zřejmě důsledkem komplexních změn chromatinu
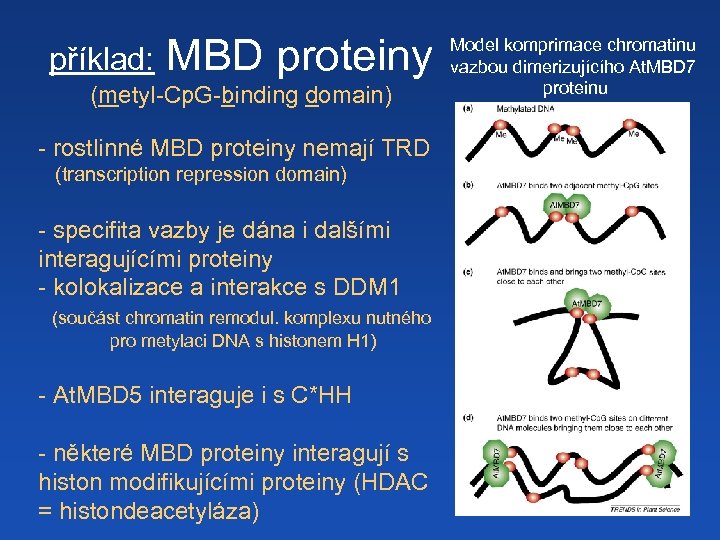 příklad: MBD proteiny (metyl-Cp. G-binding domain) - rostlinné MBD proteiny nemají TRD (transcription repression domain) - specifita vazby je dána i dalšími interagujícími proteiny - kolokalizace a interakce s DDM 1 (součást chromatin remodul. komplexu nutného pro metylaci DNA s histonem H 1) - At. MBD 5 interaguje i s C*HH - některé MBD proteiny interagují s histon modifikujícími proteiny (HDAC = histondeacetyláza) Model komprimace chromatinu vazbou dimerizujícího At. MBD 7 proteinu
příklad: MBD proteiny (metyl-Cp. G-binding domain) - rostlinné MBD proteiny nemají TRD (transcription repression domain) - specifita vazby je dána i dalšími interagujícími proteiny - kolokalizace a interakce s DDM 1 (součást chromatin remodul. komplexu nutného pro metylaci DNA s histonem H 1) - At. MBD 5 interaguje i s C*HH - některé MBD proteiny interagují s histon modifikujícími proteiny (HDAC = histondeacetyláza) Model komprimace chromatinu vazbou dimerizujícího At. MBD 7 proteinu
 Metylace DNA a stav chromatinu - přehled - prokázána korelace hypermetylace DNA a hypoacetylace histonů (pozdní replikace DNA) - metylace DNA je dědičným signálem k deacetylaci histonů a kondenzaci chromatinu - obdobné fenotypové změny při potlačení metylace (MET 1) a deacetylace histonů (At. HD 1) - transkripce udržuje aktivační značky (demetylaci H 3 K 9 – IBM 1), začleňování H 3. 3, a tím Cp. G metylaci genů - přítomnost histonu H 2 A. Z se vzájemně vylučuje s metylací DNA!!! (typicky v promotorech house-keeping genů), H 2 A. W je naopak společně s metylovanou DNA v heterochromatinu
Metylace DNA a stav chromatinu - přehled - prokázána korelace hypermetylace DNA a hypoacetylace histonů (pozdní replikace DNA) - metylace DNA je dědičným signálem k deacetylaci histonů a kondenzaci chromatinu - obdobné fenotypové změny při potlačení metylace (MET 1) a deacetylace histonů (At. HD 1) - transkripce udržuje aktivační značky (demetylaci H 3 K 9 – IBM 1), začleňování H 3. 3, a tím Cp. G metylaci genů - přítomnost histonu H 2 A. Z se vzájemně vylučuje s metylací DNA!!! (typicky v promotorech house-keeping genů), H 2 A. W je naopak společně s metylovanou DNA v heterochromatinu
 Udržování epigenetického stavu – přehled Heterochromatin (histon H 1) - dimetylace H 3 K 9 (KYP) je signálem pro metylaci CHG - metylace CHG je signálem pro metylaci H 3 K 9 MET 1 – udržovací metylace C*G KYP (SUVH 5, 6) – H 3 K 9 me 2 CMT 3 - C*HG (CMT 2 – C*HH) Transkripčně neaktivní (eu)chromatin: Rd. DM: DRM 2, (DRM 1) – udrž. metylace CHH kompl. si. RNA Represe pomocí H 3 K 27 me 2 (PRC) – nezávislá na metylaci Euchromatin – transkripčně aktivní - trimetylace H 3 K 4 a zřejmě i demetylace H 3 K 9 (IBM 1) v souvislosti s transkripcí Pol II transkripce IBM 1 – demetylace H 3 K 9, H 3 K 4 me 3 (x tvorbě si. RNA) ROS 1/ROS 3, DML 2, DML 3 – demet. C transkripce? , s. RNA?
Udržování epigenetického stavu – přehled Heterochromatin (histon H 1) - dimetylace H 3 K 9 (KYP) je signálem pro metylaci CHG - metylace CHG je signálem pro metylaci H 3 K 9 MET 1 – udržovací metylace C*G KYP (SUVH 5, 6) – H 3 K 9 me 2 CMT 3 - C*HG (CMT 2 – C*HH) Transkripčně neaktivní (eu)chromatin: Rd. DM: DRM 2, (DRM 1) – udrž. metylace CHH kompl. si. RNA Represe pomocí H 3 K 27 me 2 (PRC) – nezávislá na metylaci Euchromatin – transkripčně aktivní - trimetylace H 3 K 4 a zřejmě i demetylace H 3 K 9 (IBM 1) v souvislosti s transkripcí Pol II transkripce IBM 1 – demetylace H 3 K 9, H 3 K 4 me 3 (x tvorbě si. RNA) ROS 1/ROS 3, DML 2, DML 3 – demet. C transkripce? , s. RNA?


