lecture7_coding sequences.ppt
- Количество слайдов: 35
 Экзон-интронная структура эукариотических генов Лекция № 7 – Свойства эукариотических геномов В. Н. Бабенко
Экзон-интронная структура эукариотических генов Лекция № 7 – Свойства эукариотических геномов В. Н. Бабенко
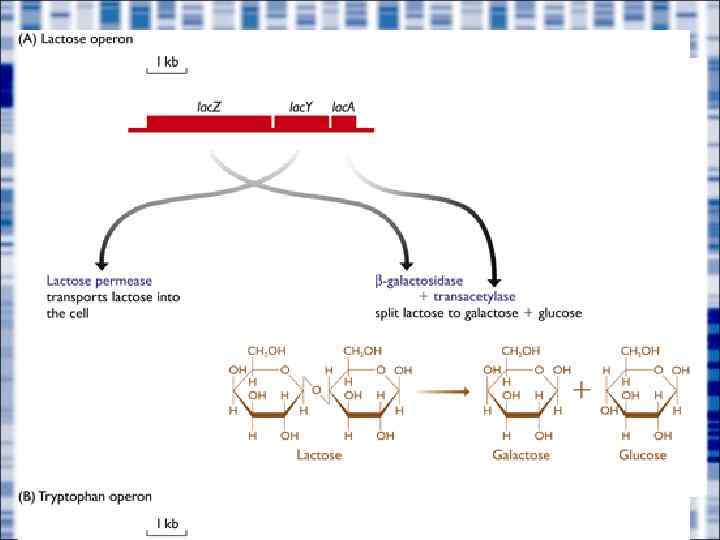
 Введение • Экзон-интронная структура присуща только эукариотическим генам (генам в клетке с ядерной оболочкой) • Структура (размер) гена непостредственно связана со структурой (размером) генома • Прокариотические гены не содержат интронов, организованы в опероны и содержат один промотор на «взвод» (несколько генов).
Введение • Экзон-интронная структура присуща только эукариотическим генам (генам в клетке с ядерной оболочкой) • Структура (размер) гена непостредственно связана со структурой (размером) генома • Прокариотические гены не содержат интронов, организованы в опероны и содержат один промотор на «взвод» (несколько генов).
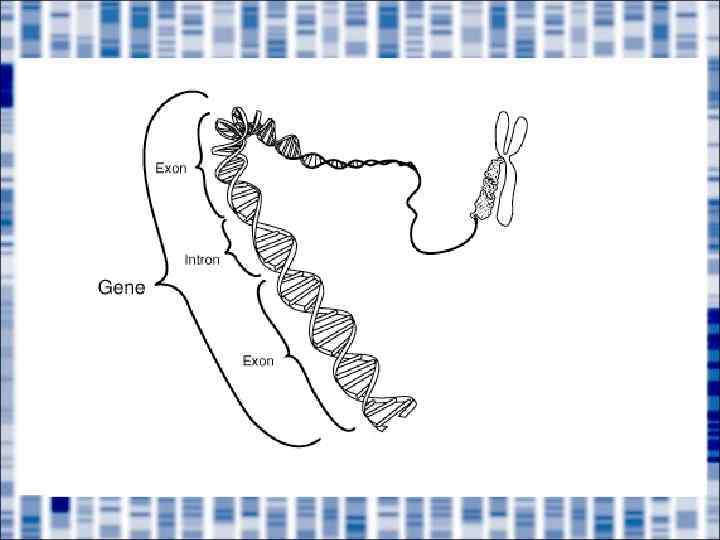
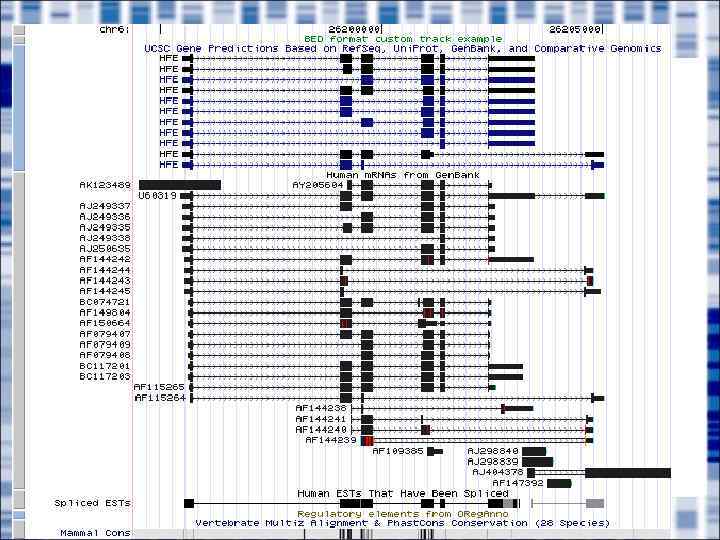
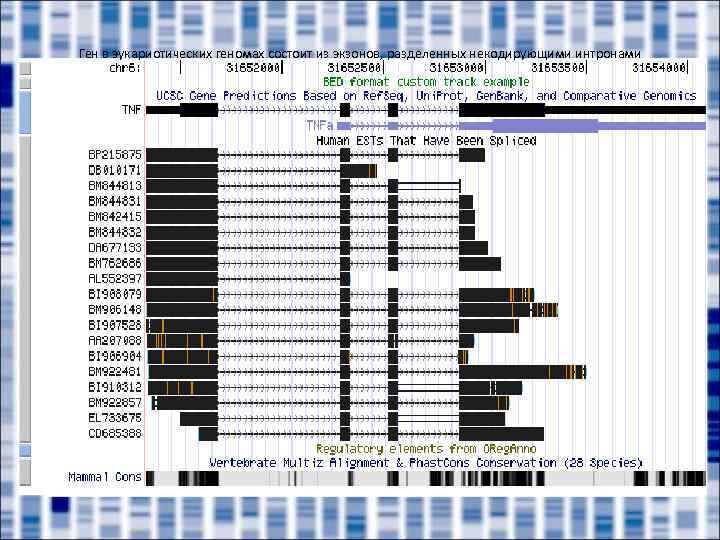 Ген в эукариотических геномах состоит из экзонов, разделенных некодирующими интронами
Ген в эукариотических геномах состоит из экзонов, разделенных некодирующими интронами
 Фундаментальные вопросы • Происхождение интронов? Интроны «сначала» или «потом» ? /при инвазии митохондрий и возникновении ядра/ • Почему они нужны (важны)? /содержат регуляторы сплайсинга; источник вариабельности/ • Как может геном эукариот выдерживать такую эволюционную нагрузку ? /он существует, значит может/ • Зачем нужен льтернативный сплайсинг ? (координированная экспрессия нужной изоформы)
Фундаментальные вопросы • Происхождение интронов? Интроны «сначала» или «потом» ? /при инвазии митохондрий и возникновении ядра/ • Почему они нужны (важны)? /содержат регуляторы сплайсинга; источник вариабельности/ • Как может геном эукариот выдерживать такую эволюционную нагрузку ? /он существует, значит может/ • Зачем нужен льтернативный сплайсинг ? (координированная экспрессия нужной изоформы)
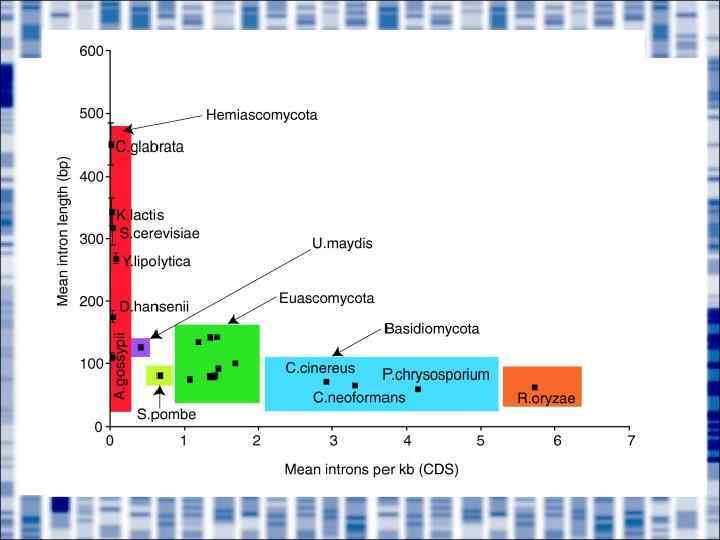
 Характеристики экзонов и интронов • ЭКЗОН: Средняя длина экзона ~100 пн, медиана ~120 пн (характерна для всех эукариотических геномов) распределение длины нормальное • ИНТРОН: Средняя длина ~2000 пн, медиана ~200 пн. Распределение практически бесконечное (до 600 кб). Средняя длина интрона варьирует пропорционально размеру генома.
Характеристики экзонов и интронов • ЭКЗОН: Средняя длина экзона ~100 пн, медиана ~120 пн (характерна для всех эукариотических геномов) распределение длины нормальное • ИНТРОН: Средняя длина ~2000 пн, медиана ~200 пн. Распределение практически бесконечное (до 600 кб). Средняя длина интрона варьирует пропорционально размеру генома.
 Далее рассмотрим два пункта: • Механизм сплайсинга, сплайсосома, альтернативный сплайсинг • Происхождение и эволюция интронов
Далее рассмотрим два пункта: • Механизм сплайсинга, сплайсосома, альтернативный сплайсинг • Происхождение и эволюция интронов
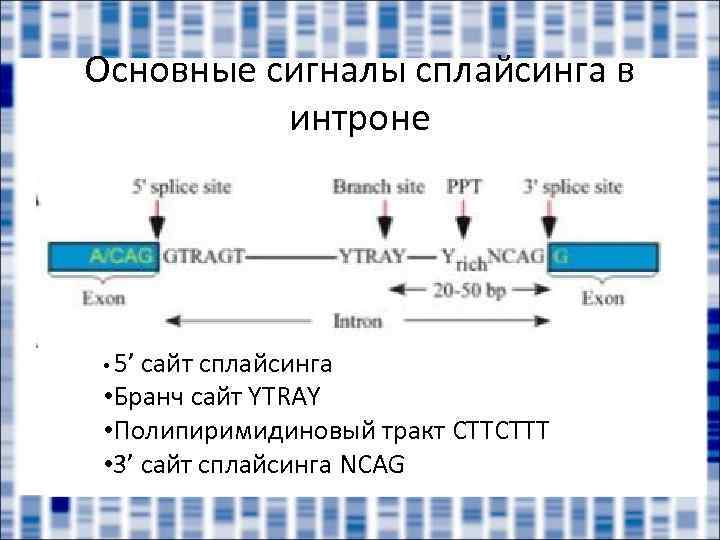 Основные сигналы сплайсинга в интроне • 5’ сайт сплайсинга • Бранч сайт YTRAY • Полипиримидиновый тракт CTTCTTT • 3’ сайт сплайсинга NCAG
Основные сигналы сплайсинга в интроне • 5’ сайт сплайсинга • Бранч сайт YTRAY • Полипиримидиновый тракт CTTCTTT • 3’ сайт сплайсинга NCAG
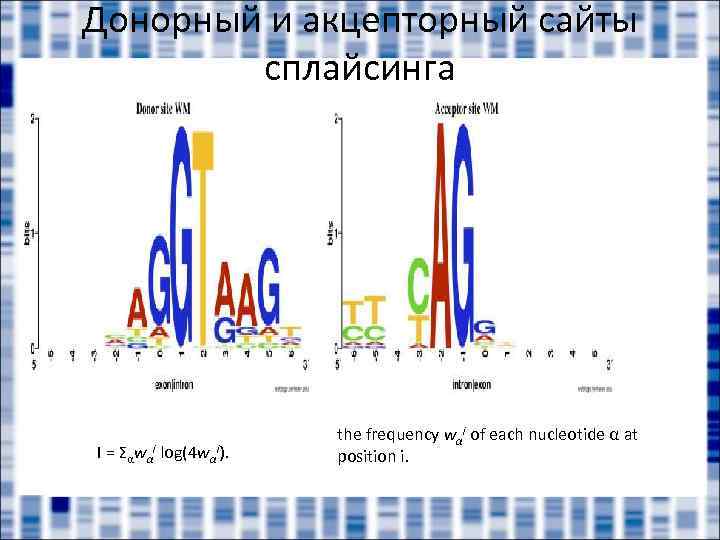 Донорный и акцепторный сайты сплайсинга I = Σαwαi log(4 wαi). the frequency wαi of each nucleotide α at position i.
Донорный и акцепторный сайты сплайсинга I = Σαwαi log(4 wαi). the frequency wαi of each nucleotide α at position i.
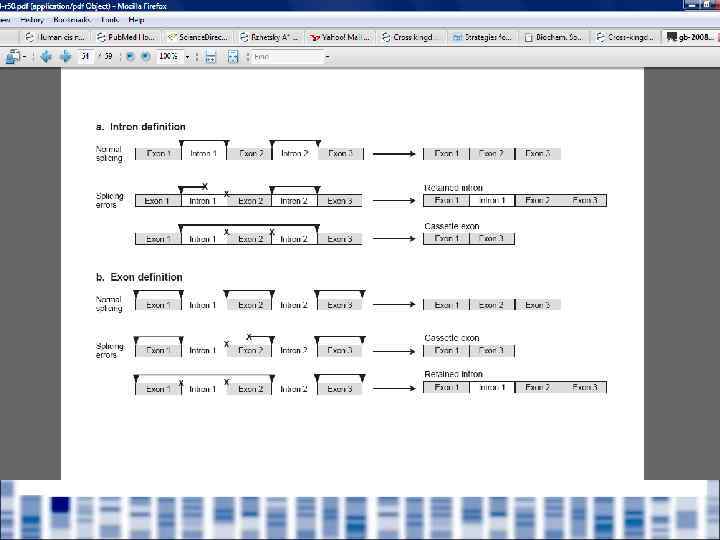
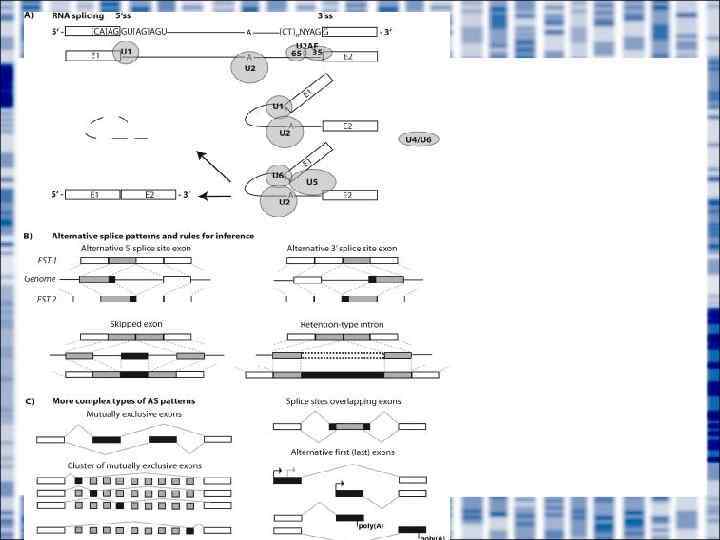
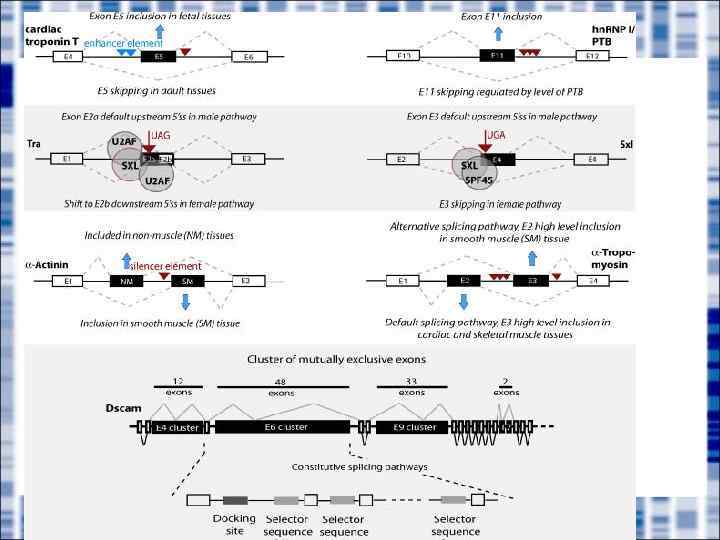
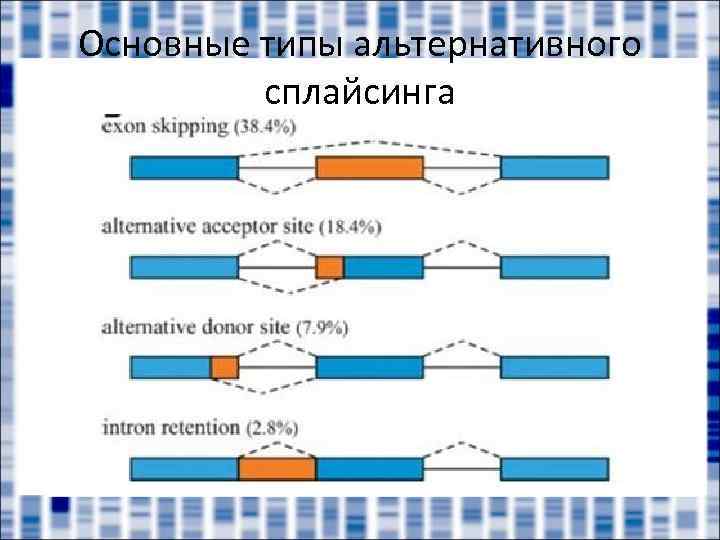 Основные типы альтернативного сплайсинга
Основные типы альтернативного сплайсинга
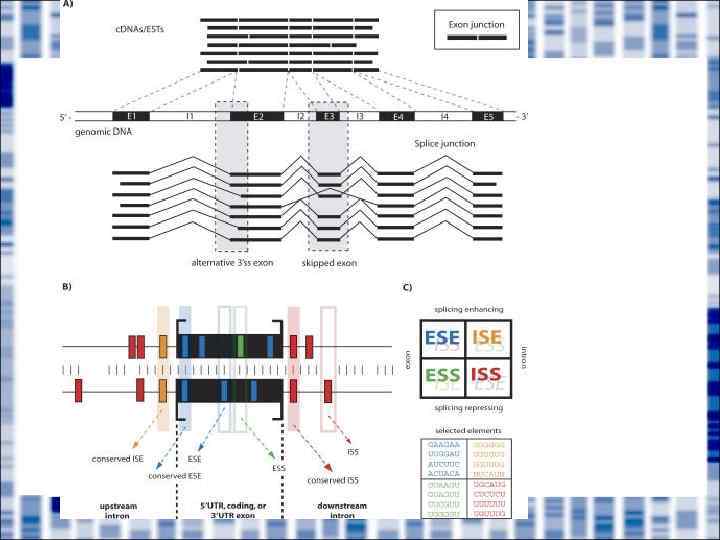
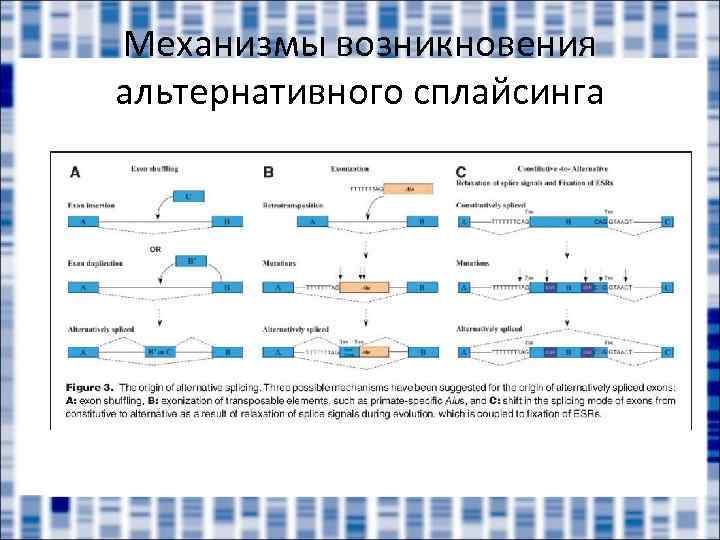 Механизмы возникновения альтернативного сплайсинга
Механизмы возникновения альтернативного сплайсинга
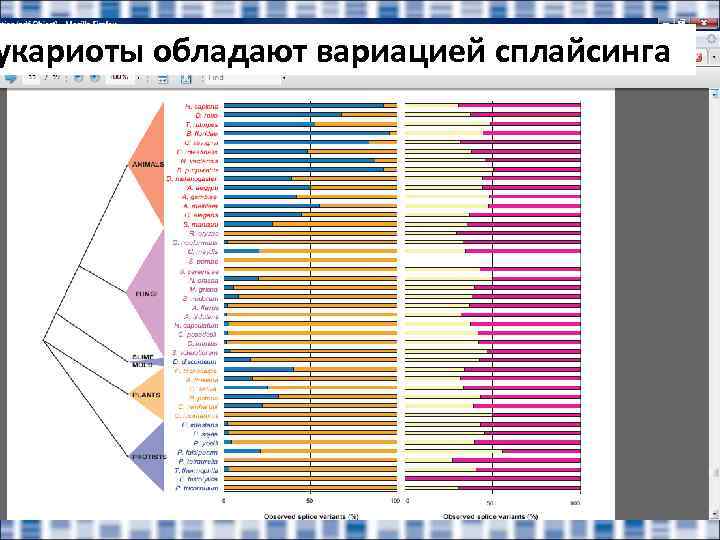 укариоты обладают вариацией сплайсинга
укариоты обладают вариацией сплайсинга
 Figure 1 Assembly of the U sn. RNPs into the spliceosome and the rearrangement of RNA-RNA interactions during the spliceosome assembly Сборка sn. RNP в сплайсосому и процесс сплайсинга Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -
Figure 1 Assembly of the U sn. RNPs into the spliceosome and the rearrangement of RNA-RNA interactions during the spliceosome assembly Сборка sn. RNP в сплайсосому и процесс сплайсинга Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -
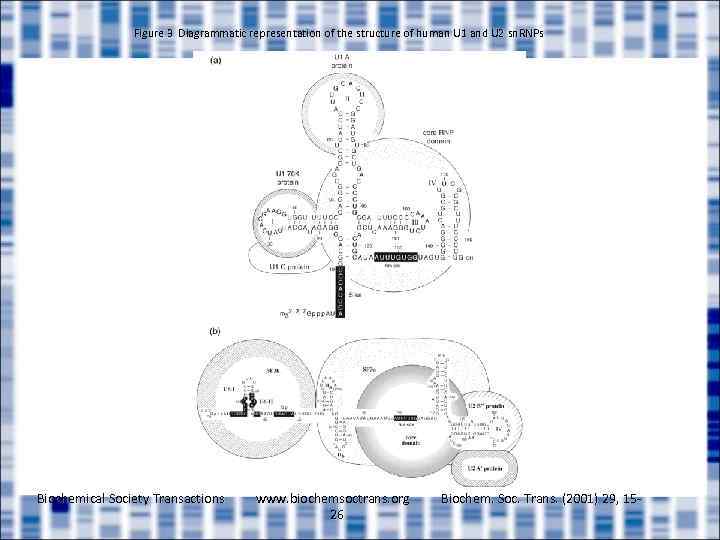 Figure 3 Diagrammatic representation of the structure of human U 1 and U 2 sn. RNPs Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -
Figure 3 Diagrammatic representation of the structure of human U 1 and U 2 sn. RNPs Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -
 Происхождение интронов • The "intron-early" hypothesis suggests that introns existed before the divergence of prokaryotes and eukaryotes (W. Gilbert). Loss and sliding • The "intron-late" hypothesis claims that introns were inserted into eukaryotic genes after this divergence (T. Cavalier-Smith, Doolittles, J. Palmer) Gain and loss
Происхождение интронов • The "intron-early" hypothesis suggests that introns existed before the divergence of prokaryotes and eukaryotes (W. Gilbert). Loss and sliding • The "intron-late" hypothesis claims that introns were inserted into eukaryotic genes after this divergence (T. Cavalier-Smith, Doolittles, J. Palmer) Gain and loss
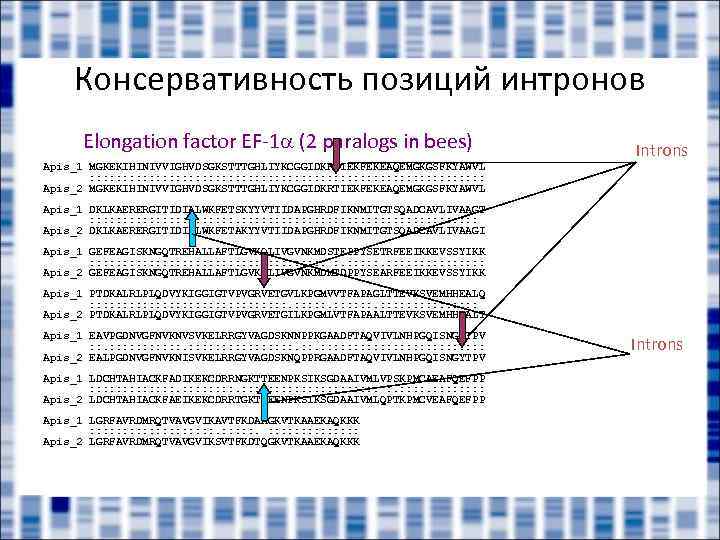 Консервативность позиций интронов Elongation factor EF-1 (2 paralogs in bees) Introns Apis_1 MGKEKIHINIVVIGHVDSGKSTTTGHLIYKCGGIDKRTIEKFEKEAQEMGKGSFKYAWVL : : : : : : : : : : : : : : : Apis_2 MGKEKIHINIVVIGHVDSGKSTTTGHLIYKCGGIDKRTIEKFEKEAQEMGKGSFKYAWVL Apis_1 DKLKAERERGITIDIALWKFETSKYYVTIIDAPGHRDFIKNMITGTSQADCAVLIVAAGT : : : : : : : : : Apis_2 DKLKAERERGITIDIALWKFETAKYYVTIIDAPGHRDFIKNMITGTSQADCAVLIVAAGI Apis_1 GEFEAGISKNGQTREHALLAFTLGVKQLIVGVNKMDSTEPPYSETRFEEIKKEVSSYIKK : : : : : : : : : : Apis_2 GEFEAGISKNGQTREHALLAFTLGVKQLIVGVNKMDMTDPPYSEARFEEIKKEVSSYIKK Apis_1 PTDKALRLPLQDVYKIGGIGTVPVGRVETGVLKPGMVVTFAPAGLTTEVKSVEMHHEALQ : : : : : : : : Apis_2 PTDKALRLPLQDVYKIGGIGTVPVGRVETGILKPGMLVTFAPAALTTEVKSVEMHHEALT Apis_1 EAVPGDNVGFNVKNVSVKELRRGYVAGDSKNNPPKGAADFTAQVIVLNHPGQISNGYTPV : : : : : : : : Apis_2 EALPGDNVGFNVKNISVKELRRGYVAGDSKNQPPRGAADFTAQVIVLNHPGQISNGYTPV Apis_1 LDCHTAHIACKFADIKEKCDRRNGKTTEENPKSIKSGDAAIVMLVPSKPMCAEAFQEFPP : : : : : : : : Apis_2 LDCHTAHIACKFAEIKEKCDRRTGKTTEENPKSIKSGDAAIVMLQPTKPMCVEAFQEFPP Apis_1 LGRFAVRDMRQTVAVGVIKAVTFKDAAGKVTKAAEKAQKKK : : : : : Apis_2 LGRFAVRDMRQTVAVGVIKSVTFKDTQGKVTKAAEKAQKKK Introns
Консервативность позиций интронов Elongation factor EF-1 (2 paralogs in bees) Introns Apis_1 MGKEKIHINIVVIGHVDSGKSTTTGHLIYKCGGIDKRTIEKFEKEAQEMGKGSFKYAWVL : : : : : : : : : : : : : : : Apis_2 MGKEKIHINIVVIGHVDSGKSTTTGHLIYKCGGIDKRTIEKFEKEAQEMGKGSFKYAWVL Apis_1 DKLKAERERGITIDIALWKFETSKYYVTIIDAPGHRDFIKNMITGTSQADCAVLIVAAGT : : : : : : : : : Apis_2 DKLKAERERGITIDIALWKFETAKYYVTIIDAPGHRDFIKNMITGTSQADCAVLIVAAGI Apis_1 GEFEAGISKNGQTREHALLAFTLGVKQLIVGVNKMDSTEPPYSETRFEEIKKEVSSYIKK : : : : : : : : : : Apis_2 GEFEAGISKNGQTREHALLAFTLGVKQLIVGVNKMDMTDPPYSEARFEEIKKEVSSYIKK Apis_1 PTDKALRLPLQDVYKIGGIGTVPVGRVETGVLKPGMVVTFAPAGLTTEVKSVEMHHEALQ : : : : : : : : Apis_2 PTDKALRLPLQDVYKIGGIGTVPVGRVETGILKPGMLVTFAPAALTTEVKSVEMHHEALT Apis_1 EAVPGDNVGFNVKNVSVKELRRGYVAGDSKNNPPKGAADFTAQVIVLNHPGQISNGYTPV : : : : : : : : Apis_2 EALPGDNVGFNVKNISVKELRRGYVAGDSKNQPPRGAADFTAQVIVLNHPGQISNGYTPV Apis_1 LDCHTAHIACKFADIKEKCDRRNGKTTEENPKSIKSGDAAIVMLVPSKPMCAEAFQEFPP : : : : : : : : Apis_2 LDCHTAHIACKFAEIKEKCDRRTGKTTEENPKSIKSGDAAIVMLQPTKPMCVEAFQEFPP Apis_1 LGRFAVRDMRQTVAVGVIKAVTFKDAAGKVTKAAEKAQKKK : : : : : Apis_2 LGRFAVRDMRQTVAVGVIKSVTFKDTQGKVTKAAEKAQKKK Introns
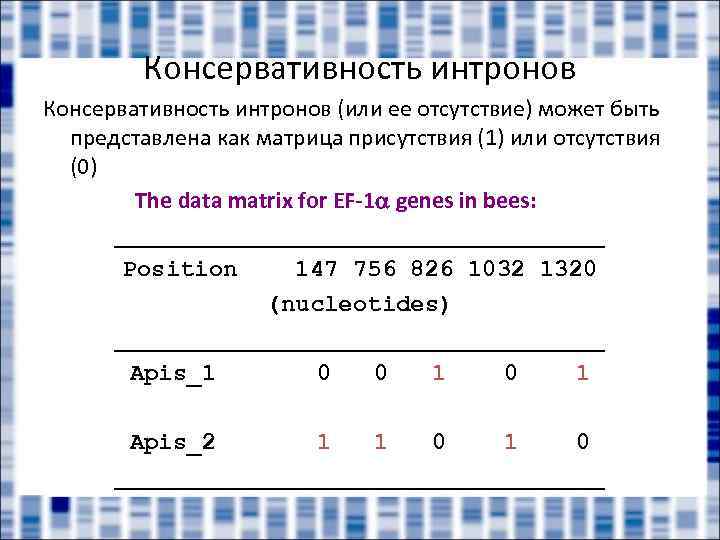 Консервативность интронов (или ее отсутствие) может быть представлена как матрица присутствия (1) или отсутствия (0) The data matrix for EF-1 genes in bees: _________________ Position 147 756 826 1032 1320 (nucleotides) _________________ Apis_1 0 0 1 Apis_2 1 1 0 _________________
Консервативность интронов (или ее отсутствие) может быть представлена как матрица присутствия (1) или отсутствия (0) The data matrix for EF-1 genes in bees: _________________ Position 147 756 826 1032 1320 (nucleotides) _________________ Apis_1 0 0 1 Apis_2 1 1 0 _________________
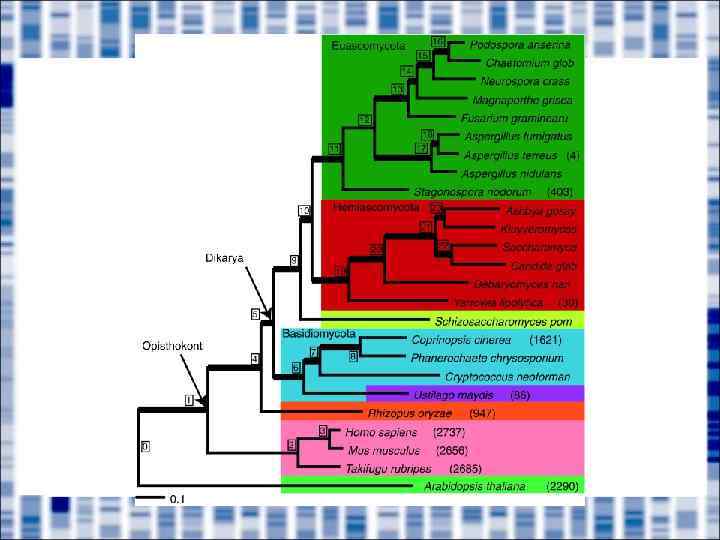
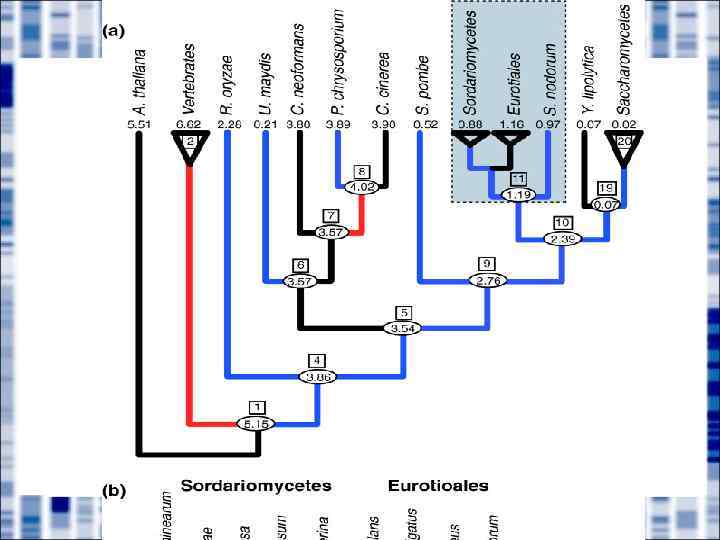
 Observed and expected numbers of shared introns SC SP AT CE DM HS SC 23 2 1 1 1 2 SP AT CE DM HS 0 1 1 0 2 74 2 0 0 3 21 420 1 2 8 Expected 15 46 236 1 5 (Monte Carlo) 17 42 46 139 4 30 131 99 95 523 observed The total number of introns in the 98 analyzed genes from the given species.
Observed and expected numbers of shared introns SC SP AT CE DM HS SC 23 2 1 1 1 2 SP AT CE DM HS 0 1 1 0 2 74 2 0 0 3 21 420 1 2 8 Expected 15 46 236 1 5 (Monte Carlo) 17 42 46 139 4 30 131 99 95 523 observed The total number of introns in the 98 analyzed genes from the given species.
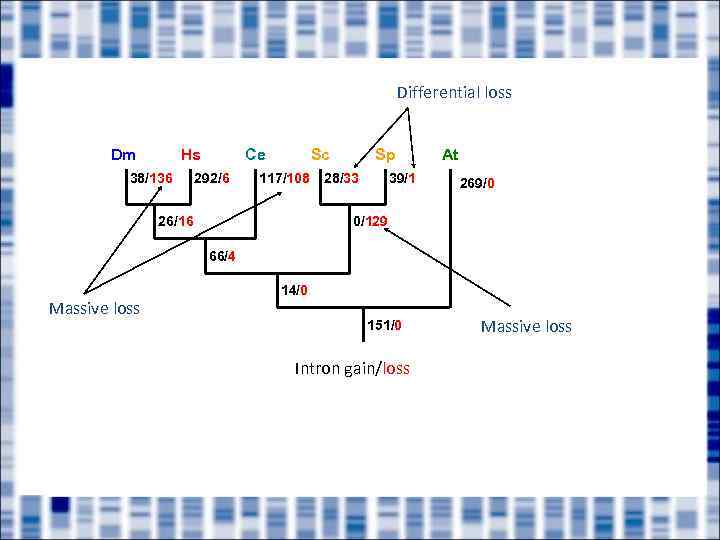 Differential loss Dm Hs 38/136 Ce 292/6 Sc 117/108 26/16 Sp 28/33 39/1 At 269/0 0/129 66/4 Massive loss 14/0 151/0 Intron gain/loss Massive loss
Differential loss Dm Hs 38/136 Ce 292/6 Sc 117/108 26/16 Sp 28/33 39/1 At 269/0 0/129 66/4 Massive loss 14/0 151/0 Intron gain/loss Massive loss
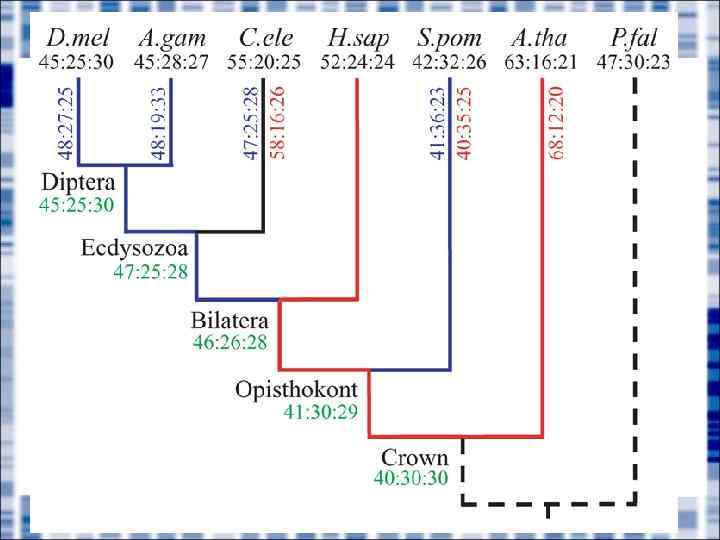
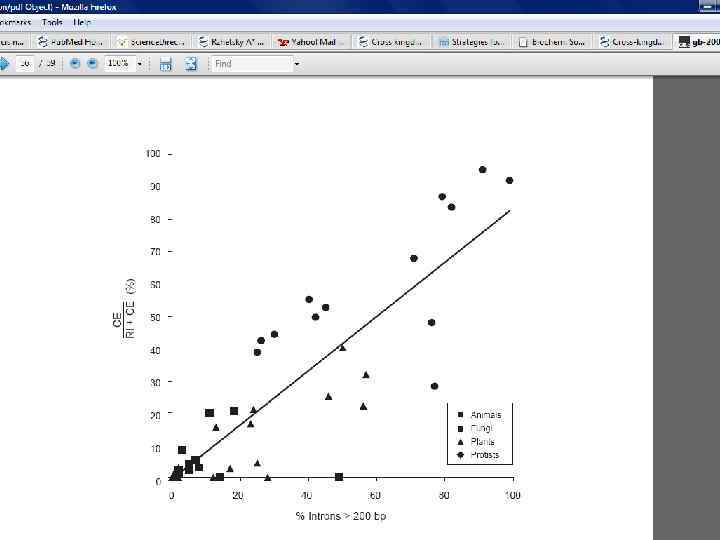
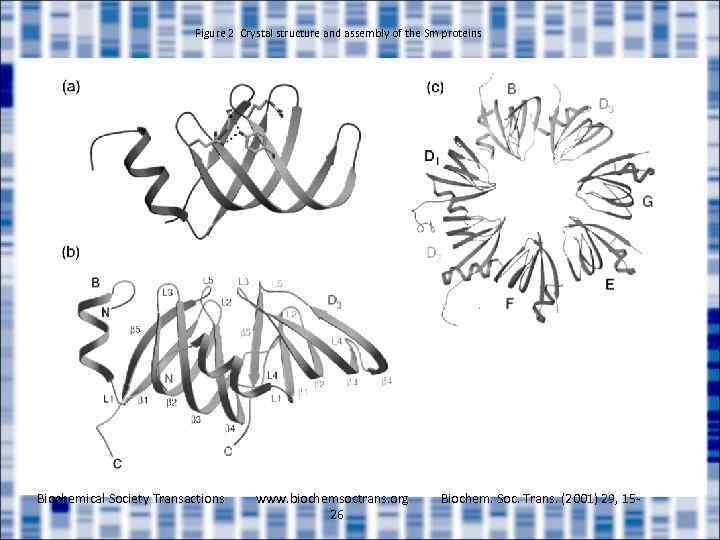 Figure 2 Crystal structure and assembly of the Sm proteins Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -
Figure 2 Crystal structure and assembly of the Sm proteins Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -
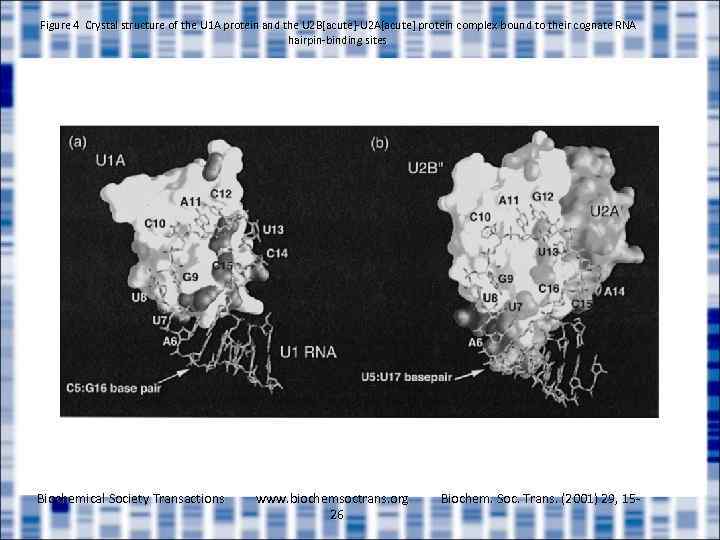 Figure 4 Crystal structure of the U 1 A protein and the U 2 B[acute]-U 2 A[acute] protein complex bound to their cognate RNA hairpin-binding sites Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -
Figure 4 Crystal structure of the U 1 A protein and the U 2 B[acute]-U 2 A[acute] protein complex bound to their cognate RNA hairpin-binding sites Biochemical Society Transactions www. biochemsoctrans. org 26 Biochem. Soc. Trans. (2001) 29, 15 -

 Различие в экспрессии в норме и раковой ткани
Различие в экспрессии в норме и раковой ткани
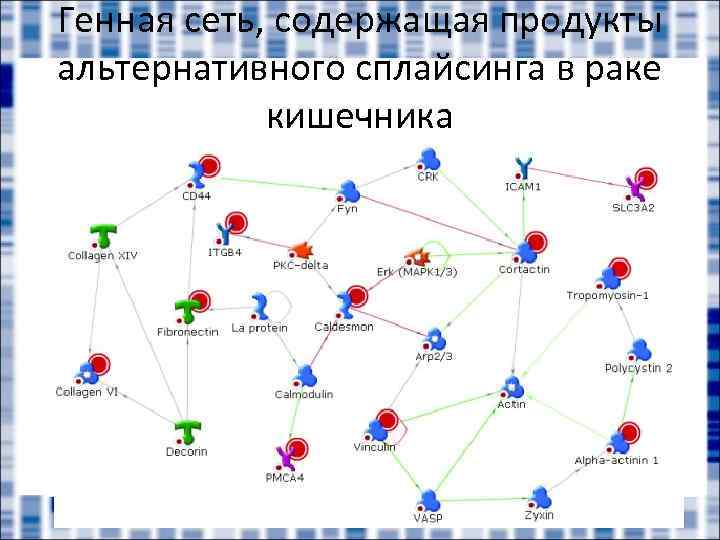 Генная сеть, содержащая продукты альтернативного сплайсинга в раке кишечника
Генная сеть, содержащая продукты альтернативного сплайсинга в раке кишечника


