acd99628e07c9499f949c1d4ad6e5494.ppt
- Количество слайдов: 68

互联网生物信息资源 Bioinformatics Resources on the Internet 罗静初 北京大学生物信息中心 luojc@pku. edu. cn http: //www. cbi. pku. edu. cn/

Half day on the web, saves you half month in the lab. - Alan Bleasby

2000年 2月2日,北京大学燕北园 300多位教师的家用计算 机接入Internet; 2001年 2月12日,北京大学 2000多个本 科生宿舍的计算机接入Internet. 02022000 01011000 AGAGGAAA Bio. Med. X Bioinformatic s 3/15/2018

网络时代的生命科学 和生物技术产业 讨论会 9 -10 Apr 2001 首届中国生物信息学 大会 11 -13 Apr 2001
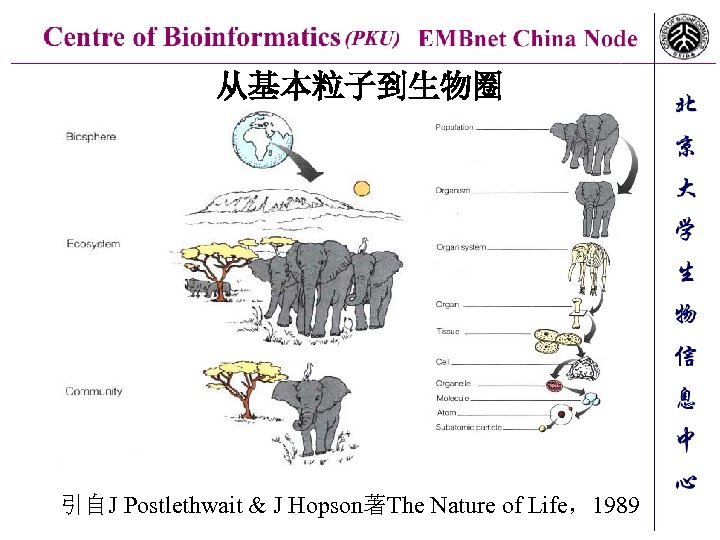
从基本粒子到生物圈 引自J Postlethwait & J Hopson著The Nature of Life,1989
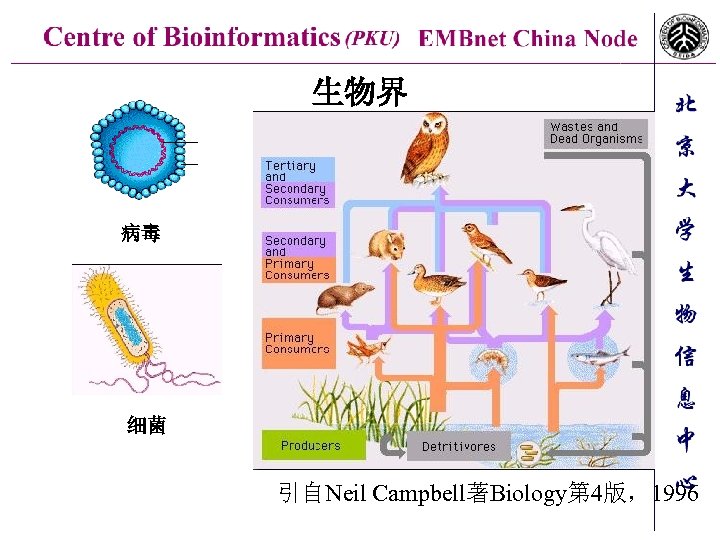
生物界 病毒 细菌 引自Neil Campbell著Biology第 4版,1996
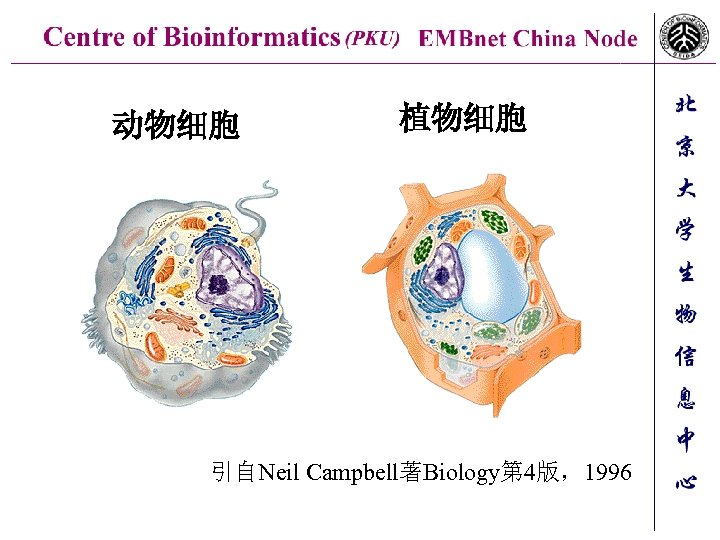
动物细胞 植物细胞 引自Neil Campbell著Biology第 4版,1996
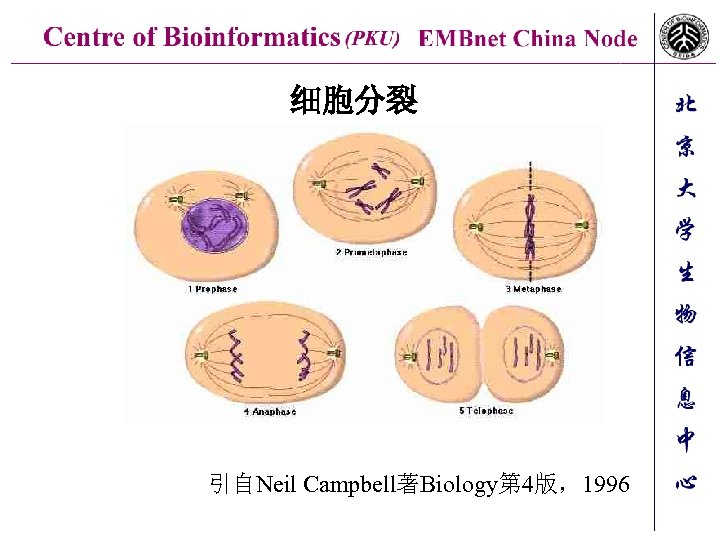
细胞分裂 引自Neil Campbell著Biology第 4版,1996
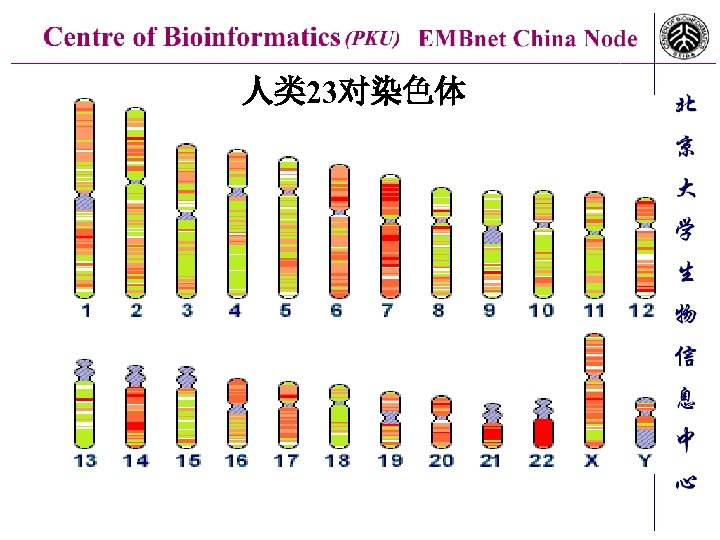
人类 23对染色体
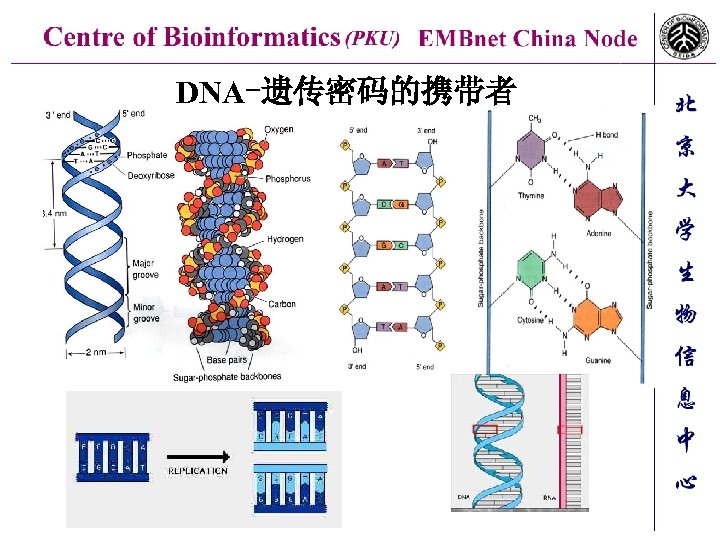
DNA-遗传密码的携带者
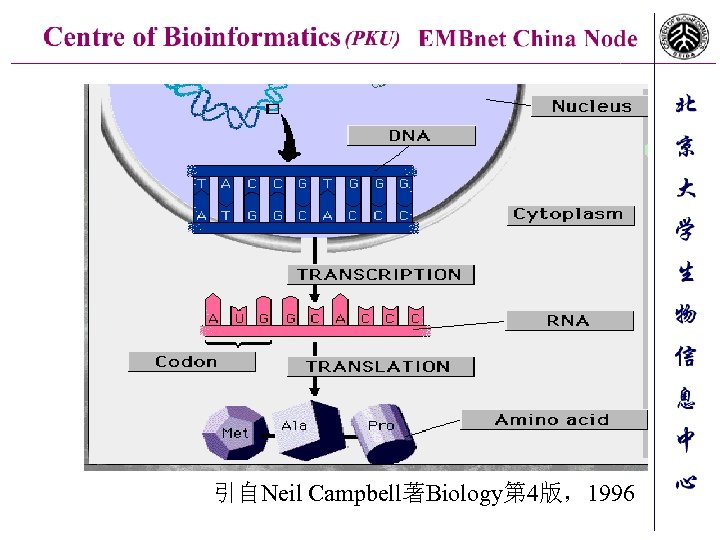
引自Neil Campbell著Biology第 4版,1996
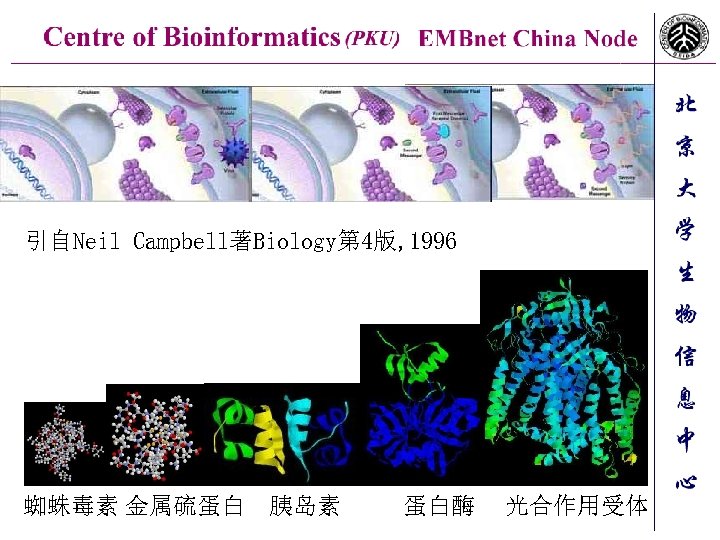
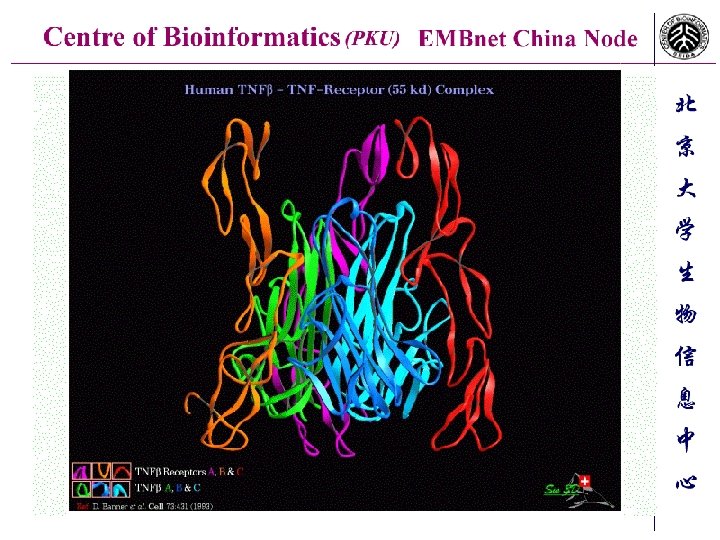
引自Neil Campbell著Biology第 4版, 1996 蜘蛛毒素 金属硫蛋白 胰岛素 蛋白酶 光合作用受体
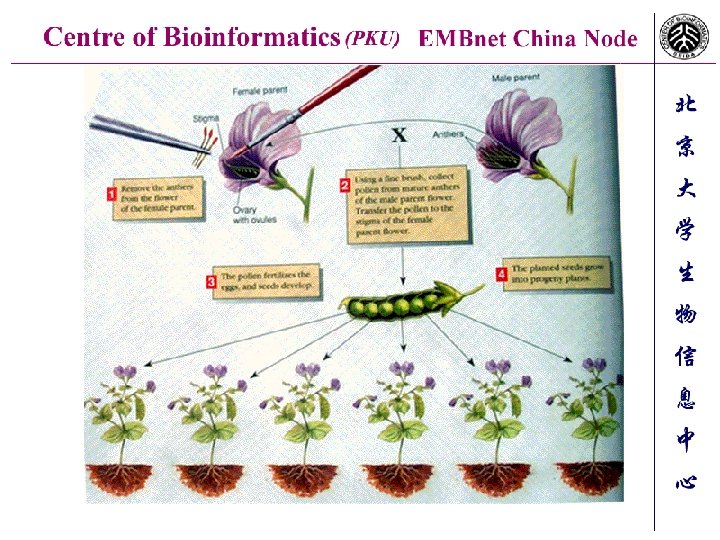

Nature 171, 737 -734 (1953) (C) Macmillan Publishers Ltd. Molecular structure of Nucleic Acids WATSON, J. D. & CRICK, F. H. C. Medical Research Council Unit for the Study of Molecular Structure of Biological Systems, Cavendish Laboratory, Cambridge. A Structure for Deoxyribose Nucleic Acid We wish to suggest a structure for the salt of deoxyribose nucleic acid (D. N. A. ). This structure has novel features which are of considerable biological interest. Figure 1 This figure is purely diagrammatic. The two ribbons symbolize the two phophate-sugar chains, and the horizonal rods the pairs of bases holding the chains together. The vertical line marks the fibre axis.
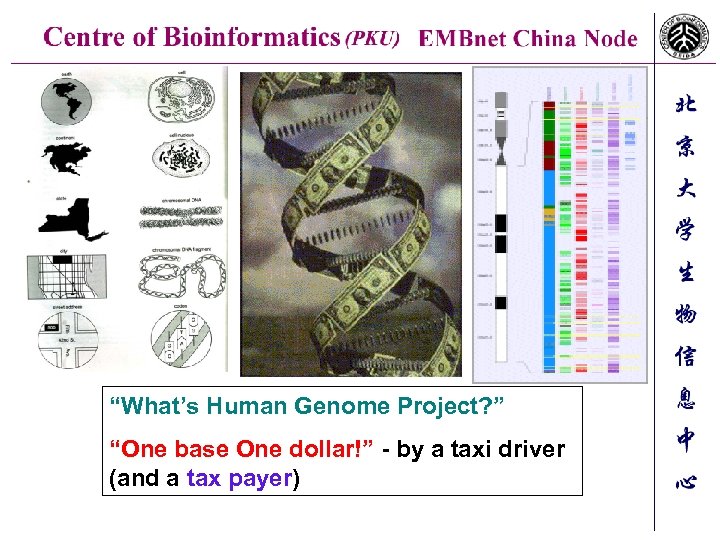
“What’s Human Genome Project? ” “One base One dollar!” - by a taxi driver (and a tax payer)

Ureaplasma urealyticum Buchnerasp. APS Thermoplasma acidophilum Plasmodium falciparum Bacillus subtilis Escherichia coli大肠杆菌 mouse Borrelia burgorferi Drosophila melanogaster human Caenorhabitis elegans Aquifex aeolicus Rickettsia prowazekii Arabidopsis 拟南芥 rat Neisseria meningitidis Z 2491 Helicobacter pylori Thermotoga maritima Borrelia burgorferi Mycobacteriu m tuberculosis

数据引自http: //wit. integratedgenomics. com/GOLD/ 图片引自http: //www. ri. bbsrc. ac. uk/arkdb/sites. html
![Initial sequencing and analysis of the human genome [PDF] Nature 409, 860 - 921 Initial sequencing and analysis of the human genome [PDF] Nature 409, 860 - 921](https://present5.com/presentation/acd99628e07c9499f949c1d4ad6e5494/image-18.jpg)
Initial sequencing and analysis of the human genome [PDF] Nature 409, 860 - 921 (2001), 15 February 2001 International Human Genome Sequencing Consortium Whitehead Institute for Biomedical Research, Center for Genome Research: ERIC S. LANDER 1*, LAUREN M. LINTON 1, BRUCE BIRREN 1*, CHAD NUSBAUM 1*, MICHAEL C. ZODY 1*, JENNIFER BALDWIN 1, KERI DEVON 1, KEN DEWAR 1, MICHAEL DOYLE 1, WILLIAM FITZHUGH 1*, ROEL FUNKE 1, DIANE GAGE 1, KATRINA HARRIS 1, ANDREW HEAFORD 1, JOHN HOWLAND 1, LISA KANN 1, JESSICA LEHOCZKY 1, ROSIE LEVINE 1, PAUL MCEWAN 1, KEVIN MCKERNAN 1, JAMES MELDRIM 1, JILL P. MESIROV 1, CHER MIRANDA 1, WILLIAM MORRIS 1, JEROME NAYLOR 1, CHRISTINA RAYMOND 1, MARK ROSETTI 1, RALPH SANTOS 1, ANDREW SHERIDAN 1, CARRIE SOUGNEZ 1, NICOLE STANGE-THOMANN 1, NIKOLA STOJANOVIC 1, ARAVIND SUBRAMANIAN 1 & DUDLEY WYMAN 1 The Sanger Centre: JANE ROGERS 2, JOHN SULSTON 2*, RACHAEL AINSCOUGH 2, STEPHAN BECK 2, DAVID BENTLEY 2, JOHN BURTON 2, CHRISTOPHER CLEE 2, NIGEL CARTER 2, ALAN COULSON 2, REBECCA DEADMAN 2, PANOS DELOUKAS 2, ANDREW DUNHAM 2, IAN DUNHAM 2, RICHARD DURBIN 2*, LISA FRENCH 2, DARREN GRAFHAM 2, SIMON GREGORY 2, TIM HUBBARD 2*, SEAN HUMPHRAY 2, ADRIENNE HUNT 2, MATTHEW JONES 2, CHRISTINE LLOYD 2, AMANDA MCMURRAY 2, LUCY MATTHEWS 2, SIMON MERCER 2, SARAH MILNE 2, JAMES C. MULLIKIN 2, ANDREW MUNGALL 2, ROBERT PLUMB 2, MARK ROSS 2, RATNA SHOWNKEEN 2 & SARAH SIMS 2 Washington University Genome Sequencing Center ROBERT H. WATERSTON 3*, RICHARD K. WILSON 3, LADEANA W. HILLIER 3, JOHN D. MCPHERSON 3, MARCO A. MARRA 3, ELAINE R. MARDIS 3, LUCINDA A. FULTON 3, ASIF T. CHINWALLA 3, KYMBERLIE H. PEPIN 3, WARREN R. GISH 3, STEPHANIE L. CHISSOE 3, MICHAEL C. WENDL 3, KIM D. DELEHAUNTY 3, TRACIE L. MINER 3, ANDREW DELEHAUNTY 3, JASON B. KRAMER 3, LISA L. COOK 3, ROBERT S. FULTON 3, DOUGLAS L. JOHNSON 3, PATRICK J. MINX 3 & SANDRA W. CLIFTON 3 US DOE Joint Genome Institute: TREVOR HAWKINS 4, ELBERT BRANSCOMB 4, PAUL PREDKI 4, PAUL RICHARDSON 4, SARAH WENNING 4, TOM SLEZAK 4, NORMAN DOGGETT 4, JAN-FANG CHENG 4, ANNE OLSEN 4, SUSAN LUCAS 4, CHRISTOPHER ELKIN 4, EDWARD UBERBACHER 4 & MARVIN FRAZIER 4 Baylor College of Medicine Human Genome Sequencing Center: RICHARD A. GIBBS 5*, DONNA M. MUZNY 5, STEVEN E. SCHERER 5, JOHN B. BOUCK 5, ERICA J. SODERGREN 5, KIM C. WORLEY 5, CATHERINE M. RIVES 5, JAMES H. GORRELL 5, MICHAEL L. METZKER 5, SUSAN L. NAYLOR 6, RAJU S. KUCHERLAPATI 7, DAVID L. NELSON & GEORGE M. WEINSTOCK 8 RIKEN Genomic Sciences Center: YOSHIYUKI SAKAKI 9, ASAO FUJIYAMA 9, MASAHIRA HATTORI 9, TETSUSHI YADA 9, ATSUSHI TOYODA 9, TAKEHIKO ITOH 9, CHIHARU KAWAGOE 9, HIDEMI WATANABE 9, YASUSHI TOTOKI 9 & TODD TAYLOR 9 Genoscope and CNRS UMR-8030: JEAN WEISSENBACH 10, ROLAND HEILIG 10, WILLIAM SAURIN 10, FRANCOIS ARTIGUENAVE 10, PHILIPPE BROTTIER 10, THOMAS BRULS 10, ERIC PELLETIER 10, CATHERINE ROBERT 10 & PATRICK WINCKER 10
![The Sequence of the Human Genome [ PDF] J. Craig Venter, Mark D. Adams, The Sequence of the Human Genome [ PDF] J. Craig Venter, Mark D. Adams,](https://present5.com/presentation/acd99628e07c9499f949c1d4ad6e5494/image-19.jpg)
The Sequence of the Human Genome [ PDF] J. Craig Venter, Mark D. Adams, Eugene W. Myers, Peter W. Li, Richard J. Mural, Granger G. Sutton, Hamilton O. Smith, Mark Yandell, Cheryl A. Evans, Robert A. Holt, Jeannine D. Gocayne, Peter Amanatides, Richard M. Ballew, Daniel H. Huson, Jennifer Russo Wortman, Qing Zhang, Chinnappa D. Kodira, Xiangqun H. Zheng, Lin Chen, Marian Skupski, Gangadharan Subramanian, Paul D. Thomas, Jinghui Zhang, George L. Gabor Miklos, Catherine Nelson, Samuel Broder, Andrew G. Clark, 4 Joe Nadeau, Victor A. Mc. Kusick, Norton Zinder, Arnold J. Levine, Richard J. Roberts, 8 Mel Simon, Carolyn Slayman, Michael Hunkapiller, Randall Bolanos, Arthur Delcher, Ian Dew, Daniel Fasulo, Michael Flanigan, Liliana Florea, Aaron Halpern, Sridhar Hannenhalli, Saul Kravitz, Samuel Levy, Clark Mobarry, Knut Reinert, Karin Remington, Jane Abu-Threideh, Ellen Beasley, Kendra Biddick, Vivien Bonazzi, Rhonda Brandon, Michele Cargill, Ishwar handramouliswaran, Rosane Charlab, Kabir Chaturvedi, Zuoming Deng, Valentina Di Francesco, Patrick Dunn, Karen Eilbeck, Carlos Evangelista, Andrei E. Gabrielian, Weiniu Gan, Wangmao Ge, Fangcheng Gong, Zhiping Gu, Ping Guan, Thomas J. Heiman, Maureen E. Higgins, Rui-Ru Ji, Zhaoxi Ke, Karen A. Ketchum, Zhongwu Lai, Yiding Lei, Zhenya Li, Jiayin Li, Yong Liang, Xiaoying Lin, Fu Lu, Gennady V. Merkulov, Natalia Milshina, Helen M. Moore, Ashwinikumar K Naik, Vaibhav A. Narayan, Beena Neelam, Deborah Nusskern, Douglas B. Rusch, Steven Salzberg, Wei Shao, Bixiong Shue, Jingtao Sun, Zhen Yuan Wang, Aihui Wang, Xin Wang, Jian Wang, Ming-Hui Wei, Ron Wides, Chunlin Xiao, Chunhua Yan, Alison Yao, Jane Ye, Ming Zhan, Weiqing Zhang, Hongyu Zhang, Qi Zhao, Liansheng Zheng, Fei Zhong, Wenyan Zhong, Shiaoping C. Zhu, Shaying Zhao, Dennis Gilbert, Suzanna Baumhueter, Gene Spier, Christine Carter, Anibal Cravchik, Trevor Woodage, Feroze Ali, Huijin An, Aderonke Awe, Danita Baldwin, Holly Baden, Mary Barnstead, Ian Barrow, Karen eeson, Dana Busam, Amy Carver, Angela Center, Ming Lai Cheng, Liz Curry, Steve Danaher, Lionel Davenport, Raymond Desilets, Susanne Dietz, Kristina Dodson, Lisa Doup, Steven Ferriera, Neha Garg, Andres Gluecksmann, Brit Hart, Jason Haynes, Charles Haynes, Cheryl Heiner, Suzanne Hladun, Damon Hostin, Jarrett Houck, Timothy Howland, Chinyere Ibegwam, Jeffery Johnson, Francis Kalush, Lesley Kline, Shashi Koduru, Amy Love, Felecia Mann, David May, Steven Mc. Cawley, Tina Mc. Intosh, Ivy Mc. Mullen, Mee Moy, Linda Moy, Brian Murphy, Keith Nelson, Cynthia Pfannkoch, Eric Pratts, Vinita Puri, Hina Qureshi, Matthew Reardon, Robert Rodriguez, Yu-Hui Rogers, Deanna Romblad, Bob Ruhfel, Richard Scott, Cynthia Sitter, Michelle Smallwood, rin Stewart, Renee Strong, Ellen Suh, Reginald Thomas, Ni Ni Tint, Sukyee Tse, Claire Vech, Gary Wang, Jeremy Wetter, Sherita Williams, Monica Williams, Sandra Windsor, Emily Winn-Deen, Keriellen Wolfe, Jayshree Zaveri, Karena Zaveri, Josep F. Abril, 4 Roderic Guigó, 4 Michael J. Campbell, Kimmen V. Sjolander, Brian Karlak, Anish Kejariwal, Huaiyu Mi, Betty Lazareva, Thomas Hatton, Apurva Narechania, Karen Diemer, Anushya Muruganujan, Nan Guo, Shinji Sato, Vineet Bafna, Sorin Istrail, Ross Lippert, Russell Schwartz, Brian Walenz, Shibu Yooseph, David Allen, Anand Basu, James Baxendale, Louis Blick, Marcelo Caminha, John Carnes-Stine, Parris Caulk, Yen-Hui Chiang, My Coyne, Carl Dahlke, Anne Deslattes Mays, Maria Dombroski, Michael Donnelly, Dale Ely, Shiva Esparham, Carl Fosler, Harold Gire, Stephen Glanowski, Kenneth Glasser, Anna Glodek, Mark Gorokhov, Ken Graham, Barry Gropman, Michael Harris, Jeremy Heil, Scott Henderson, Jeffrey Hoover, Donald Jennings, Catherine Jordan, James Jordan, John Kasha, Leonid Kagan, Cheryl Kraft, Alexander Levitsky, Mark Lewis, Xiangjun Liu, John Lopez, Daniel Ma, William Majoros, Joe Mc. Daniel, Sean Murphy, Matthew Newman, Trung Nguyen, Ngoc Nguyen, Marc Nodell, Sue Pan, Jim Peck, Marshall Peterson, William Rowe, Robert Sanders, John Scott, Michael Simpson, Thomas Smith, Arlan Sprague, Timothy Stockwell, Russell Turner, Eli Venter, Mei Wang, Meiyuan Wen, David Wu, Mitchell Wu, Ashley Xia, Ali Zandieh, Xiaohong Zhu

ID AC SV DT DT DE KW OS OC OC RN RA RT RT RL RN RP RA RT RL RL RL DR DR DR FH FH FT FT FT FT FT SQ // PSPPF 1 standard; RNA; PLN; 1523 BP. Y 12618; Y 12618. 1 30 -JUN-1997 (Rel. 52, Created) 02 -FEB-1999 (Rel. 58, Last updated, Version 4) Pisum sativum m. RNA for PPF-1 protein ppf-1 gene; PPF-1 protein. Pisum sativum (pea) Eukaryota; Viridiplantae; Streptophyta; Embryophyta; Tracheophyta; euphyllophytes; Spermatophyta; Magnoliophyta; eudicotyledons; core eudicots; Rosidae; eurosids I; Fabales; Fabaceae; Papilionoideae; Pisum. [1] Zhu Y. , Zhang Y. , Luo J. , Davies P. J. , Ho D. T. H. ; "PPF-1, a post-floral-specific gene expressed in short-day-grown G 2 pea, may be important for its never-senescing phenotype"; Gene 208: 1 -6(1998). [3] 1 -1523 Zhang Y. ; ; Submitted (02 -FEB-1999) to the EMBL/Gen. Bank/DDBJ databases. Y. Zhang, Peking University, Box 28, College of Life Sciences, Beijing, 100871, PRC Demeter; Y 12618. MENDEL; 14275; Pissa; 2332; 14275. SPTREMBL; O 04699. Key Location/Qualifiers source 1. . 1523 /db_xref="taxon: 3888" /organism="Pisum sativum" /strain="G 2" /dev_stage="pre-floral seedlings" /tissue_type="apical bud" /clone_lib="lambda ZAPII" CDS 48. . 1376 /db_xref="SPTREMBL: O 04699" /gene="ppf-1" /product="PPF-1 protein" /protein_id="CAA 73179. 1" /translation="MAKTLISSPSFLGTPLPSLHRTFSPNRTRLFTKVQFSFHQLPPIQ SVSHSVDLSGIFARAEGLLYTLADATVAADAAASTDVAAQKNGGWFGFISDGMEFVLKV LKDGLSSVHVPYSYGFAIILLTVIVKAATLPLTKQQVESTLAMQNLQPKIKAIQERYAG NQERIQLETSRLYTQAGVNPLAGCLPTLATIPVWIGLYQALSNVANEGLLTEGFLWIPS LGGPTSIAARQSGSGISWLFPFVDGHPLLGWYDTAAYLVLPVLLIVSQYVSMEIMKPPQ TNDPNQKNTLLIFKFLPLMIGYFSLSVPSGLTIYWFTNNVLSTAQQVWLRKLGGAKPAV NENAGGIITAGQAKRSASKPEKGGERFRQLKEEEKKKKLIKALPVEEVQPLASASASND GSDVENNKEQEVTEESNTSKVSQEVQSFSRERRSKRSKRKPVA" Sequence 1523 BP; 421 A; 325 C; 311 G; 466 T; 0 other; ctcaagcctt caagcctgaa gcgtctcgta cacaaacctt ctcatccatg gcgaagacac 60 tgatttcttc tccatcattc ctcggtactc cacttcaccgt actttctccc 120 ctaatcgcac caggcttttc accaaagttc aattcagttt ccaccaactt cctccgattc 180. . . ggaccacata catttg tagtttatag taagttttgt atatgtcaaa cagtttgtat 1440 catttttggg ttgacaattt tattgaacat gttatttaat catgcaaaat atcttttgtt 1500 tcatttaagt tccacatgtt agc 1523
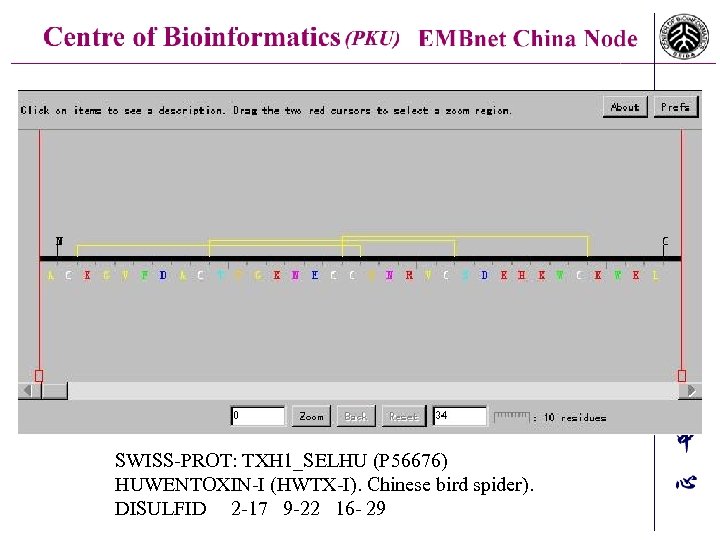
SWISS-PROT: TXH 1_SELHU (P 56676) HUWENTOXIN-I (HWTX-I). Chinese bird spider). DISULFID 2 -17 9 -22 16 - 29
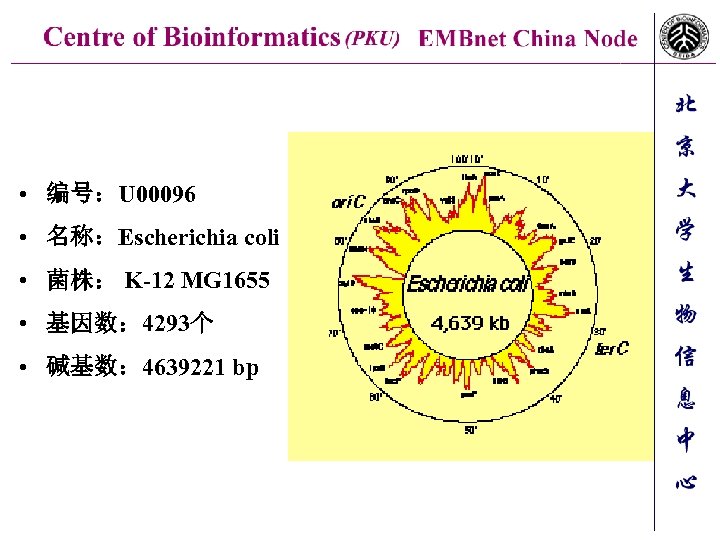
• 编号:U 00096 • 名称:Escherichia coli • 菌株: K-12 MG 1655 • 基因数: 4293个 • 碱基数: 4639221 bp

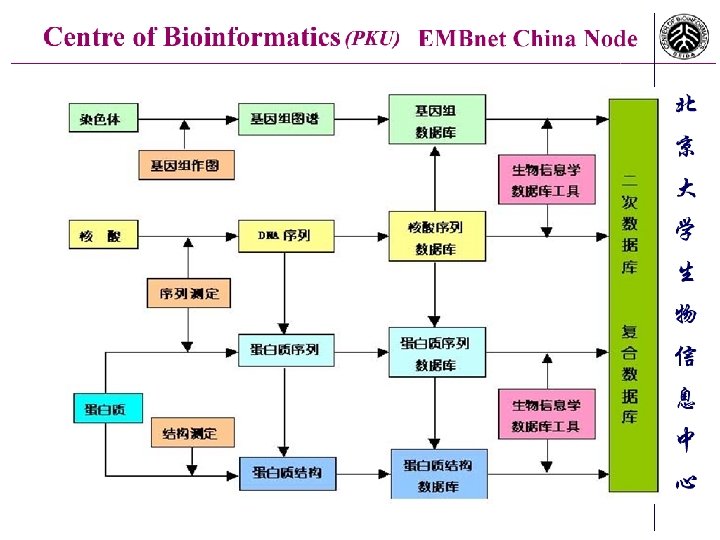
生物信息的开发和应用 • 以核酸蛋白质等生物大分子为主要研究对象 • 以信息、数理、计算机科学为主要研究手段 • 以计算机网络为主要研究环境 • 以计算机软件为主要研究 具 • 对序列数据进行存储、管理、注释、加 • 对各种数据库进行查询、搜索、比较、分析 • 构建各种类型的专用数据库信息系统 • 研究开发面向生物学家的新一代计算机软件

生物信息学研究 • 利用数理统计、模式识别、动态规划、密码解读、语 意解析、信令传递、神经网络、遗传算法以及隐马氏 模型等各种方法 • 对序列、结构数据进行定性和定量分析,从中获取基 因编码、基因调控、序列-结构-功能关系等理性知识 • 阐明细胞、器官和个体的发生、发育、病变、衰亡的 基本规律和时空联系 • 探索生命起源、生物进化、生命本质等重大理论问题, 最终建立“生物学周期表”

生物信息学 – 研究方向 • • • 基因组序列装配 基因识别 基因功能预报 基因多态性分析 基因进化 m. RNA结构预测 基因芯片设计 基因芯片数据分析 疾病相关基因分析 • • • 蛋白质序列分析 蛋白质家族分类 蛋白质结构预测 蛋白质折叠研究 代谢途径分析 转录调控机制 蛋白质芯片设计 蛋白质芯片数据分析 药物设计
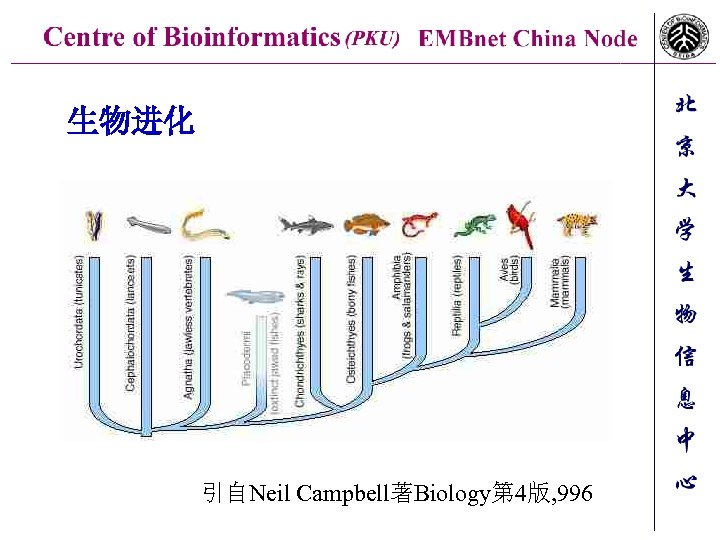
生物进化 引自Neil Campbell著Biology第 4版, 996
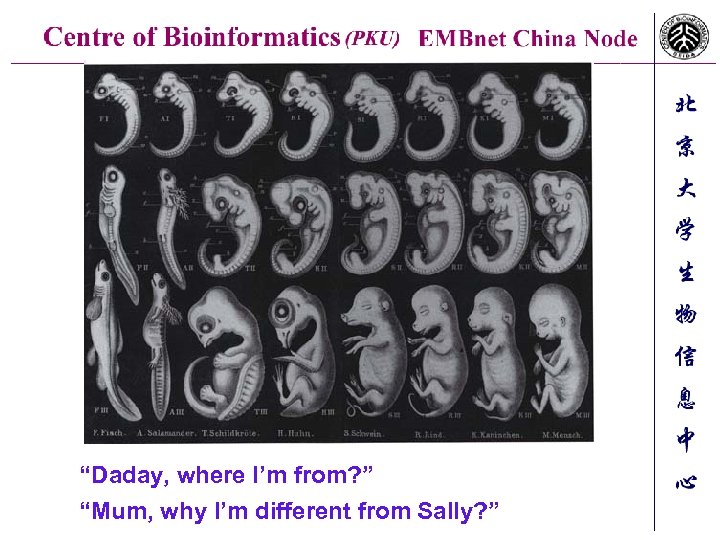
“Daday, where I’m from? ” “Mum, why I’m different from Sally? ”
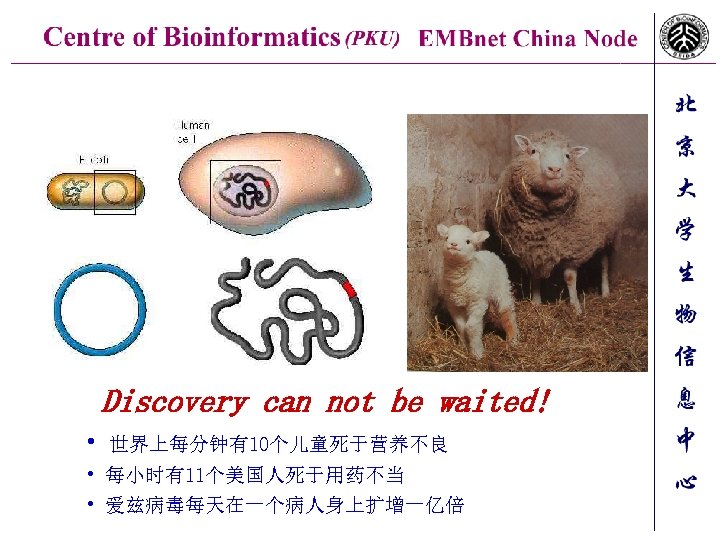
Discovery can not be waited! • 世界上每分钟有10个儿童死于营养不良 • 每小时有11个美国人死于用药不当 • 爱兹病毒每天在一个病人身上扩增一亿倍
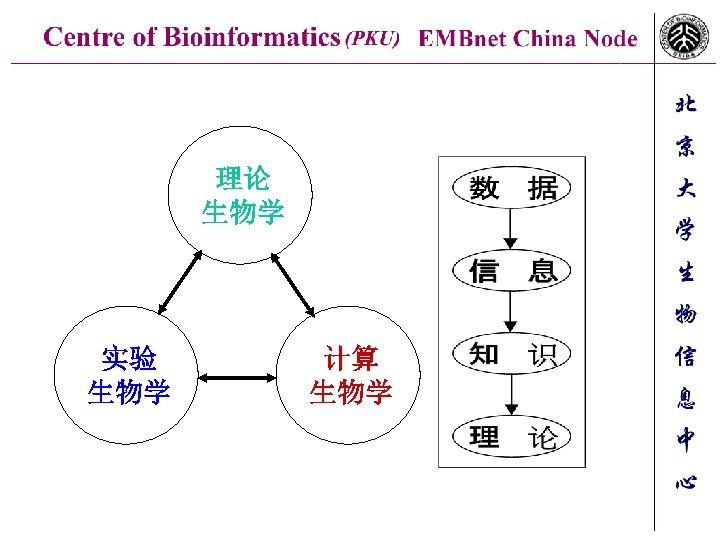
理论 生物学 实验 生物学 计算 生物学

国际著名生物信息中心 Bioinformatics Centres NCBI National Center for Biotechnology Information (US) EBI European Bioinformatics Institute (EU) HGMP Human Genome Mapping Project Resource Centre (UK ) Ex. PASy Expert of Protein Analysis System (Switzerland ) CMBI Centre of Molecular and Biomolecule (The Netherlands) ANGIS National Genome Information Service (Australia) NIG National Institute of Genetics (Japan) BIC National Bioinformatics Centre (Singapore)

欧洲分子生物学网络组织 (EMBnet) European Molecular Biology Network EMBnet为国际著名生物信息学组织,为世界各国提供生物 信息资源,并合作进行生物信息的研究、开发、应用和人 才培训。

EMBnet国家节点 欧洲: 奥地利、比利时、丹麦、法国、芬兰 、德国、希 腊 匈牙利、爱尔兰、以色列、意大利、挪威、 波兰、葡萄牙、斯洛伐克、西班牙、瑞典、瑞士、 荷兰、土耳其、英国 亚洲: 中国、印度 澳洲: 澳大利亚 北美洲: 加拿大 非洲:南非 南美洲: 阿根廷、古巴、智利、墨西哥
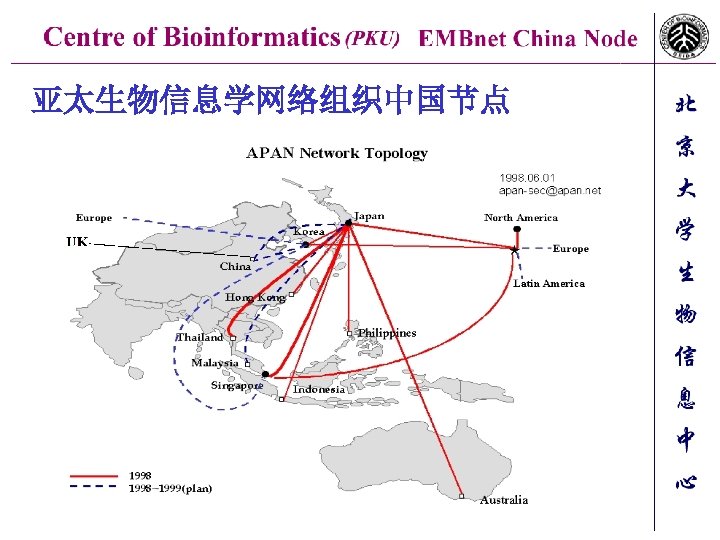
亚太生物信息学网络组织中国节点

欧洲分子生物学网络组织 中国国家节点 National Node European Molecular Biology Network 北京大学生物信息中心 Centre of Bioinformatics Peking University 生物技术和信息技术是 21世 纪的两大经济发展支柱,生 物信息学是生命科学和信息 科学的结合点,是当今自然 科学新的前沿领域。生物信 息资源建设是生物信息研究 开发的基础。 1996年,北京大学加入欧洲分子生物 学网络组织,成为该组织的中国国家 节点,并成立生物信息中心,为生物、 医学、制药、农业、环境等领域的研 究开发提供生物信息资源服务,并开 展二次数据库构建、软件集成、基因 组分析等研究。
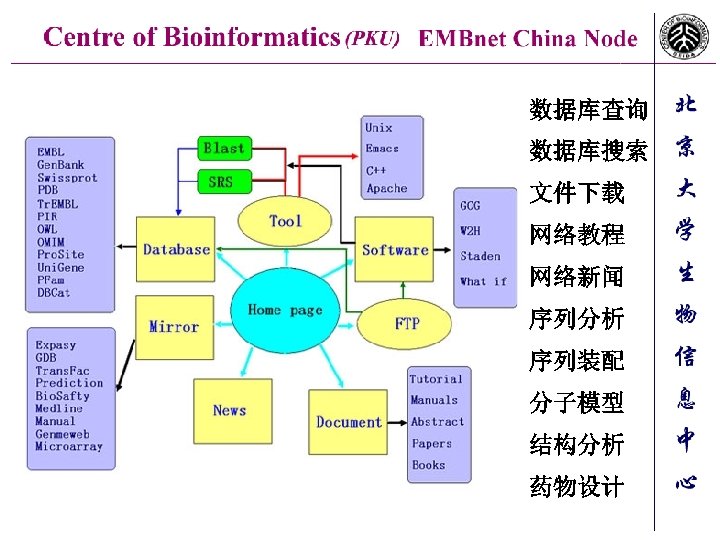
数据库查询 数据库搜索 文件下载 网络教程 网络新闻 序列分析 序列装配 分子模型 结构分析 药物设计
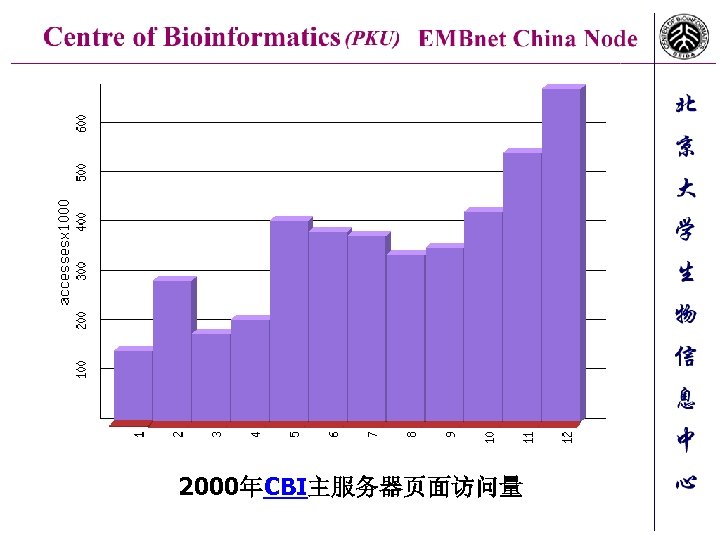
2000年CBI主服务器页面访问量

v 安装了70多个数据库,提供 200多种软件下载 v 建立了14个国外著名生物信息中心镜象 v 提供了数据库和文献查询、搜索 v 构建了中华民族基因多样性等专用数据库 v 集成和开发了基于Web的生物信息软件 具 v 开展了分子模拟、序列分析等应用研究 v 举办了国际国内培训班、讲习班、讨论会 v 开设了生物信息学概论研究生课程

构建二次数据库 中华民族基因多样性数据库 转录因子细胞特异性数据库Cytomer 蛋白质结构域数据库Domain 蛋白质回环数据库Loop 水稻矮缩病毒数据库RDV 二硫键信息数据库Bridge

中华民族基因多态性数据库

水稻矮缩病毒基因组数据库
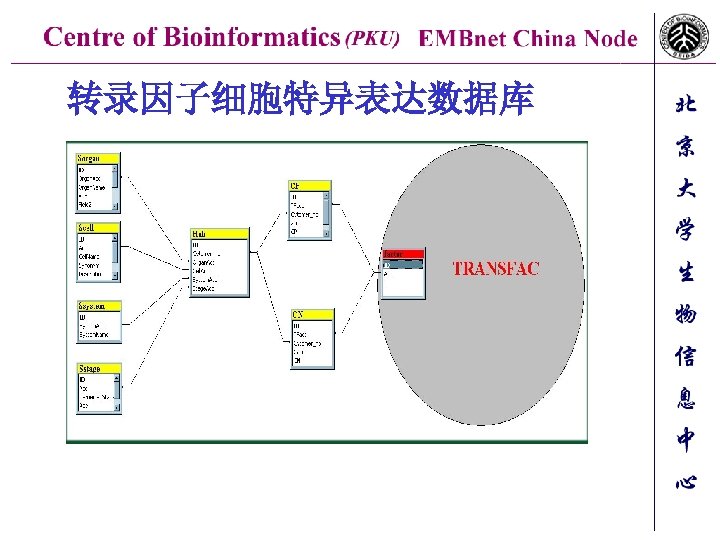
转录因子细胞特异表达数据库

蛋白质回环数据库

蛋白质二硫键数据库 廖黔宁,罗静初,周培爱,顾孝诚,梁宋平,虎纹捕鸟蛛毒素-I突变体的设计、 合成和活性鉴定,中国生物化学和分子生物学学报, 5(5): 756 -761, 1999年。 SY Lu, PC Deng, XC Liu, JC Luo, RS Han, XC Gu,SP Liang, XC Wang, F Li, V Lozanov, A Patthy and S Pongor, Solution structure of the Major a-amylase inhibitor of the crop plant amaranth,J. Biol. Chem. 274 (29): 20473 -20478, 1999.
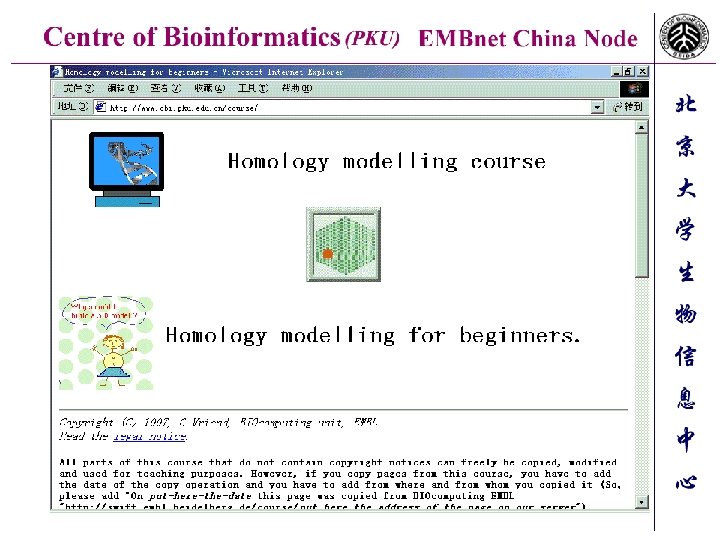
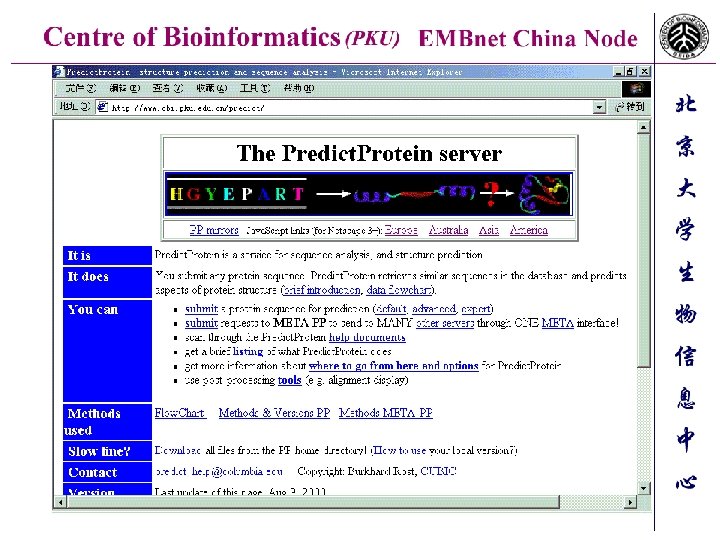
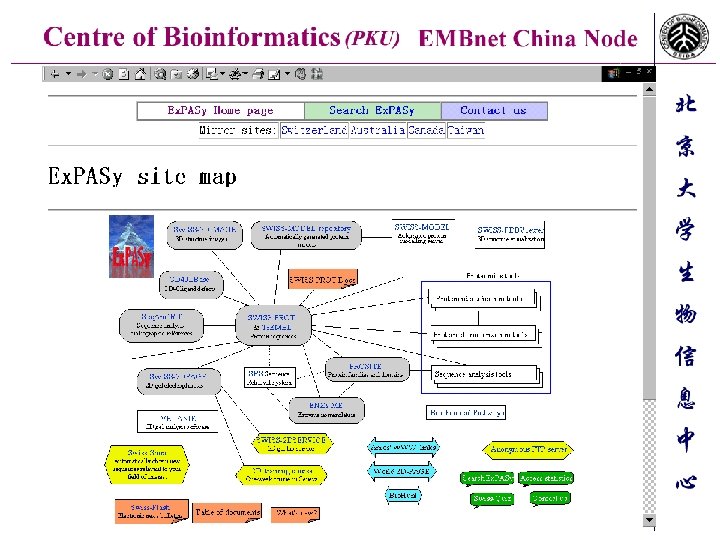

拟南芥突变体库数据库—北大耶鲁合作项目
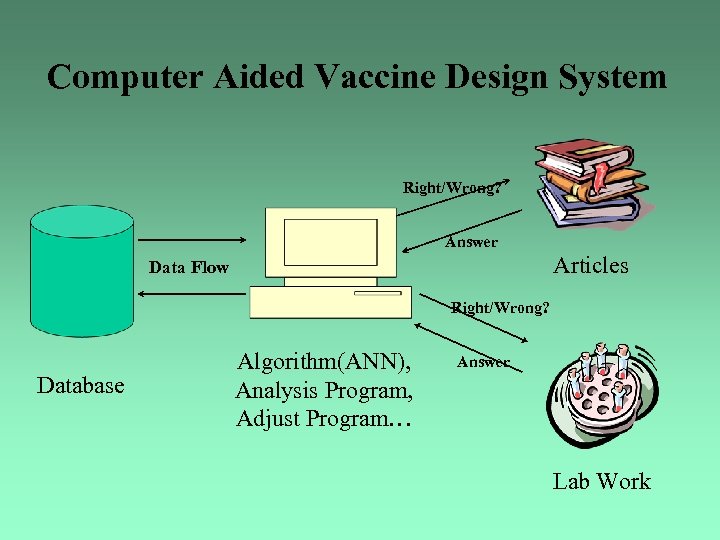
Computer Aided Vaccine Design System Right/Wrong? Answer Articles Data Flow Right/Wrong? Database Algorithm(ANN), Analysis Program, Adjust Program… Answer Lab Work
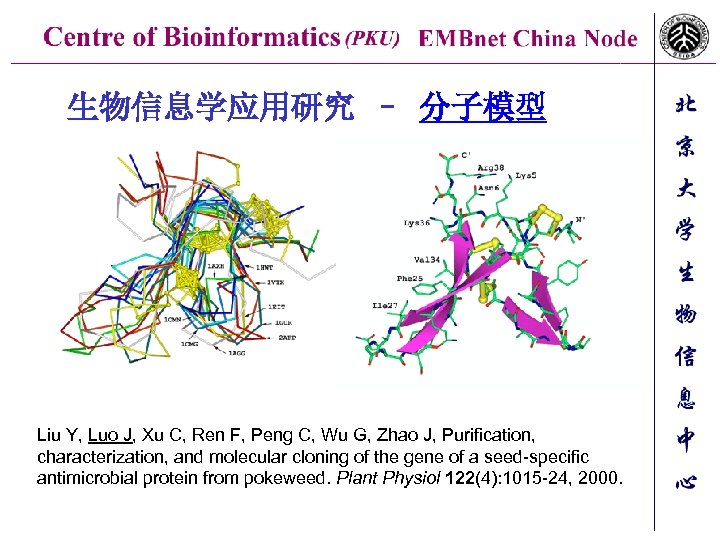
生物信息学应用研究 – 分子模型 Liu Y, Luo J, Xu C, Ren F, Peng C, Wu G, Zhao J, Purification, characterization, and molecular cloning of the gene of a seed-specific antimicrobial protein from pokeweed. Plant Physiol 122(4): 1015 -24, 2000.
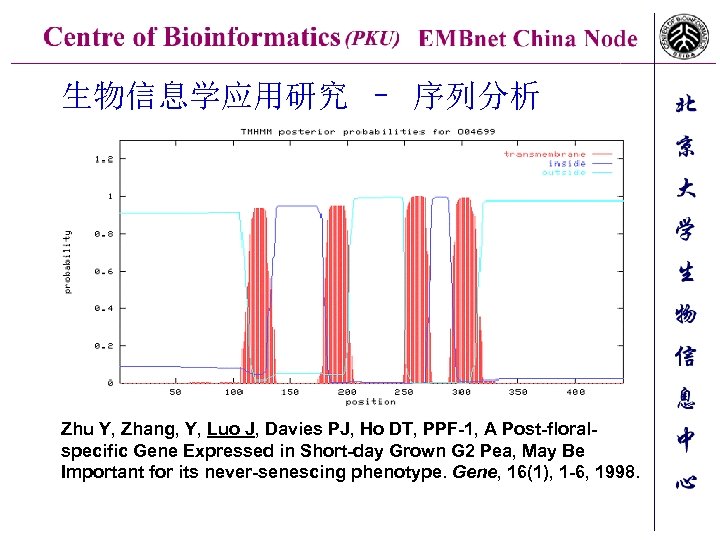
生物信息学应用研究 – 序列分析 Zhu Y, Zhang, Y, Luo J, Davies PJ, Ho DT, PPF-1, A Post-floralspecific Gene Expressed in Short-day Grown G 2 Pea, May Be Important for its never-senescing phenotype. Gene, 16(1), 1 -6, 1998.
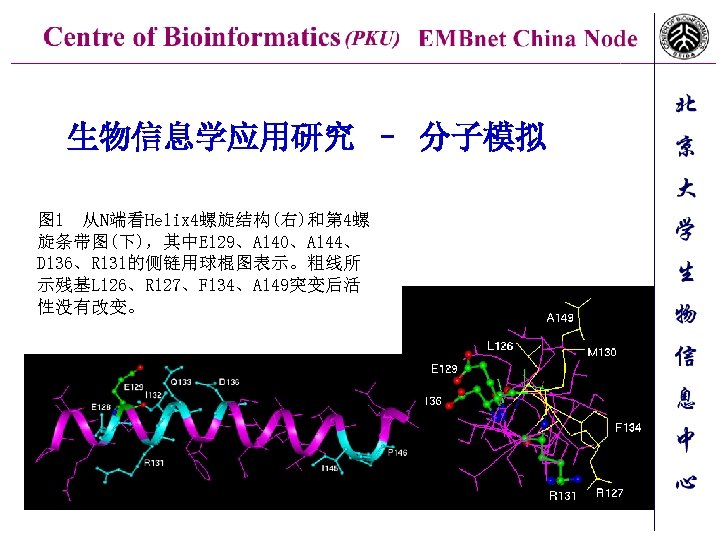
生物信息学应用研究 – 分子模拟 图 1 从N端看Helix 4螺旋结构(右)和第 4螺 旋条带图(下),其中E 129、A 140、A 144、 D 136、R 131的侧链用球棍图表示。粗线所 示残基L 126、R 127、F 134、A 149突变后活 性没有改变。
软件开发和集成

Friends all over the world

• 1998. 4 – EMBnet生物信息 讲习班 • 1998. 6 – EMBL分子模型 培训班 • 1998. 9 – 药物设计培训班 • 1999. 4 – ICGEB国际生物 信息讲习班 • 1999. 11 – 中瑞生物信息 讨论班 • 2000. 9 – 核磁共振培训班 • 2000. 11 – 基因组数据分 析讲习班 • 1999. 9起 理论生物学讨论 班

Introduction to Bioinformatics Graduate Course for 85 students from biology and medicine 3/15/2018

Do your experiment, at least once a year! - Sydney Brenner Discovery can not be planned… - Antonie Danchin

开拓生物技术新的研究领域 - 生物信息数据管理和服务系统 生物信息学是当今自然科学新的前沿领域,是生命科学和信息技术的结合点,是解读 基因组遗传密码的重要 具。“九五”期间, 863生物技术领域努力建设生物数据管 理和服务系统,为我国生物信息学研究以及生物信息资源的应用和开发服务。 北京大学生物信息中心数据资源 上海生命科学院生物信息中心主页 在 863生物技术和信息技术领域支持下, 北京大学生物信息中心在引进国外数据库和 软件 具方面做了开创性 作,已建成国内最大的生物信息资源系统。中科院上海 生命科学院生物信息中心建立了中国核酸蛋白数据库和生物信息网站。 “八六三”生物信息数据管理和服务系 统的建立,为我国生物学、医学、药 物学、农业和环境科学的研究开发提 供信息资源服务,为建立国家生物信 息中心奠定了基础。 北京大学 863生物信息数据库中心 八 六 三 计 划 十 五 周 年 成 就 展 览

Brains Biologists 顾孝诚 罗明 姜颖 顾红雅 曲红 陈新 唐汶 潘卫 方刚 禹胄 陈蕴佳 刘翟 何坤 吴昕 李涛 王键民 张勇 Mathematicians and Physicts 李松岗官山 郝柏林 郑伟谋 纪丰民 Computer Scientists 李笑难 滕小玲 陈国义 李兵 江涛 杜晓锋 李昭 张兴华 戴龙基 肖珑 陈凌 聂华

Last, but not least … I think we can not get a Nobel prize by what we are doing, but the Nobel prize winners know what we are doing for. So, I will go to my death with smile. - Alan Bleasby Alan walking around the Genome Campus. Cambridge, 5 Oct 2000

Thank you for your patience!
acd99628e07c9499f949c1d4ad6e5494.ppt